| ソフトウェア | | 名称 | バージョン | 分類 |
|---|
| PHENIX | 1.18_3855| 精密化 | | XDS | | データ削減 | | XDS | | データスケーリング | | MOLREP | | 位相決定 | |
|
|---|
| 精密化 | 構造決定の手法:  分子置換 分子置換
開始モデル: 2V05
解像度: 2.65→47.53 Å / SU ML: 0.3217 / 交差検証法: FREE R-VALUE / σ(F): 1.34 / 位相誤差: 23.1208
立体化学のターゲット値: GeoStd + Monomer Library + CDL v1.2
| Rfactor | 反射数 | %反射 |
|---|
| Rfree | 0.2419 | 613 | 4.56 % |
|---|
| Rwork | 0.2008 | 12841 | - |
|---|
| obs | 0.2028 | 13454 | 99.63 % |
|---|
|
|---|
| 溶媒の処理 | 減衰半径: 0.9 Å / VDWプローブ半径: 1.11 Å / 溶媒モデル: FLAT BULK SOLVENT MODEL |
|---|
| 原子変位パラメータ | Biso mean: 58.12 Å2 |
|---|
| 精密化ステップ | サイクル: LAST / 解像度: 2.65→47.53 Å
| タンパク質 | 核酸 | リガンド | 溶媒 | 全体 |
|---|
| 原子数 | 2580 | 0 | 103 | 44 | 2727 |
|---|
|
|---|
| 拘束条件 | | Refine-ID | タイプ | Dev ideal | 数 |
|---|
| X-RAY DIFFRACTION | f_bond_d| 0.0018 | 2763 | | X-RAY DIFFRACTION | f_angle_d| 0.3958 | 3744 | | X-RAY DIFFRACTION | f_chiral_restr| 0.0375 | 337 | | X-RAY DIFFRACTION | f_plane_restr| 0.0016 | 465 | | X-RAY DIFFRACTION | f_dihedral_angle_d| 11.4762 | 396 | | | | | |
|
|---|
| LS精密化 シェル | | 解像度 (Å) | Rfactor Rfree | Num. reflection Rfree | Rfactor Rwork | Num. reflection Rwork | Refine-ID | % reflection obs (%) |
|---|
| 2.65-2.92 | 0.334 | 156 | 0.2941 | 3151 | X-RAY DIFFRACTION | 99.82 | | 2.92-3.34 | 0.2585 | 137 | 0.2483 | 3164 | X-RAY DIFFRACTION | 99.79 | | 3.34-4.21 | 0.236 | 154 | 0.1917 | 3186 | X-RAY DIFFRACTION | 99.61 | | 4.21-47.53 | 0.2204 | 166 | 0.1703 | 3340 | X-RAY DIFFRACTION | 99.32 |
|
|---|
| 精密化 TLS | 手法: refined / Refine-ID: X-RAY DIFFRACTION | ID | L11 (°2) | L12 (°2) | L13 (°2) | L22 (°2) | L23 (°2) | L33 (°2) | S11 (Å °) | S12 (Å °) | S13 (Å °) | S21 (Å °) | S22 (Å °) | S23 (Å °) | S31 (Å °) | S32 (Å °) | S33 (Å °) | T11 (Å2) | T12 (Å2) | T13 (Å2) | T22 (Å2) | T23 (Å2) | T33 (Å2) | Origin x (Å) | Origin y (Å) | Origin z (Å) |
|---|
| 1 | 2.23785835409 | -1.34993945386 | -1.3769736859 | 4.26901667494 | -1.18243939007 | 3.80887946762 | 0.358655470445 | 0.52547782716 | 1.15709600483 | -0.517878826064 | -0.0190645123846 | 0.111340292414 | -0.447102356377 | 0.0332372134873 | -0.339167656987 | 0.571553748236 | 0.0590245887742 | 0.141523796599 | 0.466418267926 | 0.153185333372 | 0.730317111658 | 9.49403721706 | 45.2113281422 | -5.92439369001 | | 2 | 4.02295527228 | -1.3224351578 | -0.45115256101 | 2.21324818707 | -0.692425294782 | 3.15771147023 | 0.368197124406 | -0.000721292207504 | 0.568920485155 | -0.113818726631 | 0.00433904696435 | 0.230191279096 | -0.115601070272 | -0.0599191991079 | -0.329273177817 | 0.315933835301 | -0.0170256372241 | 0.0227663234068 | 0.313621078097 | 0.0189096126446 | 0.498628929504 | 11.4237077071 | 35.4319400377 | -0.286646393142 | | 3 | 2.12131341472 | 0.616832675664 | -0.350773582648 | 0.548386749742 | -0.100763754665 | 0.960828040351 | 0.255312362398 | 0.0830336495682 | 0.552925361511 | 0.320439465128 | -0.127754619014 | 0.00677753897027 | -0.186942114515 | -0.111677860898 | -0.0207944599465 | 0.450206907336 | 0.0493203359302 | 0.135835380883 | 0.518095150408 | 0.02172993991 | 0.465581148222 | -0.364036399205 | 35.7732442231 | 3.1089504024 | | 4 | 3.10120015965 | -0.614476805285 | -1.08345703382 | 2.46798883593 | -2.13648788111 | 4.08932002074 | 0.0266901222559 | 0.369466634628 | 0.600675669306 | 0.062241012648 | -0.0723302566921 | -0.384502832081 | -0.066747415241 | 0.368410386745 | 0.102695160298 | 0.324813550263 | 0.0283799035433 | 0.0628164828318 | 0.410102082639 | 0.0739832280338 | 0.438432064687 | 19.8913105849 | 30.1849008825 | 2.68525366625 | | 5 | 1.36614251989 | -0.757094992477 | 0.699010202478 | 2.96796219368 | -1.65463364128 | 4.10513796431 | 0.372680177082 | -0.0202305988011 | 0.00964244115886 | -0.129666311162 | -0.275499480604 | -0.430749390441 | -0.028431421941 | 0.00520692301552 | -0.0686904239373 | 0.275644351253 | 0.0391723955848 | 0.00538353698133 | 0.354497517312 | 0.0537583996008 | 0.316473249768 | 19.1587599357 | 16.4565326268 | 6.95018713602 | | 6 | 1.3957551666 | 0.433659900805 | 0.314373014835 | 1.34538490602 | -0.631451076265 | 0.492828280904 | -0.268576546094 | -0.233426668519 | 0.424221087821 | 0.561740772884 | 0.495858438039 | 0.0265985634456 | -0.57100870538 | 0.0874824605725 | -0.217821060412 | 0.510946617701 | 0.0375969621931 | -0.0518573623997 | 0.570259739143 | 0.0327823361728 | 0.437976308974 | 17.3605030646 | 21.5629339017 | 19.9587543899 | | 7 | 1.17619660597 | 1.00850666472 | 1.0101437484 | 3.07295723897 | 0.202424569916 | 3.11913401532 | 0.142646355005 | -0.296864018168 | -0.27858777456 | 0.0664511703748 | -0.057578482011 | 0.640734691169 | -0.376125720205 | -0.267610621457 | -0.153085485269 | 0.430117715761 | 0.0231241028221 | 0.0594910127648 | 0.50654385513 | 0.0643014136581 | 0.332497284602 | 13.3664606797 | 10.599845808 | 19.1779967436 | | 8 | 0.348543269688 | -0.00520677145615 | -0.13789627707 | 3.08442519611 | -2.34025704173 | 2.38903507786 | 0.057957496492 | 0.0755493685194 | 0.0797558619467 | -0.094564206492 | 0.157985175194 | 0.0900160873181 | 0.0601245908509 | -0.0715613598353 | -0.204597451374 | 0.331886571218 | -0.0237179987759 | -0.0180601089128 | 0.455763032878 | 0.0484424277609 | 0.354033205236 | 18.1255500118 | -8.59189143226 | 34.4104698189 | | 9 | 1.67892771456 | -0.990836455675 | 1.7530435549 | 1.44552669332 | -2.48509069674 | 4.49278134104 | -0.24378054236 | 0.338138777046 | -0.145925769762 | -0.459459242928 | 0.510921651179 | 0.537030588521 | 0.863228899569 | -0.938387765465 | -0.0889408476992 | 0.470815619214 | -0.0524501956151 | 0.00551576010105 | 0.588739922383 | 0.151830834417 | 0.571223220364 | 9.93030581428 | -24.4808441748 | 46.0934650454 | | 10 | 3.28763901506 | -1.29623665051 | 2.79617061837 | 4.48762616208 | 0.208509127297 | 5.47430286242 | -0.142245868673 | -0.53912204914 | -0.763108641414 | 0.774784834309 | -0.00366037496888 | -0.192932025237 | 1.01956337848 | 0.118422188822 | 0.000368614152686 | 0.581795909609 | 0.102426096788 | 0.155410472975 | 0.650178601323 | 0.115008366615 | 0.532713336868 | 14.9205281874 | -28.493379129 | 55.9332980661 |
|
|---|
| 精密化 TLSグループ | Refine-ID: X-RAY DIFFRACTION / Auth asym-ID: AA / Label asym-ID: A | ID | Refine TLS-ID | Selection details | Auth seq-ID | Label seq-ID |
|---|
| 1 | 1 | chain 'AA' and (resid 1 through 25 )| 1 - 25 | 1 - 25 | | 2 | 2 | chain 'AA' and (resid 26 through 50 )| 26 - 50 | 26 - 50 | | 3 | 3 | chain 'AA' and (resid 51 through 72 )| 51 - 72 | 51 - 72 | | 4 | 4 | chain 'AA' and (resid 73 through 109 )| 73 - 109 | 73 - 109 | | 5 | 5 | chain 'AA' and (resid 110 through 144 )| 110 - 144 | 110 - 144 | | 6 | 6 | chain 'AA' and (resid 145 through 165 )| 145 - 165 | 145 - 165 | | 7 | 7 | chain 'AA' and (resid 166 through 193 )| 166 - 193 | 166 - 193 | | 8 | 8 | chain 'AA' and (resid 194 through 265 )| 194 - 265 | 194 - 265 | | 9 | 9 | chain 'AA' and (resid 266 through 286 )| 266 - 286 | 266 - 286 | | 10 | 10 | chain 'AA' and (resid 287 through 311 )| 287 - 311 | 287 - 311 | | | | | | | | | | |
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 2.65 Å
分子置換 / 解像度: 2.65 Å  データ登録者
データ登録者 引用
引用 ジャーナル: Acs Appl Bio Mater / 年: 2021
ジャーナル: Acs Appl Bio Mater / 年: 2021 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 7bay.cif.gz
7bay.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb7bay.ent.gz
pdb7bay.ent.gz PDB形式
PDB形式 7bay.json.gz
7bay.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/ba/7bay
https://data.pdbj.org/pub/pdb/validation_reports/ba/7bay ftp://data.pdbj.org/pub/pdb/validation_reports/ba/7bay
ftp://data.pdbj.org/pub/pdb/validation_reports/ba/7bay
 リンク
リンク 集合体
集合体
 要素
要素 Streptococcus pneumoniae (strain ATCC BAA-255 / R6) (肺炎レンサ球菌)
Streptococcus pneumoniae (strain ATCC BAA-255 / R6) (肺炎レンサ球菌)


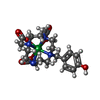





 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  ALBA
ALBA  / ビームライン: XALOC / 波長: 0.97934 Å
/ ビームライン: XALOC / 波長: 0.97934 Å 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj




