+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-6105 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM Structure of the 80S-RAC complex from yeast | |||||||||
 マップデータ マップデータ | Reconstruction of yeast 80S-RAC complex (Non-rotated state with higher RAC occupancy from Dataset RAC5, RAC9, RAC10) | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | ribosome-associated complex / co-translational chaperone / cryo-em / translation regulation / Zuotin / SSZ | |||||||||
| 生物種 |  | |||||||||
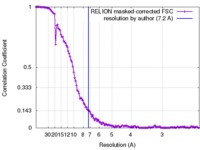
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 7.2 Å | |||||||||
 データ登録者 データ登録者 | Zhang YX / Ma CY / Yuan Y / Zhu J / Li NN / Chen C / Wu S / Yu L / Lei JL / Gao N | |||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2014 ジャーナル: Nat Struct Mol Biol / 年: 2014タイトル: Structural basis for interaction of a cotranslational chaperone with the eukaryotic ribosome. 著者: Yixiao Zhang / Chengying Ma / Yi Yuan / Jing Zhu / Ningning Li / Chu Chen / Shan Wu / Li Yu / Jianlin Lei / Ning Gao /  要旨: Cotranslational chaperones, ubiquitous in all living organisms, protect nascent polypeptides from aggregation and facilitate their de novo folding. Importantly, emerging data have also suggested that ...Cotranslational chaperones, ubiquitous in all living organisms, protect nascent polypeptides from aggregation and facilitate their de novo folding. Importantly, emerging data have also suggested that ribosome-associated cotranslational chaperones have active regulatory roles in modulating protein translation. By characterizing the structure of a type of eukaryotic cotranslational chaperone, the ribosome-associated complex (RAC) from Saccharomyces cerevisiae, we show that RAC cross-links two ribosomal subunits, through a single long α-helix, to limit the predominant intersubunit rotation required for peptide elongation. We further demonstrate that any changes in the continuity, length or rigidity of this middle α-helix impair RAC function in vivo. Our results suggest a new mechanism in which RAC directly regulates protein translation by mechanically coupling cotranslational folding with the peptide-elongation cycle, and they lay the foundation for further exploration of regulatory roles of RAC in translation control. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_6105.map.gz emd_6105.map.gz | 157.1 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-6105-v30.xml emd-6105-v30.xml emd-6105.xml emd-6105.xml | 9.6 KB 9.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_6105_fsc.xml emd_6105_fsc.xml | 12.6 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_6105.tif emd_6105.tif | 1.6 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-6105 http://ftp.pdbj.org/pub/emdb/structures/EMD-6105 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-6105 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-6105 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_6105_validation.pdf.gz emd_6105_validation.pdf.gz | 79.1 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_6105_full_validation.pdf.gz emd_6105_full_validation.pdf.gz | 78.2 KB | 表示 | |
| XML形式データ |  emd_6105_validation.xml.gz emd_6105_validation.xml.gz | 494 B | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-6105 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-6105 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-6105 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-6105 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_6105.map.gz / 形式: CCP4 / 大きさ: 173.8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_6105.map.gz / 形式: CCP4 / 大きさ: 173.8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Reconstruction of yeast 80S-RAC complex (Non-rotated state with higher RAC occupancy from Dataset RAC5, RAC9, RAC10) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.16 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
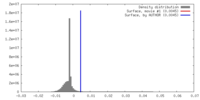
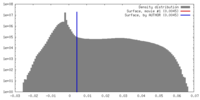
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Ribosome-associated complex (RAC) interacting with Saccharomyces ...
| 全体 | 名称: Ribosome-associated complex (RAC) interacting with Saccharomyces cerevisiae 80S ribosome |
|---|---|
| 要素 |
|
-超分子 #1000: Ribosome-associated complex (RAC) interacting with Saccharomyces ...
| 超分子 | 名称: Ribosome-associated complex (RAC) interacting with Saccharomyces cerevisiae 80S ribosome タイプ: sample / ID: 1000 / Number unique components: 2 |
|---|
-超分子 #1: Saccharomyces cerevisiae 80S ribosome
| 超分子 | 名称: Saccharomyces cerevisiae 80S ribosome / タイプ: complex / ID: 1 / 組換発現: Yes / Ribosome-details: ribosome-eukaryote: ALL |
|---|---|
| 由来(天然) | 生物種:  |
| 組換発現 | 生物種:  |
-分子 #1: Ribosome-associated complex
| 分子 | 名称: Ribosome-associated complex / タイプ: protein_or_peptide / ID: 1 / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:  |
| 組換発現 | 生物種:  |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 / 詳細: 20mM Hepes-KOH, 120mM KOAc, 10mM Mg(OAc)2 |
|---|---|
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 90 % / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 日付 | 2013年1月9日 |
| 撮影 | カテゴリ: CCD / フィルム・検出器のモデル: FEI EAGLE (4k x 4k) / 実像数: 8501 / 平均電子線量: 20 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)