| 登録情報 | データベース: PDB / ID: 4xct
|
|---|
| タイトル | Crystal structure of a hydroxamate based inhibitor ARP101 (EN73) in complex with the MMP-9 catalytic domain. |
|---|
 要素 要素 | Matrix metalloproteinase-9,Matrix metalloproteinase-9 |
|---|
 キーワード キーワード | HYDROLASE / Inhibitor-complex / metalloprotease |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
gelatinase B / negative regulation of epithelial cell differentiation involved in kidney development / : / : / cellular response to UV-A / regulation of neuroinflammatory response / positive regulation of keratinocyte migration / positive regulation of epidermal growth factor receptor signaling pathway / Assembly of collagen fibrils and other multimeric structures / positive regulation of DNA binding ...gelatinase B / negative regulation of epithelial cell differentiation involved in kidney development / : / : / cellular response to UV-A / regulation of neuroinflammatory response / positive regulation of keratinocyte migration / positive regulation of epidermal growth factor receptor signaling pathway / Assembly of collagen fibrils and other multimeric structures / positive regulation of DNA binding / Activation of Matrix Metalloproteinases / negative regulation of intrinsic apoptotic signaling pathway / endodermal cell differentiation / positive regulation of release of cytochrome c from mitochondria / Collagen degradation / response to amyloid-beta / collagen catabolic process / macrophage differentiation / extracellular matrix disassembly / EPH-ephrin mediated repulsion of cells / ephrin receptor signaling pathway / collagen binding / positive regulation of vascular associated smooth muscle cell proliferation / Degradation of the extracellular matrix / extracellular matrix organization / embryo implantation / skeletal system development / Signaling by SCF-KIT / metalloendopeptidase activity / metallopeptidase activity / positive regulation of protein phosphorylation / tertiary granule lumen / cell migration / peptidase activity / : / cellular response to lipopolysaccharide / Interleukin-4 and Interleukin-13 signaling / endopeptidase activity / ficolin-1-rich granule lumen / Extra-nuclear estrogen signaling / positive regulation of apoptotic process / serine-type endopeptidase activity / apoptotic process / Neutrophil degranulation / negative regulation of apoptotic process / proteolysis / extracellular space / extracellular exosome / extracellular region / zinc ion binding / identical protein binding類似検索 - 分子機能 Fibronectin type II domain / Fibronectin type II domain superfamily / Fibronectin type II domain / Fibronectin type-II collagen-binding domain signature. / Fibronectin type-II collagen-binding domain profile. / Fibronectin type 2 domain / Hemopexin, conserved site / Hemopexin domain signature. / Hemopexin-like domain / Peptidase M10A, cysteine switch, zinc binding site ...Fibronectin type II domain / Fibronectin type II domain superfamily / Fibronectin type II domain / Fibronectin type-II collagen-binding domain signature. / Fibronectin type-II collagen-binding domain profile. / Fibronectin type 2 domain / Hemopexin, conserved site / Hemopexin domain signature. / Hemopexin-like domain / Peptidase M10A, cysteine switch, zinc binding site / Matrixins cysteine switch. / Hemopexin-like repeats / Hemopexin-like domain superfamily / Hemopexin / Hemopexin repeat profile. / Hemopexin-like repeats. / Peptidase M10A / Peptidase M10A, catalytic domain / Peptidase M10, metallopeptidase / Matrixin / PGBD-like superfamily / Peptidase, metallopeptidase / Zinc-dependent metalloprotease / Collagenase (Catalytic Domain) / Collagenase (Catalytic Domain) / Metallopeptidase, catalytic domain superfamily / Kringle-like fold / Neutral zinc metallopeptidases, zinc-binding region signature. / 3-Layer(aba) Sandwich / Alpha Beta類似検索 - ドメイン・相同性 (2S,3S)-butane-2,3-diol / Chem-N73 / S-1,2-PROPANEDIOL / Matrix metalloproteinase-9類似検索 - 構成要素 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.3 Å 分子置換 / 解像度: 1.3 Å |
|---|
 データ登録者 データ登録者 | Stura, E.A. / Tepshi, L. / Nuti, E. / Dive, V. / Cassar-Lajeunesse, E. / Vera, L. / Rossello, A. |
|---|
 引用 引用 |  ジャーナル: J.Med.Chem. / 年: 2015 ジャーナル: J.Med.Chem. / 年: 2015
タイトル: N-O-Isopropyl Sulfonamido-Based Hydroxamates as Matrix Metalloproteinase Inhibitors: Hit Selection and in Vivo Antiangiogenic Activity.
著者: Nuti, E. / Cantelmo, A.R. / Gallo, C. / Bruno, A. / Bassani, B. / Camodeca, C. / Tuccinardi, T. / Vera, L. / Orlandini, E. / Nencetti, S. / Stura, E.A. / Martinelli, A. / Dive, V. / Albini, A. / Rossello, A. |
|---|
| 履歴 | | 登録 | 2014年12月18日 | 登録サイト: RCSB / 処理サイト: PDBE |
|---|
| 改定 1.0 | 2015年4月22日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2015年8月26日 | Group: Database references |
|---|
| 改定 1.2 | 2015年10月7日 | Group: Database references |
|---|
| 改定 2.0 | 2019年5月29日 | Group: Advisory / Atomic model ...Advisory / Atomic model / Data collection / Derived calculations / Non-polymer description / Structure summary
カテゴリ: atom_site / atom_site_anisotrop ...atom_site / atom_site_anisotrop / chem_comp / entity / pdbx_distant_solvent_atoms / pdbx_entity_nonpoly / pdbx_nonpoly_scheme / pdbx_solvent_atom_site_mapping / pdbx_struct_conn_angle / pdbx_struct_special_symmetry / struct_conn / struct_site_gen
Item: _atom_site.B_iso_or_equiv / _atom_site.Cartn_x ..._atom_site.B_iso_or_equiv / _atom_site.Cartn_x / _atom_site.Cartn_y / _atom_site.Cartn_z / _atom_site.auth_seq_id / _atom_site.label_alt_id / _atom_site.occupancy / _atom_site.pdbx_auth_seq_id / _atom_site_anisotrop.U[1][1] / _atom_site_anisotrop.U[1][2] / _atom_site_anisotrop.U[1][3] / _atom_site_anisotrop.U[2][2] / _atom_site_anisotrop.U[2][3] / _atom_site_anisotrop.U[3][3] / _atom_site_anisotrop.id / _atom_site_anisotrop.pdbx_PDB_residue_no / _atom_site_anisotrop.pdbx_auth_seq_id / _atom_site_anisotrop.pdbx_label_alt_id / _chem_comp.formula / _chem_comp.formula_weight / _chem_comp.name / _entity.formula_weight / _entity.pdbx_description / _pdbx_distant_solvent_atoms.auth_seq_id / _pdbx_entity_nonpoly.name / _pdbx_nonpoly_scheme.auth_seq_num / _pdbx_solvent_atom_site_mapping.auth_seq_id / _pdbx_struct_conn_angle.ptnr1_auth_seq_id / _pdbx_struct_conn_angle.ptnr3_auth_seq_id / _pdbx_struct_special_symmetry.auth_seq_id / _struct_conn.ptnr2_auth_seq_id / _struct_site_gen.auth_seq_id |
|---|
| 改定 2.1 | 2024年1月10日 | Group: Data collection / Database references ...Data collection / Database references / Derived calculations / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model / struct_conn
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _struct_conn.pdbx_dist_value / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 1.3 Å
分子置換 / 解像度: 1.3 Å  データ登録者
データ登録者 引用
引用 ジャーナル: J.Med.Chem. / 年: 2015
ジャーナル: J.Med.Chem. / 年: 2015 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 4xct.cif.gz
4xct.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb4xct.ent.gz
pdb4xct.ent.gz PDB形式
PDB形式 4xct.json.gz
4xct.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/xc/4xct
https://data.pdbj.org/pub/pdb/validation_reports/xc/4xct ftp://data.pdbj.org/pub/pdb/validation_reports/xc/4xct
ftp://data.pdbj.org/pub/pdb/validation_reports/xc/4xct リンク
リンク 集合体
集合体
 要素
要素 Homo sapiens (ヒト) / 遺伝子: MMP9, CLG4B / プラスミド: pET-14b / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: MMP9, CLG4B / プラスミド: pET-14b / 発現宿主: 
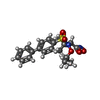





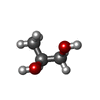
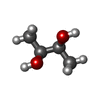









 X線回折
X線回折 試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  SOLEIL
SOLEIL  / ビームライン: PROXIMA 1 / 波長: 0.97857 Å
/ ビームライン: PROXIMA 1 / 波長: 0.97857 Å 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj


















