+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-4610 | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | CryoEM reconstructuion of Cowpea Mosaic Virus (CPMV) bound to an Affimer reagent | ||||||||||||
 マップデータ マップデータ | postprocessed map of cryoEM map of Cowpea Mosaic virus bound to an Affimer protein | ||||||||||||
 試料 試料 |
| ||||||||||||
 キーワード キーワード | VIRUS / CPMV / COMOVIRIDAE / PICORNAVIRALES / AFFIMEr REAGENT / antibody-like | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報transport of virus in host, cell to cell / host cell plasmodesma / T=3 icosahedral viral capsid / symbiont-mediated suppression of host innate immune response / virus-mediated perturbation of host defense response / host cell nucleus / GTP binding / structural molecule activity / DNA binding / RNA binding 類似検索 - 分子機能 | ||||||||||||
| 生物種 | synthetic construct (人工物) /   Cowpea mosaic virus (ササゲモザイクウイルス) Cowpea mosaic virus (ササゲモザイクウイルス) | ||||||||||||
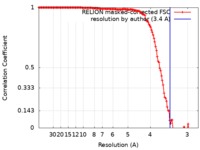
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.4 Å | ||||||||||||
 データ登録者 データ登録者 | Hesketh EL / Tiede C | ||||||||||||
| 資金援助 |  英国, 3件 英国, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2015 ジャーナル: Nat Commun / 年: 2015タイトル: Mechanisms of assembly and genome packaging in an RNA virus revealed by high-resolution cryo-EM. 著者: Emma L Hesketh / Yulia Meshcheriakova / Kyle C Dent / Pooja Saxena / Rebecca F Thompson / Joseph J Cockburn / George P Lomonossoff / Neil A Ranson /  要旨: Cowpea mosaic virus is a plant-infecting member of the Picornavirales and is of major interest in the development of biotechnology applications. Despite the availability of >100 crystal structures of ...Cowpea mosaic virus is a plant-infecting member of the Picornavirales and is of major interest in the development of biotechnology applications. Despite the availability of >100 crystal structures of Picornavirales capsids, relatively little is known about the mechanisms of capsid assembly and genome encapsidation. Here we have determined cryo-electron microscopy reconstructions for the wild-type virus and an empty virus-like particle, to 3.4 Å and 3.0 Å resolution, respectively, and built de novo atomic models of their capsids. These new structures reveal the C-terminal region of the small coat protein subunit, which is essential for virus assembly and which was missing from previously determined crystal structures, as well as residues that bind to the viral genome. These observations allow us to develop a new model for genome encapsidation and capsid assembly. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_4610.map.gz emd_4610.map.gz | 30.1 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-4610-v30.xml emd-4610-v30.xml emd-4610.xml emd-4610.xml | 22.7 KB 22.7 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_4610_fsc.xml emd_4610_fsc.xml | 13.6 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_4610.png emd_4610.png | 315 KB | ||
| Filedesc metadata |  emd-4610.cif.gz emd-4610.cif.gz | 6.7 KB | ||
| その他 |  emd_4610_half_map_1.map.gz emd_4610_half_map_1.map.gz emd_4610_half_map_2.map.gz emd_4610_half_map_2.map.gz | 166.3 MB 166.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-4610 http://ftp.pdbj.org/pub/emdb/structures/EMD-4610 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-4610 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-4610 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_4610.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_4610.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | postprocessed map of cryoEM map of Cowpea Mosaic virus bound to an Affimer protein | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.4 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-ハーフマップ: Unfiltered half map of cryoEM map of Cowpea...
| ファイル | emd_4610_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Unfiltered half map of cryoEM map of Cowpea Mosaic virus bound to an Affimer protein | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Unfiltered half map of cryoEM map of Cowpea...
| ファイル | emd_4610_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Unfiltered half map of cryoEM map of Cowpea Mosaic virus bound to an Affimer protein | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Cowpea mosaic virus
| 全体 | 名称:   Cowpea mosaic virus (ササゲモザイクウイルス) Cowpea mosaic virus (ササゲモザイクウイルス) |
|---|---|
| 要素 |
|
-超分子 #1: Cowpea mosaic virus
| 超分子 | 名称: Cowpea mosaic virus / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|
-超分子 #3: Affimer
| 超分子 | 名称: Affimer / タイプ: complex / ID: 3 / 親要素: 1 / 含まれる分子: #3 |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
-超分子 #2: Cowpea mosaic virus
| 超分子 | 名称: Cowpea mosaic virus / タイプ: virus / ID: 2 / 親要素: 1 / 含まれる分子: #1-#2 / NCBI-ID: 12264 / 生物種: Cowpea mosaic virus / ウイルスタイプ: VIRION / ウイルス・単離状態: SPECIES / ウイルス・エンベロープ: No / ウイルス・中空状態: No |
|---|---|
| 宿主 | 生物種:   Cowpea mosaic virus (ササゲモザイクウイルス) Cowpea mosaic virus (ササゲモザイクウイルス) |
-分子 #1: RNA2 polyprotein
| 分子 | 名称: RNA2 polyprotein / タイプ: protein_or_peptide / ID: 1 / コピー数: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Cowpea mosaic virus (ササゲモザイクウイルス) Cowpea mosaic virus (ササゲモザイクウイルス)株: SB |
| 分子量 | 理論値: 20.961564 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: GPVCAEASDV YSPCMIASTP PAPFSDVTAV TFDLINGKIT PVGDDNWNTH IYNPPIMNVL RTAAWKSGTI HVQLNVRGAG VKRADWDGQ VFVYLRQSMN PESYDARTFV ISQPGSAMLN FSFDIIGPNS GFEFAESPWA NQTTWYLECV ATNPRQIQQF E VNMRFDPN ...文字列: GPVCAEASDV YSPCMIASTP PAPFSDVTAV TFDLINGKIT PVGDDNWNTH IYNPPIMNVL RTAAWKSGTI HVQLNVRGAG VKRADWDGQ VFVYLRQSMN PESYDARTFV ISQPGSAMLN FSFDIIGPNS GFEFAESPWA NQTTWYLECV ATNPRQIQQF E VNMRFDPN FRVAGNILMP PFPLSTETPP L UniProtKB: RNA2 polyprotein |
-分子 #2: Cowpea mosaic virus large subunit
| 分子 | 名称: Cowpea mosaic virus large subunit / タイプ: protein_or_peptide / ID: 2 / コピー数: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Cowpea mosaic virus (ササゲモザイクウイルス) Cowpea mosaic virus (ササゲモザイクウイルス)株: SB |
| 分子量 | 理論値: 40.858434 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MEQNLFALSL DDTSSVRGSL LDTKFAQTRV LLSKAMAGGD VLLDEYLYDV VNGQDFRATV AFLRTHVITG KIKVTATTNI SDNSGCCLM LAINSGVRGK YSTDVYTICS QDSMTWNPGC KKNFSFTFNP NPCGDSWSAE MISRSRVRMT VICVSGWTLS P TTDVIAKL ...文字列: MEQNLFALSL DDTSSVRGSL LDTKFAQTRV LLSKAMAGGD VLLDEYLYDV VNGQDFRATV AFLRTHVITG KIKVTATTNI SDNSGCCLM LAINSGVRGK YSTDVYTICS QDSMTWNPGC KKNFSFTFNP NPCGDSWSAE MISRSRVRMT VICVSGWTLS P TTDVIAKL DWSIVNEKCE PTIYHLADCQ NWLPLNRWMG KLTFPQGVTS EVRRMPLSIG GGAGATQAFL ANMPNSWISM WR YFRGELH FEVTKMSSPY IKATVTFLIA FGNLSDAFGF YESFPHRIVQ FAEVEEKCTL VFSQQEFVTA WSTQVNPRTT LEA DGCPYL YAIIHDSTTG TISGDFNLGV KLVGIKDFCG IGSNPGIDGS RLL UniProtKB: RNA2 polyprotein |
-分子 #3: Affimer binding protein
| 分子 | 名称: Affimer binding protein / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 9.286674 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: ENSLEIEELA RFAVDEHNKK ENALLEFVRV VKAKEQVVAG TMYYLTLEAK DGGKKKLYEA KVWVKPWENF KELQEFKPV |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7 |
|---|---|
| グリッド | 材質: COPPER / メッシュ: 400 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: LACEY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 30 sec. / 前処理 - 雰囲気: AIR |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 95 % / チャンバー内温度: 281 K / 装置: LEICA EM GP |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: FEI FALCON II (4k x 4k) 検出モード: INTEGRATING / 撮影したグリッド数: 1 / 実像数: 2980 / 平均露光時間: 2.0 sec. / 平均電子線量: 45.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 70.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー













 Z
Z Y
Y X
X