| 登録情報 | データベース: PDB / ID: 2ati
|
|---|
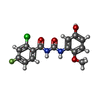
| タイトル | Glycogen Phosphorylase Inhibitors |
|---|
 要素 要素 | Glycogen phosphorylase, liver form |
|---|
 キーワード キーワード | TRANSFERASE / Glycogen Phosphorylase |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
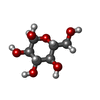
purine nucleobase binding / vitamin binding / D-glucose binding / glycogen phosphorylase / glycogen phosphorylase activity / bile acid binding / glycogen catabolic process / AMP binding / glycogen metabolic process / Glycogen breakdown (glycogenolysis) ...purine nucleobase binding / vitamin binding / D-glucose binding / glycogen phosphorylase / glycogen phosphorylase activity / bile acid binding / glycogen catabolic process / AMP binding / glycogen metabolic process / Glycogen breakdown (glycogenolysis) / necroptotic process / response to bacterium / pyridoxal phosphate binding / glucose homeostasis / secretory granule lumen / ficolin-1-rich granule lumen / Neutrophil degranulation / extracellular exosome / extracellular region / ATP binding / identical protein binding / cytosol / cytoplasm類似検索 - 分子機能 Glycosyl transferase, family 35 / Glycogen/starch/alpha-glucan phosphorylase / Phosphorylase pyridoxal-phosphate attachment site / Carbohydrate phosphorylase / Phosphorylase pyridoxal-phosphate attachment site. / Glycogen Phosphorylase B; / Rossmann fold / 3-Layer(aba) Sandwich / Alpha Beta類似検索 - ドメイン・相同性 alpha-D-glucopyranose / Chem-IHU / PYRIDOXAL-5'-PHOSPHATE / Glycogen phosphorylase, liver form類似検索 - 構成要素 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.9 Å 分子置換 / 解像度: 1.9 Å |
|---|
 データ登録者 データ登録者 | Klabunde, T. / Wendt, K.U. / Kadereit, D. / Brachvogel, V. / Burger, H.J. / Herling, A.W. / Oikonomakos, N.G. / Schmoll, D. / Sarubbi, E. / von Roedern, E. ...Klabunde, T. / Wendt, K.U. / Kadereit, D. / Brachvogel, V. / Burger, H.J. / Herling, A.W. / Oikonomakos, N.G. / Schmoll, D. / Sarubbi, E. / von Roedern, E. / Schoenafinger, K. / Defossa, E. |
|---|
 引用 引用 |  ジャーナル: J.Med.Chem. / 年: 2005タイトル ジャーナル: J.Med.Chem. / 年: 2005タイトル: Acyl ureas as human liver glycogen phosphorylase inhibitors for the treatment of type 2 diabetes. 著者: Klabunde, T. / Wendt, K.U. / Kadereit, D. / Brachvogel, V. / Burger, H.J. / Herling, A.W. / Oikonomakos, N.G. / Kosmopoulou, M.N. / Schmoll, D. / Sarubbi, E. / von Roedern, E. / Defossa, E.#1:  ジャーナル: Protein Sci. / 年: 2005タイトル ジャーナル: Protein Sci. / 年: 2005タイトル: Crystallographic studies on acyl ureas, a new class of glycogen phosphorylase inhibitors, as potential antidiabetic drugs 著者: Oikonomakos, N.G. / Kosmopoulou, M.N. / Chrysina, E.D. / Leonidas, D.D. / Kostas, I.D. / Wendt, K.U. / Klabunde, T. / Defossa, E. #2:  ジャーナル: Mol.Cell / 年: 2000タイトル ジャーナル: Mol.Cell / 年: 2000タイトル: Activation of human liver glycogen phosphorylase by alteration of the secondary structure and packing of the catalytic core 著者: Rath, V.L. / Ammirati, M. / LeMotte, P.K. / Fennell, K.F. / Mansour, M.N. / Danley, D.E. / Hynes, T.R. / Schulte, G.K. / Wasilko, D.J. / Pandit, J. |
|---|
| 履歴 | | 登録 | 2005年8月25日 | 登録サイト: RCSB / 処理サイト: PDBJ |
|---|
| 改定 1.0 | 2006年8月25日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2008年4月30日 | Group: Version format compliance |
|---|
| 改定 1.2 | 2011年7月13日 | Group: Non-polymer description / Version format compliance |
|---|
| 改定 1.3 | 2020年7月29日 | Group: Data collection / Derived calculations / Structure summary
カテゴリ: chem_comp / entity ...chem_comp / entity / pdbx_chem_comp_identifier / pdbx_entity_nonpoly / struct_conn / struct_site / struct_site_gen
Item: _chem_comp.name / _chem_comp.type ..._chem_comp.name / _chem_comp.type / _entity.pdbx_description / _pdbx_entity_nonpoly.name / _struct_conn.pdbx_leaving_atom_flag / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_conn.ptnr2_label_seq_id
解説: Carbohydrate remediation / Provider: repository / タイプ: Remediation |
|---|
| 改定 1.4 | 2025年3月26日 | Group: Data collection / Database references / Structure summary
カテゴリ: chem_comp / chem_comp_atom ...chem_comp / chem_comp_atom / chem_comp_bond / database_2 / pdbx_entry_details
Item: _chem_comp.pdbx_synonyms / _database_2.pdbx_DOI / _database_2.pdbx_database_accession |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 1.9 Å
分子置換 / 解像度: 1.9 Å  データ登録者
データ登録者 引用
引用 ジャーナル: J.Med.Chem. / 年: 2005
ジャーナル: J.Med.Chem. / 年: 2005 ジャーナル: Protein Sci. / 年: 2005
ジャーナル: Protein Sci. / 年: 2005 ジャーナル: Mol.Cell / 年: 2000
ジャーナル: Mol.Cell / 年: 2000 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 2ati.cif.gz
2ati.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb2ati.ent.gz
pdb2ati.ent.gz PDB形式
PDB形式 2ati.json.gz
2ati.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/at/2ati
https://data.pdbj.org/pub/pdb/validation_reports/at/2ati ftp://data.pdbj.org/pub/pdb/validation_reports/at/2ati
ftp://data.pdbj.org/pub/pdb/validation_reports/at/2ati リンク
リンク 集合体
集合体
 要素
要素 Homo sapiens (ヒト)
Homo sapiens (ヒト)
 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  ESRF
ESRF  / ビームライン: ID14-2
/ ビームライン: ID14-2 解析
解析 分子置換 / 最高解像度: 1.9 Å / σ(F): 0 / 立体化学のターゲット値: Engh & Huber
分子置換 / 最高解像度: 1.9 Å / σ(F): 0 / 立体化学のターゲット値: Engh & Huber ムービー
ムービー コントローラー
コントローラー



























 PDBj
PDBj