+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-21701 | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
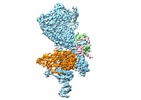
| タイトル | Structure of the Saccharomyces cerevisiae polymerase epsilon holoenzyme | ||||||||||||
 マップデータ マップデータ | Saccharomyces cerevisiae polymerase epsilon holoenzyme | ||||||||||||
 試料 試料 |
| ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報: / : / chromatin remodeling => GO:0006338 / CHRAC / : / DNA-templated DNA replication maintenance of fidelity / gene conversion / DNA replication initiation / epsilon DNA polymerase complex / SUMO binding ...: / : / chromatin remodeling => GO:0006338 / CHRAC / : / DNA-templated DNA replication maintenance of fidelity / gene conversion / DNA replication initiation / epsilon DNA polymerase complex / SUMO binding / Activation of the pre-replicative complex / single-stranded DNA 3'-5' DNA exonuclease activity / Termination of translesion DNA synthesis / mitotic DNA replication checkpoint signaling / mitotic intra-S DNA damage checkpoint signaling / 加水分解酵素; エステル加水分解酵素; 5'-リン酸モノエステル産生エンドデオキシリボヌクレアーゼ / nucleotide-excision repair, DNA gap filling / DNA replication proofreading / mitotic sister chromatid cohesion / leading strand elongation / nuclear replication fork / Dual incision in TC-NER / error-prone translesion synthesis / heterochromatin formation / nucleosomal DNA binding / base-excision repair, gap-filling / replication fork / base-excision repair / chromatin DNA binding / DNA-templated DNA replication / double-strand break repair via nonhomologous end joining / double-strand break repair / mitotic cell cycle / single-stranded DNA binding / 4 iron, 4 sulfur cluster binding / double-stranded DNA binding / DNA-directed DNA polymerase / DNA-directed DNA polymerase activity / cell cycle / protein heterodimerization activity / nucleotide binding / mRNA binding / DNA damage response / DNA binding / zinc ion binding / nucleus / cytoplasm 類似検索 - 分子機能 | ||||||||||||
| 生物種 |  | ||||||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.5 Å | ||||||||||||
 データ登録者 データ登録者 | Yuan Z / Georgescu R / Schauer GD / O'Donnell M / Li H | ||||||||||||
| 資金援助 |  米国, 3件 米国, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2020 ジャーナル: Nat Commun / 年: 2020タイトル: Structure of the polymerase ε holoenzyme and atomic model of the leading strand replisome. 著者: Zuanning Yuan / Roxana Georgescu / Grant D Schauer / Michael E O'Donnell / Huilin Li /  要旨: The eukaryotic leading strand DNA polymerase (Pol) ε contains 4 subunits, Pol2, Dpb2, Dpb3 and Dpb4. Pol2 is a fusion of two B-family Pols; the N-terminal Pol module is catalytic and the C-terminal ...The eukaryotic leading strand DNA polymerase (Pol) ε contains 4 subunits, Pol2, Dpb2, Dpb3 and Dpb4. Pol2 is a fusion of two B-family Pols; the N-terminal Pol module is catalytic and the C-terminal Pol module is non-catalytic. Despite extensive efforts, there is no atomic structure for Pol ε holoenzyme, critical to understanding how DNA synthesis is coordinated with unwinding and the DNA path through the CMG helicase-Pol ε-PCNA clamp. We show here a 3.5-Å cryo-EM structure of yeast Pol ε revealing that the Dpb3-Dpb4 subunits bridge the two DNA Pol modules of Pol2, holding them rigid. This information enabled an atomic model of the leading strand replisome. Interestingly, the model suggests that an OB fold in Dbp2 directs leading ssDNA from CMG to the Pol ε active site. These results complete the DNA path from entry of parental DNA into CMG to exit of daughter DNA from PCNA. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_21701.map.gz emd_21701.map.gz | 6.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-21701-v30.xml emd-21701-v30.xml emd-21701.xml emd-21701.xml | 16.9 KB 16.9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_21701.png emd_21701.png | 144.5 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-21701 http://ftp.pdbj.org/pub/emdb/structures/EMD-21701 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-21701 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-21701 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_21701_validation.pdf.gz emd_21701_validation.pdf.gz | 345.7 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_21701_full_validation.pdf.gz emd_21701_full_validation.pdf.gz | 345.3 KB | 表示 | |
| XML形式データ |  emd_21701_validation.xml.gz emd_21701_validation.xml.gz | 6.1 KB | 表示 | |
| CIF形式データ |  emd_21701_validation.cif.gz emd_21701_validation.cif.gz | 6.9 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21701 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21701 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21701 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21701 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_21701.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_21701.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Saccharomyces cerevisiae polymerase epsilon holoenzyme | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.029 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : DNA polymerase epsilon
| 全体 | 名称: DNA polymerase epsilon |
|---|---|
| 要素 |
|
-超分子 #1: DNA polymerase epsilon
| 超分子 | 名称: DNA polymerase epsilon / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#4 |
|---|---|
| 由来(天然) | 生物種:  株: ATCC 204508 / S288c |
| 組換発現 | 生物種:  |
-分子 #1: DNA polymerase epsilon catalytic subunit A
| 分子 | 名称: DNA polymerase epsilon catalytic subunit A / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO / EC番号: DNA-directed DNA polymerase |
|---|---|
| 由来(天然) | 生物種:  株: ATCC 204508 / S288c |
| 分子量 | 理論値: 255.992484 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MMFGKKKNNG GSSTARYSAG NKYNTLSNNY ALSAQQLLNA SKIDDIDSMM GFERYVPPQY NGRFDAKDID QIPGRVGWLT NMHATLVSQ ETLSSGSNGG GNSNDGERVT TNQGISGVDF YFLDEEGGSF KSTVVYDPYF FIACNDESRV NDVEELVKKY L ESCLKSLQ ...文字列: MMFGKKKNNG GSSTARYSAG NKYNTLSNNY ALSAQQLLNA SKIDDIDSMM GFERYVPPQY NGRFDAKDID QIPGRVGWLT NMHATLVSQ ETLSSGSNGG GNSNDGERVT TNQGISGVDF YFLDEEGGSF KSTVVYDPYF FIACNDESRV NDVEELVKKY L ESCLKSLQ IIRKEDLTMD NHLLGLQKTL IKLSFVNSNQ LFEARKLLRP ILQDNANNNV QRNIYNVAAN GSEKVDAKHL IE DIREYDV PYHVRVSIDK DIRVGKWYKV TQQGFIEDTR KIAFADPVVM AFDIETTKPP LKFPDSAVDQ IMMISYMIDG EGF LITNRE IISEDIEDFE YTPKPEYPGF FTIFNENDEV ALLQRFFEHI RDVRPTVIST FNGDFFDWPF IHNRSKIHGL DMFD EIGFA PDAEGEYKSS YCSHMDCFRW VKRDSYLPQG SQGLKAVTQS KLGYNPIELD PELMTPYAFE KPQHLSEYSV SDAVA TYYL YMKYVHPFIF SLCTIIPLNP DETLRKGTGT LCEMLLMVQA YQHNILLPNK HTDPIERFYD GHLLESETYV GGHVES LEA GVFRSDLKNE FKIDPSAIDE LLQELPEALK FSVEVENKSS VDKVTNFEEI KNQITQKLLE LKENNIRNEL PLIYHVD VA SMYPNIMTTN RLQPDSIKAE RDCASCDFNR PGKTCARKLK WAWRGEFFPS KMDEYNMIKR ALQNETFPNK NKFSKKKV L TFDELSYADQ VIHIKKRLTE YSRKVYHRVK VSEIVEREAI VCQRENPFYV DTVKSFRDRR YEFKGLAKTW KGNLSKIDP SDKHARDEAK KMIVLYDSLQ LAHKVILNSF YGYVMRKGSR WYSMEMAGIT CLTGATIIQM ARALVERVGR PLELDTDGIW CILPKSFPE TYFFTLENGK KLYLSYPCSM LNYRVHQKFT NHQYQELKDP LNYIYETHSE NTIFFEVDGP YKAMILPSSK E EGKGIKKR YAVFNEDGSL AELKGFELKR RGELQLIKNF QSDIFKVFLE GDTLEGCYSA VASVCNRWLD VLDSHGLMLE DE DLVSLIC ENRSMSKTLK EYEGQKSTSI TTARRLGDFL GEDMVKDKGL QCKYIISSKP FNAPVTERAI PVAIFSADIP IKR SFLRRW TLDPSLEDLD IRTIIDWGYY RERLGSAIQK IITIPAALQG VSNPVPRVEH PDWLKRKIAT KEDKFKQTSL TKFF SKTKN VPTMGKIKDI EDLFEPTVEE DNAKIKIART TKKKAVSKRK RNQLTNEEDP LVLPSEIPSM DEDYVGWLNY QKIKW KIQA RDRKRRDQLF GNTNSSRERS ALGSMIRKQA ESYANSTWEV LQYKDSGEPG VLEVFVTING KVQNITFHIP KTIYMK FKS QTMPLQKIKN CLIEKSSASL PNNPKTSNPA GGQLFKITLP ESVFLEEKEN CTSIFNDENV LGVFEGTITP HQRAIMD LG ASVTFRSKAM GALGKGIQQG FEMKDLSMAE NERYLSGFSM DIGYLLHFPT SIGYEFFSLF KSWGDTITIL VLKPSNQA Q EINASSLGQI YKQMFEKKKG KIETYSYLVD IKEDINFEFV YFTDISKLYR RLSQETTKLK EERGLQFLLL LQSPFITKL LGTIRLLNQM PIVKLSLNEV LLPQLNWQPT LLKKLVNHVL SSGSWISHLI KLSQYSNIPI CNLRLDSMDY IIDVLYARKL KKENIVLWW NEKAPLPDHG GIQNDFDLNT SWIMNDSEFP KINNSGVYDN VVLDVGVDNL TVNTILTSAL INDAEGSDLV N NNMGIDDK DAVINSPSEF VHDAFSNDAL NVLRGMLKEW WDEALKENST ADLLVNSLAS WVQNPNAKLF DGLLRYHVHN LT KKALLQL VNEFSALGST IVYADRNQIL IKTNKYSPEN CYAYSQYMMK AVRTNPMFSY LDLNIKRYWD LLIWMDKFNF SGL ACIEIE EKENQDYTAV SQWQLKKFLS PIYQPEFEDW MMIILDSMLK TKQSYLKLNS GTQRPTQIVN VKKQDKEDSV ENSL NGFSH LFSKPLMKRV KKLFKNQQEF ILDPQYEADY VIPVLPGSHL NVKNPLLELV KSLCHVMLLS KSTILEIRTL RKELL KIFE LREFAKVAEF KDPSLSLVVP DFLCEYCFFI SDIDFCKAAP ESIFSCVRCH KAFNQVLLQE HLIQKLRSDI ESYLIQ DLR CSRCHKVKRD YMSAHCPCAG AWEGTLPRES IVQKLNVFKQ VAKYYGFDIL LSCIADLTI |
-分子 #2: DNA polymerase epsilon subunit B
| 分子 | 名称: DNA polymerase epsilon subunit B / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  株: ATCC 204508 / S288c |
| 分子量 | 理論値: 78.425852 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MFGSGNVLPV KIQPPLLRPL AYRVLSRKYG LSIKSDGLSA LAEFVGTNIG ANWRQGPATI KFLEQFAAVW KQQERGLFID QSGVKEVIQ EMKEREKVEW SHEHPIQHEE NILGRTDDDE NNSDDEMPIA ADSSLQNVSL SSPMRQPTER DEYKQPFKPE S SKALDWRD ...文字列: MFGSGNVLPV KIQPPLLRPL AYRVLSRKYG LSIKSDGLSA LAEFVGTNIG ANWRQGPATI KFLEQFAAVW KQQERGLFID QSGVKEVIQ EMKEREKVEW SHEHPIQHEE NILGRTDDDE NNSDDEMPIA ADSSLQNVSL SSPMRQPTER DEYKQPFKPE S SKALDWRD YFKVINASQQ QRFSYNPHKM QFIFVPNKKQ NGLGGIAGFL PDIEDKVQMF LTRYYLTNDR VMRNENFQNS DM FNPLSSM VSLQNELSNT NRQQQSSSMS ITPIKNLLGR DAQNFLLLGL LNKNFKGNWS LEDPSGSVEI DISQTIPTQG HYY VPGCMV LVEGIYYSVG NKFHVTSMTL PPGERREITL ETIGNLDLLG IHGISNNNFI ARLDKDLKIR LHLLEKELTD HKFV ILGAN LFLDDLKIMT ALSKILQKLN DDPPTLLIWQ GSFTSVPVFA SMSSRNISSS TQFKNNFDAL ATLLSRFDNL TENTT MIFI PGPNDLWGSM VSLGASGTLP QDPIPSAFTK KINKVCKNVV WSSNPTRIAY LSQEIVIFRD DLSGRFKRHR LEFPFN ESE DVYTENDNMM SKDTDIVPID ELVKEPDQLP QKVQETRKLV KTILDQGHLS PFLDSLRPIS WDLDHTLTLC PIPSTMV LC DTTSAQFDLT YNGCKVINPG SFIHNRRARY MEYVPSSKKT IQEEIYI |
-分子 #3: DNA polymerase epsilon subunit C
| 分子 | 名称: DNA polymerase epsilon subunit C / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  株: ATCC 204508 / S288c |
| 分子量 | 理論値: 22.694014 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MSNLVKEKAP VFPISKVKKI AKCDPEYVIT SNVAISATAF AAELFVQNLV EESLVLAQLN SKGKTSLRLS LNSIEECVEK RDNFRFLED AIKQLKKNSA LDKKRELNMQ PGRSDQEVVI EEPELHEDDG VEEEEEEDEV SEEEEPVHNE ELLDDSKDQQ N DKSTRSVA ...文字列: MSNLVKEKAP VFPISKVKKI AKCDPEYVIT SNVAISATAF AAELFVQNLV EESLVLAQLN SKGKTSLRLS LNSIEECVEK RDNFRFLED AIKQLKKNSA LDKKRELNMQ PGRSDQEVVI EEPELHEDDG VEEEEEEDEV SEEEEPVHNE ELLDDSKDQQ N DKSTRSVA SLLSRFQYKS ALDVGEHSDS SDIEVDHTKS TDP |
-分子 #4: DNA polymerase epsilon subunit D
| 分子 | 名称: DNA polymerase epsilon subunit D / タイプ: protein_or_peptide / ID: 4 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  株: ATCC 204508 / S288c |
| 分子量 | 理論値: 22.029484 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MPPKGWRKDA QGNYPTTSYI KEQENITIQD LLFPKSTIVN LAREVPQQSG KKLLINKDAS LALQRGATVF VNHLLLFARE IAKSQDKKS CSVDDVLSAL DHIGHSALKG PVRDKLDEYQ AAVEQRKKEK LDSGEVDADG DIDMGEDKEN VPVEKVKEHD E IEEQGDAL ...文字列: MPPKGWRKDA QGNYPTTSYI KEQENITIQD LLFPKSTIVN LAREVPQQSG KKLLINKDAS LALQRGATVF VNHLLLFARE IAKSQDKKS CSVDDVLSAL DHIGHSALKG PVRDKLDEYQ AAVEQRKKEK LDSGEVDADG DIDMGEDKEN VPVEKVKEHD E IEEQGDAL QDVEESSEKK QKTESQDVET RVQNLEQT |
-分子 #5: ZINC ION
| 分子 | 名称: ZINC ION / タイプ: ligand / ID: 5 / コピー数: 1 / 式: ZN |
|---|---|
| 分子量 | 理論値: 65.409 Da |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: SUPER-RESOLUTION / 平均電子線量: 60.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 最終 再構成 | 想定した対称性 - 点群: C1 (非対称) / 解像度のタイプ: BY AUTHOR / 解像度: 3.5 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 187298 |
|---|---|
| 初期 角度割当 | タイプ: PROJECTION MATCHING |
| 最終 角度割当 | タイプ: PROJECTION MATCHING |
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: FLEXIBLE FIT |
|---|---|
| 得られたモデル |  PDB-6wjv: |
 ムービー
ムービー コントローラー
コントローラー