| 登録情報 | データベース: PDB / ID: 1zp0
|
|---|
| タイトル | Crystal Structure of Mitochondrial Respiratory Complex II bound with 3-nitropropionate and 2-thenoyltrifluoroacetone |
|---|
 要素 要素 | - FAD-binding protein
- Iron-sulfur protein
- Large cytochrome binding protein
- Small cytochrome binding protein
|
|---|
 キーワード キーワード | OXIDOREDUCTASE / succinate / ubiquinone oxidoreductase / respiratory Complex II / inhibitors / membrane protein structure |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
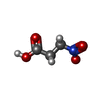
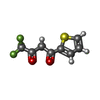
Maturation of TCA enzymes and regulation of TCA cycle / Citric acid cycle (TCA cycle) / 酸化還元酵素; CH-OHの結合に対し酸化酵素として働く; キノンあるいはその類似化合物を用いる / succinate metabolic process / respiratory chain complex II (succinate dehydrogenase) / mitochondrial electron transport, succinate to ubiquinone / succinate dehydrogenase (quinone) activity / succinate dehydrogenase / 3 iron, 4 sulfur cluster binding / ubiquinone binding ...Maturation of TCA enzymes and regulation of TCA cycle / Citric acid cycle (TCA cycle) / 酸化還元酵素; CH-OHの結合に対し酸化酵素として働く; キノンあるいはその類似化合物を用いる / succinate metabolic process / respiratory chain complex II (succinate dehydrogenase) / mitochondrial electron transport, succinate to ubiquinone / succinate dehydrogenase (quinone) activity / succinate dehydrogenase / 3 iron, 4 sulfur cluster binding / ubiquinone binding / tricarboxylic acid cycle / protein-membrane adaptor activity / aerobic respiration / respiratory electron transport chain / 2 iron, 2 sulfur cluster binding / mitochondrial membrane / flavin adenine dinucleotide binding / nervous system development / 4 iron, 4 sulfur cluster binding / electron transfer activity / mitochondrial inner membrane / heme binding / nucleolus / metal ion binding類似検索 - 分子機能 Single helix bin / Succinate dehydrogenase [ubiquinone] cytochrome b small subunit, CybS / CybS, succinate dehydrogenase cytochrome B small subunit / succinate dehydrogenase protein domain / Fumarate reductase/succinate dehydrogenase, transmembrane subunit / Succinate dehydrogenase, cytochrome b subunit, conserved site / Succinate dehydrogenase cytochrome b subunit signature 1. / Succinate dehydrogenase cytochrome b subunit signature 2. / Succinate dehydrogenase, cytochrome b556 subunit / Fumarate reductase/succinate dehydrogenase flavoprotein-like, C-terminal domain ...Single helix bin / Succinate dehydrogenase [ubiquinone] cytochrome b small subunit, CybS / CybS, succinate dehydrogenase cytochrome B small subunit / succinate dehydrogenase protein domain / Fumarate reductase/succinate dehydrogenase, transmembrane subunit / Succinate dehydrogenase, cytochrome b subunit, conserved site / Succinate dehydrogenase cytochrome b subunit signature 1. / Succinate dehydrogenase cytochrome b subunit signature 2. / Succinate dehydrogenase, cytochrome b556 subunit / Fumarate reductase/succinate dehydrogenase flavoprotein-like, C-terminal domain / Succinate dehydrogenase, flavoprotein subunit / Succinate dehydrogenase/fumarate reductase type B, transmembrane subunit / Succinate dehydrogenase/Fumarate reductase transmembrane subunit / Alpha-helical ferredoxin / Fumarate Reductase Iron-sulfur Protein; Chain B, domain 2 / Succinate dehydrogenase/fumarate reductase, flavoprotein subunit / Fumarate reductase/succinate dehydrogenase, FAD-binding site / Fumarate reductase / succinate dehydrogenase FAD-binding site. / 3 helical TM bundles of succinate and fumarate reductases / Fumarate reductase/succinate dehydrogenase, transmembrane subunit / : / 4Fe-4S dicluster domain / Succinate dehydrogenase/fumarate reductase iron-sulphur protein / FAD-dependent oxidoreductase SdhA/FrdA/AprA / Succinate dehydogenase/fumarate reductase N-terminal / 2Fe-2S iron-sulfur cluster binding domain / Flavocytochrome C3; Chain A, domain 1 / Succinate dehydrogenase/fumarate reductase flavoprotein, catalytic domain / Fumarate reductase/succinate dehydrogenase flavoprotein-like, C-terminal / Fumarate reductase flavoprotein C-term / Fumarate reductase/succinate dehydrogenase flavoprotein-like, C-terminal domain superfamily / Succinate dehydrogenase/fumarate reductase flavoprotein, catalytic domain superfamily / FAD-dependent oxidoreductase 2, FAD binding domain / Rhinovirus 14, subunit 4 / FAD binding domain / Alpha-helical ferredoxin / 2Fe-2S ferredoxin, iron-sulphur binding site / 2Fe-2S ferredoxin-type iron-sulfur binding region signature. / Beta-grasp domain / Beta-grasp domain superfamily / FAD/NAD(P)-binding domain / 2Fe-2S ferredoxin-type iron-sulfur binding domain profile. / FAD/NAD(P)-binding domain / 2Fe-2S ferredoxin-type iron-sulfur binding domain / 2Fe-2S ferredoxin-like superfamily / 4Fe-4S ferredoxin, iron-sulphur binding, conserved site / 4Fe-4S ferredoxin-type iron-sulfur binding region signature. / Single alpha-helices involved in coiled-coils or other helix-helix interfaces / 4Fe-4S ferredoxin-type iron-sulfur binding domain profile. / 4Fe-4S ferredoxin-type, iron-sulphur binding domain / Methane Monooxygenase Hydroxylase; Chain G, domain 1 / 3-Layer(bba) Sandwich / FAD/NAD(P)-binding domain superfamily / Few Secondary Structures / Irregular / Ubiquitin-like (UB roll) / Roll / Alpha-Beta Complex / Up-down Bundle / Orthogonal Bundle / Mainly Alpha / Alpha Beta類似検索 - ドメイン・相同性 3-NITROPROPANOIC ACID / FE3-S4 CLUSTER / FLAVIN-ADENINE DINUCLEOTIDE / FE2/S2 (INORGANIC) CLUSTER / PROTOPORPHYRIN IX CONTAINING FE / IRON/SULFUR CLUSTER / 4,4,4-TRIFLUORO-1-THIEN-2-YLBUTANE-1,3-DIONE / Succinate dehydrogenase [ubiquinone] cytochrome b small subunit, mitochondrial / Succinate dehydrogenase cytochrome b560 subunit, mitochondrial / Succinate dehydrogenase [ubiquinone] iron-sulfur subunit, mitochondrial / Succinate dehydrogenase [ubiquinone] flavoprotein subunit, mitochondrial類似検索 - 構成要素 |
|---|
| 生物種 |   Sus scrofa (ブタ) Sus scrofa (ブタ) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 3.5 Å 分子置換 / 解像度: 3.5 Å |
|---|
 データ登録者 データ登録者 | Sun, F. / Huo, X. / Zhai, Y. / Wang, A. / Xu, J. / Su, D. / Bartlam, M. / Rao, Z. |
|---|
 引用 引用 |  ジャーナル: Cell(Cambridge,Mass.) / 年: 2005 ジャーナル: Cell(Cambridge,Mass.) / 年: 2005
タイトル: Crystal Structure of Mitochondrial Respiratory Membrane Protein Complex II
著者: Sun, F. / Huo, X. / Zhai, Y. / Wang, A. / Xu, J. / Su, D. / Bartlam, M. / Rao, Z. |
|---|
| 履歴 | | 登録 | 2005年5月16日 | 登録サイト: RCSB / 処理サイト: PDBJ |
|---|
| 改定 1.0 | 2005年7月12日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2008年4月30日 | Group: Version format compliance |
|---|
| 改定 1.2 | 2011年7月13日 | Group: Version format compliance |
|---|
| 改定 2.0 | 2019年9月4日 | Group: Atomic model / Data collection / Derived calculations
カテゴリ: atom_site / pdbx_struct_conn_angle / struct_conn
Item: _atom_site.B_iso_or_equiv / _atom_site.Cartn_x ..._atom_site.B_iso_or_equiv / _atom_site.Cartn_x / _atom_site.Cartn_y / _atom_site.Cartn_z / _pdbx_struct_conn_angle.ptnr1_label_atom_id / _pdbx_struct_conn_angle.ptnr2_label_atom_id / _pdbx_struct_conn_angle.ptnr3_label_atom_id / _pdbx_struct_conn_angle.value / _struct_conn.pdbx_leaving_atom_flag / _struct_conn.ptnr1_label_atom_id |
|---|
| 改定 2.1 | 2023年10月25日 | Group: Data collection / Database references ...Data collection / Database references / Derived calculations / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model / pdbx_struct_conn_angle / struct_conn / struct_site
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_struct_conn_angle.ptnr1_auth_comp_id / _pdbx_struct_conn_angle.ptnr1_auth_seq_id / _pdbx_struct_conn_angle.ptnr1_label_asym_id / _pdbx_struct_conn_angle.ptnr1_label_atom_id / _pdbx_struct_conn_angle.ptnr1_label_comp_id / _pdbx_struct_conn_angle.ptnr1_label_seq_id / _pdbx_struct_conn_angle.ptnr2_auth_comp_id / _pdbx_struct_conn_angle.ptnr2_auth_seq_id / _pdbx_struct_conn_angle.ptnr2_label_asym_id / _pdbx_struct_conn_angle.ptnr2_label_atom_id / _pdbx_struct_conn_angle.ptnr2_label_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_seq_id / _pdbx_struct_conn_angle.ptnr3_label_asym_id / _pdbx_struct_conn_angle.ptnr3_label_atom_id / _pdbx_struct_conn_angle.ptnr3_label_comp_id / _pdbx_struct_conn_angle.value / _struct_conn.pdbx_dist_value / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_conn.ptnr2_label_seq_id / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id |
|---|
| 改定 2.2 | 2024年11月20日 | Group: Structure summary
カテゴリ: pdbx_entry_details / pdbx_modification_feature |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 3.5 Å
分子置換 / 解像度: 3.5 Å  データ登録者
データ登録者 引用
引用 ジャーナル: Cell(Cambridge,Mass.) / 年: 2005
ジャーナル: Cell(Cambridge,Mass.) / 年: 2005 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 1zp0.cif.gz
1zp0.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb1zp0.ent.gz
pdb1zp0.ent.gz PDB形式
PDB形式 1zp0.json.gz
1zp0.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/zp/1zp0
https://data.pdbj.org/pub/pdb/validation_reports/zp/1zp0 ftp://data.pdbj.org/pub/pdb/validation_reports/zp/1zp0
ftp://data.pdbj.org/pub/pdb/validation_reports/zp/1zp0 リンク
リンク 集合体
集合体
 要素
要素
















 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  APS
APS  / ビームライン: 19-ID / 波長: 0.9793 Å
/ ビームライン: 19-ID / 波長: 0.9793 Å 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー














 PDBj
PDBj




















