+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-1765 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Single particle analysis of the 1:1 complex of PSD-95 and Kir2.1NC_4 in negative stain | |||||||||
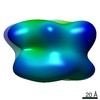
 マップデータ マップデータ | Negative stain EM map of the complex of PSD-95 and Kir2.1NC | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Scaffold protein / membrane associated / Guanylatekinase / PDZ / SH3 / Ion Channel / cytoplasmic domain / inwardly rectifying / membrane protein / homotetramer | |||||||||
| 機能・相同性 | Potassium channel, inwardly rectifying, Kir2.1 / neuronal ion channel clustering / Disks large 1-like / membrane => GO:0016020 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |   | |||||||||
| 手法 | 単粒子再構成法 / ネガティブ染色法 / 解像度: 20.5 Å | |||||||||
 データ登録者 データ登録者 | Fomina S / Howard TD / Sleator OK / Golovanova M / O'Ryan L / Leyland M / Grossmann JG / Collins RF / Prince SM | |||||||||
 引用 引用 |  ジャーナル: Biochim Biophys Acta / 年: 2011 ジャーナル: Biochim Biophys Acta / 年: 2011タイトル: Self-directed assembly and clustering of the cytoplasmic domains of inwardly rectifying Kir2.1 potassium channels on association with PSD-95. 著者: Svetlana Fomina / Tina D Howard / Olivia K Sleator / Marina Golovanova / Liam O'Ryan / Mark L Leyland / J Günter Grossmann / Richard F Collins / Stephen M Prince /  要旨: The interaction of the extra-membranous domain of tetrameric inwardly rectifying Kir2.1 ion channels (Kir2.1NC(4)) with the membrane associated guanylate kinase protein PSD-95 has been studied using ...The interaction of the extra-membranous domain of tetrameric inwardly rectifying Kir2.1 ion channels (Kir2.1NC(4)) with the membrane associated guanylate kinase protein PSD-95 has been studied using Transmission Electron Microscopy in negative stain. Three types of complexes were observed in electron micrographs corresponding to a 1:1 complex, a large self-enclosed tetrad complex and extended chains of linked channel domains. Using models derived from small angle X-ray scattering experiments in which high resolution structures from X-ray crystallographic and Nuclear Magnetic Resonance studies are positioned, the envelopes from single particle analysis can be resolved as a Kir2.1NC(4):PSD-95 complex and a tetrad of this unit (Kir2.1NC(4):PSD-95)(4). The tetrad complex shows the close association of the Kir2.1 cytoplasmic domains and the influence of PSD-95 mediated self-assembly on the clustering of these channels. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_1765.map.gz emd_1765.map.gz | 214.7 KB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-1765-v30.xml emd-1765-v30.xml emd-1765.xml emd-1765.xml | 12.5 KB 12.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_1765.png emd_1765.png | 148.6 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-1765 http://ftp.pdbj.org/pub/emdb/structures/EMD-1765 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-1765 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-1765 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_1765_validation.pdf.gz emd_1765_validation.pdf.gz | 216.3 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_1765_full_validation.pdf.gz emd_1765_full_validation.pdf.gz | 215.5 KB | 表示 | |
| XML形式データ |  emd_1765_validation.xml.gz emd_1765_validation.xml.gz | 4.6 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1765 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1765 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1765 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1765 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_1765.map.gz / 形式: CCP4 / 大きさ: 422.9 KB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_1765.map.gz / 形式: CCP4 / 大きさ: 422.9 KB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Negative stain EM map of the complex of PSD-95 and Kir2.1NC | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 3.667 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Complex of mouse Kir2.1, cytoplamic domain, homotetramer of fused...
| 全体 | 名称: Complex of mouse Kir2.1, cytoplamic domain, homotetramer of fused N,C termini with rat PSD-95 |
|---|---|
| 要素 |
|
-超分子 #1000: Complex of mouse Kir2.1, cytoplamic domain, homotetramer of fused...
| 超分子 | 名称: Complex of mouse Kir2.1, cytoplamic domain, homotetramer of fused N,C termini with rat PSD-95 タイプ: sample / ID: 1000 詳細: Multi-refinement was undertaken to separate Kir2.1NC_4 alone from the complex 集合状態: One tetramer of Kir2.1NC binds to PSD-95 / Number unique components: 2 |
|---|---|
| 分子量 | 理論値: 218 KDa / 手法: Sum of component MW |
-分子 #1: Kir2.1 cytoplasmic domain
| 分子 | 名称: Kir2.1 cytoplasmic domain / タイプ: protein_or_peptide / ID: 1 / Name.synonym: Kir2.1NC / コピー数: 4 / 集合状態: Tetramer / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 実験値: 140 KDa / 理論値: 140 KDa |
| 組換発現 | 生物種:  |
| 配列 | GO: membrane => GO:0016020 / InterPro: Potassium channel, inwardly rectifying, Kir2.1 |
-分子 #2: PSD-95
| 分子 | 名称: PSD-95 / タイプ: protein_or_peptide / ID: 2 / Name.synonym: PSD-95 / コピー数: 1 / 集合状態: Monomer / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 実験値: 95 KDa / 理論値: 78 KDa |
| 組換発現 | 生物種:  |
| 配列 | GO: neuronal ion channel clustering / InterPro: Disks large 1-like |
-実験情報
-構造解析
| 手法 | ネガティブ染色法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 1 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 詳細: 20mM Tris/HCl, 150mM NaCl, 1mM reduced GSH, 1mM EDTA, 50mM L-Glutamic acid, 50mM L-Arginine |
| 染色 | タイプ: NEGATIVE 詳細: Samples were adsorbed onto freshly glow discharged carbon film grids. Sample solution was pipetted into the grid followed by blotting, de-ionized water was then applied for 10s followed by ...詳細: Samples were adsorbed onto freshly glow discharged carbon film grids. Sample solution was pipetted into the grid followed by blotting, de-ionized water was then applied for 10s followed by blotting, 2%w/v Uranyl Acetate solution was applied followed by a final blotting step. |
| グリッド | 詳細: 400 mesh Copper |
| 凍結 | 凍結剤: NONE / 装置: OTHER |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TECNAI 10 |
|---|---|
| 詳細 | Low dose |
| 撮影 | カテゴリ: FILM / フィルム・検出器のモデル: GENERIC FILM / デジタル化 - スキャナー: OTHER / デジタル化 - サンプリング間隔: 15 µm / 実像数: 15 / Od range: 2 / ビット/ピクセル: 8 |
| Tilt angle min | 0 |
| Tilt angle max | 0 |
| 電子線 | 加速電圧: 100 kV / 電子線源: TUNGSTEN HAIRPIN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 3.6 mm / 最大 デフォーカス(公称値): 1.75 µm / 最小 デフォーカス(公称値): 0.6 µm / 倍率(公称値): 43000 |
| 試料ステージ | 試料ホルダー: Eucentric / 試料ホルダーモデル: PHILIPS ROTATION HOLDER |
- 画像解析
画像解析
| 詳細 | Particles initially selected using automated particle picking based on a subset of representative particles on each micrograph. |
|---|---|
| CTF補正 | 詳細: Parameters determined using a calculated Scattering curve |
| 最終 再構成 | 想定した対称性 - 点群: C1 (非対称) / 解像度のタイプ: BY AUTHOR / 解像度: 20.5 Å / 解像度の算出法: FSC 0.5 CUT-OFF / ソフトウェア - 名称: EMAN / 使用した粒子像数: 24199 |
| 最終 2次元分類 | クラス数: 84 |
-原子モデル構築 1
| 初期モデル | PDB ID: |
|---|---|
| ソフトウェア | 名称:  Chimera Chimera |
| 詳細 | ROTATION MATRIX 0.62166 0.76947 -0.14647 0.00842 0.18041 0.98355 0.78325 -0.61267 0.10567 TRANSLATION VECTOR IN AS -7.89876 -3.87420 -3.22822 |
| 精密化 | 空間: REAL |
-原子モデル構築 2
| 初期モデル | PDB ID: |
|---|---|
| ソフトウェア | 名称:  Chimera Chimera |
| 詳細 | ROTATION MATRIX 0.31682 0.16747 0.93358 -0.39203 -0.87316 0.28967 0.86368 -0.45776 -0.21099 TRANSLATION VECTOR IN AS -6.39213 21.17728 3.96066 |
| 精密化 | 空間: REAL |
 ムービー
ムービー コントローラー
コントローラー














 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)