+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of coxsackievirus A6 mature virion | |||||||||
 マップデータ マップデータ | Locally sharpened map (in LocalDeblur) of CV-A6 virion | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | enterovirus / coxsackievirus A6 / virion / native / capsid / cryo-EM / VIRUS | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of MDA-5 activity / picornain 2A / symbiont-mediated suppression of host mRNA export from nucleus / symbiont genome entry into host cell via pore formation in plasma membrane / picornain 3C / T=pseudo3 icosahedral viral capsid / host cell cytoplasmic vesicle membrane / protein complex oligomerization / cytoplasmic vesicle membrane / monoatomic ion channel activity ...symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of MDA-5 activity / picornain 2A / symbiont-mediated suppression of host mRNA export from nucleus / symbiont genome entry into host cell via pore formation in plasma membrane / picornain 3C / T=pseudo3 icosahedral viral capsid / host cell cytoplasmic vesicle membrane / protein complex oligomerization / cytoplasmic vesicle membrane / monoatomic ion channel activity / endocytosis involved in viral entry into host cell / nucleoside-triphosphate phosphatase / RNA helicase activity / induction by virus of host autophagy / RNA-directed RNA polymerase / viral RNA genome replication / cysteine-type endopeptidase activity / RNA-dependent RNA polymerase activity / virus-mediated perturbation of host defense response / DNA-templated transcription / virion attachment to host cell / structural molecule activity / ATP hydrolysis activity / proteolysis / RNA binding / ATP binding / metal ion binding 類似検索 - 分子機能 | |||||||||
| 生物種 |  Coxsackievirus A6 (コクサッキーウイルス) Coxsackievirus A6 (コクサッキーウイルス) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.68 Å | |||||||||
 データ登録者 データ登録者 | Buttner CR / Plevka P | |||||||||
| 資金援助 |  チェコ, 2件 チェコ, 2件
| |||||||||
 引用 引用 |  ジャーナル: Commun Biol / 年: 2022 ジャーナル: Commun Biol / 年: 2022タイトル: Cryo-electron microscopy and image classification reveal the existence and structure of the coxsackievirus A6 virion. 著者: Carina R Büttner / Radovan Spurný / Tibor Füzik / Pavel Plevka /  要旨: Coxsackievirus A6 (CV-A6) has recently overtaken enterovirus A71 and CV-A16 as the primary causative agent of hand, foot, and mouth disease worldwide. Virions of CV-A6 were not identified in previous ...Coxsackievirus A6 (CV-A6) has recently overtaken enterovirus A71 and CV-A16 as the primary causative agent of hand, foot, and mouth disease worldwide. Virions of CV-A6 were not identified in previous structural studies, and it was speculated that the virus is unique among enteroviruses in using altered particles with expanded capsids to infect cells. In contrast, the virions of other enteroviruses are required for infection. Here we used cryo-electron microscopy (cryo-EM) to determine the structures of the CV-A6 virion, altered particle, and empty capsid. We show that the CV-A6 virion has features characteristic of virions of other enteroviruses, including a compact capsid, VP4 attached to the inner capsid surface, and fatty acid-like molecules occupying the hydrophobic pockets in VP1 subunits. Furthermore, we found that in a purified sample of CV-A6, the ratio of infectious units to virions is 1 to 500. Therefore, it is likely that virions of CV-A6 initiate infection, like those of other enteroviruses. Our results provide evidence that future vaccines against CV-A6 should target its virions instead of the antigenically distinct altered particles. Furthermore, the structure of the virion provides the basis for the rational development of capsid-binding inhibitors that block the genome release of CV-A6. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_14186.map.gz emd_14186.map.gz | 89.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-14186-v30.xml emd-14186-v30.xml emd-14186.xml emd-14186.xml | 29.5 KB 29.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_14186_fsc.xml emd_14186_fsc.xml | 18 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_14186.png emd_14186.png | 309 KB | ||
| Filedesc metadata |  emd-14186.cif.gz emd-14186.cif.gz | 7.3 KB | ||
| その他 |  emd_14186_additional_1.map.gz emd_14186_additional_1.map.gz emd_14186_additional_2.map.gz emd_14186_additional_2.map.gz emd_14186_half_map_1.map.gz emd_14186_half_map_1.map.gz emd_14186_half_map_2.map.gz emd_14186_half_map_2.map.gz | 95.9 MB 2.9 MB 413.9 MB 414.8 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-14186 http://ftp.pdbj.org/pub/emdb/structures/EMD-14186 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-14186 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-14186 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_14186_validation.pdf.gz emd_14186_validation.pdf.gz | 1.2 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_14186_full_validation.pdf.gz emd_14186_full_validation.pdf.gz | 1.2 MB | 表示 | |
| XML形式データ |  emd_14186_validation.xml.gz emd_14186_validation.xml.gz | 26 KB | 表示 | |
| CIF形式データ |  emd_14186_validation.cif.gz emd_14186_validation.cif.gz | 33.8 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-14186 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-14186 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-14186 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-14186 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_14186.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_14186.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Locally sharpened map (in LocalDeblur) of CV-A6 virion | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.063 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-追加マップ: Unsharpened map of CV-A6 virion at 3.7 A resolution
| ファイル | emd_14186_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Unsharpened map of CV-A6 virion at 3.7 A resolution | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: Mask used for calculation of the FSC curve by RELION postprocessing
| ファイル | emd_14186_additional_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Mask used for calculation of the FSC curve by RELION postprocessing | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Ewald sphere corrected half map 2 used in RELION postprocessing
| ファイル | emd_14186_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Ewald sphere corrected half map 2 used in RELION postprocessing | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Ewald sphere corrected half map 1 used in RELION postprocessing
| ファイル | emd_14186_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Ewald sphere corrected half map 1 used in RELION postprocessing | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Coxsackievirus A6
| 全体 | 名称:  Coxsackievirus A6 (コクサッキーウイルス) Coxsackievirus A6 (コクサッキーウイルス) |
|---|---|
| 要素 |
|
-超分子 #1: Coxsackievirus A6
| 超分子 | 名称: Coxsackievirus A6 / タイプ: virus / ID: 1 / 親要素: 0 / 含まれる分子: #1-#4 / NCBI-ID: 86107 / 生物種: Coxsackievirus A6 / Sci species strain: Gdula / ウイルスタイプ: VIRION / ウイルス・単離状態: STRAIN / ウイルス・エンベロープ: No / ウイルス・中空状態: No |
|---|---|
| 宿主 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 8 MDa |
| ウイルス殻 | Shell ID: 1 / 名称: CV-A6 / 直径: 322.0 Å / T番号(三角分割数): 3 |
-超分子 #2: Capsid
| 超分子 | 名称: Capsid / タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1-#4 / 詳細: native CV-A6 virion |
|---|---|
| 由来(天然) | 生物種:  Coxsackievirus A6 (コクサッキーウイルス) Coxsackievirus A6 (コクサッキーウイルス)株: Gdula |
-分子 #1: Capsid protein VP1
| 分子 | 名称: Capsid protein VP1 / タイプ: protein_or_peptide / ID: 1 詳細: The first amino-acid of VP1 in the corresponding section of the GenBank polyprotein entry (AAR38844) (Asn) is not the actual first residue as the proteolytic cleavage of the viral polyprotein ...詳細: The first amino-acid of VP1 in the corresponding section of the GenBank polyprotein entry (AAR38844) (Asn) is not the actual first residue as the proteolytic cleavage of the viral polyprotein occurs at an alternative location, leaving the following residue Asp-2 as the first residue (D-1), and the Asn as the additional C-term residue described for VP3 (N-241). Residues 301-303 are not modelled/visible in the virion structure but the very C-terminal residue F-304 (partially) is. コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Coxsackievirus A6 (コクサッキーウイルス) Coxsackievirus A6 (コクサッキーウイルス) |
| 分子量 | 理論値: 33.530293 KDa |
| 配列 | 文字列: DPISNAIENA VSTLADTTIS RVTAANTAAS SHSLGTGRVP ALQAAETGAS SNASDENLIE TRCVMNRNGV NEASVEHFYS RAGLVGVVE VKDSGTSQDG YTVWPIDVMG FVQQRRKLEL STYMRFDAEF TFVSNLNDST TPGMLLQYMY VPPGAPKPDG R KSYQWQTA ...文字列: DPISNAIENA VSTLADTTIS RVTAANTAAS SHSLGTGRVP ALQAAETGAS SNASDENLIE TRCVMNRNGV NEASVEHFYS RAGLVGVVE VKDSGTSQDG YTVWPIDVMG FVQQRRKLEL STYMRFDAEF TFVSNLNDST TPGMLLQYMY VPPGAPKPDG R KSYQWQTA TNPSIFAKLS DPPPQVSVPF MSPASAYQWF YDGYPTFGEH KQATNLQYGQ CPNNMMGHFA IRTVSESTTG KN VHVRVYM RIKHVRAWVP RPFRSQAYMV KNYPTYSQTI SNTAADRASI TTTDYEGGVP ANPQRTF UniProtKB: Genome polyprotein |
-分子 #2: Capsid protein VP2
| 分子 | 名称: Capsid protein VP2 / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Coxsackievirus A6 (コクサッキーウイルス) Coxsackievirus A6 (コクサッキーウイルス) |
| 分子量 | 理論値: 28.006529 KDa |
| 配列 | 文字列: SPSVEACGYS DRVAQLTVGN STITTQEAAN IVLSYGEWPG YCPSTDATAV DKPTRPDVSV NRFYTLSTKS WKTESTGWYW KFPDVLNDT GVFGQNAQFH YLYRSGFCMH VQCNASKFHQ GALLVVVIPE FVVAASSPAT KPNGQGLYPD FAHTNPGKEG Q VFRDPYVL ...文字列: SPSVEACGYS DRVAQLTVGN STITTQEAAN IVLSYGEWPG YCPSTDATAV DKPTRPDVSV NRFYTLSTKS WKTESTGWYW KFPDVLNDT GVFGQNAQFH YLYRSGFCMH VQCNASKFHQ GALLVVVIPE FVVAASSPAT KPNGQGLYPD FAHTNPGKEG Q VFRDPYVL DAGIPLSQAL VFPHQWINLR TNNCATIIMP YVNALPFDSA LNHSNFGLAV IPISPLKYCN GATTEVPITL TI APLNSEF SGLRQAIKQ UniProtKB: Genome polyprotein |
-分子 #3: Capsid protein VP3
| 分子 | 名称: Capsid protein VP3 / タイプ: protein_or_peptide / ID: 3 詳細: VP3 has an additional C-terminal residue (N-241) compared to GenBank entry AAR38844 due to alternative cleavage of the polyprotein (see compound details for molecule 1 VP1). コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Coxsackievirus A6 (コクサッキーウイルス) Coxsackievirus A6 (コクサッキーウイルス) |
| 分子量 | 理論値: 26.489936 KDa |
| 配列 | 文字列: GLPTELKPGT NQFLTTDDGT SPPILPGFEP TPLIHIPGEF TSLLDLCRIE TILEVNNTTG TTGVNRLLIP VRAQNNVDQL CASFQVDPG RNGPWQSTMV GQICRYYTQW SGSLKVTFMF TGSFMATGKM LIAYTPPGSA QPTTREAAML GTHIVWDFGL Q SSVTLVIP ...文字列: GLPTELKPGT NQFLTTDDGT SPPILPGFEP TPLIHIPGEF TSLLDLCRIE TILEVNNTTG TTGVNRLLIP VRAQNNVDQL CASFQVDPG RNGPWQSTMV GQICRYYTQW SGSLKVTFMF TGSFMATGKM LIAYTPPGSA QPTTREAAML GTHIVWDFGL Q SSVTLVIP WISNTHFRAV KTGGVYDYYA TGIVTIWYQT NFVVPPDTPS EANIIALGAA QENFTLKLCK DTDEIRQTAE YQ N UniProtKB: Genome polyprotein |
-分子 #4: Capsid protein VP4
| 分子 | 名称: Capsid protein VP4 / タイプ: protein_or_peptide / ID: 4 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Coxsackievirus A6 (コクサッキーウイルス) Coxsackievirus A6 (コクサッキーウイルス) |
| 分子量 | 理論値: 7.231774 KDa |
| 配列 | 文字列: GAQVSAQKSG THETGNIATE GSTINFTNIN YYKDSYAASA SRQDFTQDPT KFTSPVLDAI KEAAAPLQ UniProtKB: Genome polyprotein |
-分子 #5: STEARIC ACID
| 分子 | 名称: STEARIC ACID / タイプ: ligand / ID: 5 / コピー数: 1 / 式: STE |
|---|---|
| 分子量 | 理論値: 284.477 Da |
| Chemical component information |  ChemComp-STE: |
-分子 #6: MYRISTIC ACID
| 分子 | 名称: MYRISTIC ACID / タイプ: ligand / ID: 6 / コピー数: 1 / 式: MYR |
|---|---|
| 分子量 | 理論値: 228.371 Da |
| Chemical component information | 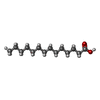 ChemComp-MYR: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 2.5 mg/mL | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.4 構成要素:
詳細: PBS, pH 7.4 | |||||||||||||||
| グリッド | モデル: Quantifoil R2/1 / 材質: COPPER / メッシュ: 300 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY / 支持フィルム - Film thickness: 12 / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 10 sec. | |||||||||||||||
| 凍結 | 凍結剤: ETHANE-PROPANE / チャンバー内湿度: 100 % / チャンバー内温度: 283.15 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: FEI FALCON II (4k x 4k) 検出モード: INTEGRATING / デジタル化 - サイズ - 横: 4096 pixel / デジタル化 - サイズ - 縦: 4096 pixel / 撮影したグリッド数: 1 / 実像数: 9862 / 平均露光時間: 1.0 sec. / 平均電子線量: 45.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 70.0 µm / 最大 デフォーカス(補正後): 3.2 µm / 最小 デフォーカス(補正後): 0.62 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 3.0 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 75000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | PDB ID: Chain - Source name: PDB / Chain - Initial model type: experimental model |
|---|---|
| 詳細 | iterative cycles of building - real space refinement - reciprocal space refinement |
| 精密化 | 空間: RECIPROCAL / プロトコル: RIGID BODY FIT / 温度因子: 66 / 当てはまり具合の基準: correlation coefficient |
| 得られたモデル |  PDB-7qw9: |
 ムービー
ムービー コントローラー
コントローラー










 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)






















































