+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-1176 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of epsilon15 bacteriophage reveals genome organization and DNA packaging/injection apparatus. | |||||||||
 マップデータ マップデータ | 3-fold view of icosahedral symmetry imposed capsid shell map | |||||||||
 試料 試料 |
| |||||||||
| 生物種 |   Salmonella phage epsilon15 (ファージ) Salmonella phage epsilon15 (ファージ) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 9.5 Å | |||||||||
 データ登録者 データ登録者 | Jiang W / Chang J / Jakana J / Weigele P / King J / Chiu W | |||||||||
 引用 引用 |  ジャーナル: Nature / 年: 2006 ジャーナル: Nature / 年: 2006タイトル: Structure of epsilon15 bacteriophage reveals genome organization and DNA packaging/injection apparatus. 著者: Wen Jiang / Juan Chang / Joanita Jakana / Peter Weigele / Jonathan King / Wah Chiu /  要旨: The critical viral components for packaging DNA, recognizing and binding to host cells, and injecting the condensed DNA into the host are organized at a single vertex of many icosahedral viruses. ...The critical viral components for packaging DNA, recognizing and binding to host cells, and injecting the condensed DNA into the host are organized at a single vertex of many icosahedral viruses. These component structures do not share icosahedral symmetry and cannot be resolved using a conventional icosahedral averaging method. Here we report the structure of the entire infectious Salmonella bacteriophage epsilon15 (ref. 1) determined from single-particle cryo-electron microscopy, without icosahedral averaging. This structure displays not only the icosahedral shell of 60 hexamers and 11 pentamers, but also the non-icosahedral components at one pentameric vertex. The densities at this vertex can be identified as the 12-subunit portal complex sandwiched between an internal cylindrical core and an external tail hub connecting to six projecting trimeric tailspikes. The viral genome is packed as coaxial coils in at least three outer layers with approximately 90 terminal nucleotides extending through the protein core and the portal complex and poised for injection. The shell protein from icosahedral reconstruction at higher resolution exhibits a similar fold to that of other double-stranded DNA viruses including herpesvirus, suggesting a common ancestor among these diverse viruses. The image reconstruction approach should be applicable to studying other biological nanomachines with components of mixed symmetries. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_1176.map.gz emd_1176.map.gz | 151.1 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-1176-v30.xml emd-1176-v30.xml emd-1176.xml emd-1176.xml | 9 KB 9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  1176.gif 1176.gif | 51.5 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-1176 http://ftp.pdbj.org/pub/emdb/structures/EMD-1176 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-1176 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-1176 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_1176_validation.pdf.gz emd_1176_validation.pdf.gz | 265.7 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_1176_full_validation.pdf.gz emd_1176_full_validation.pdf.gz | 264.8 KB | 表示 | |
| XML形式データ |  emd_1176_validation.xml.gz emd_1176_validation.xml.gz | 4.8 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1176 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1176 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1176 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1176 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_1176.map.gz / 形式: CCP4 / 大きさ: 202.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_1176.map.gz / 形式: CCP4 / 大きさ: 202.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | 3-fold view of icosahedral symmetry imposed capsid shell map | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 これらの図は立方格子座標系で作成されたものです | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.59 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
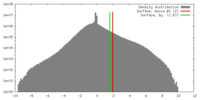
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Bacteriophage Epsilon15
| 全体 | 名称: Bacteriophage Epsilon15 |
|---|---|
| 要素 |
|
-超分子 #1000: Bacteriophage Epsilon15
| 超分子 | 名称: Bacteriophage Epsilon15 / タイプ: sample / ID: 1000 / 詳細: icosahedral shell structure / 集合状態: icosahedral / Number unique components: 1 |
|---|---|
| 分子量 | 理論値: 500 KDa |
-超分子 #1: Salmonella phage epsilon15
| 超分子 | 名称: Salmonella phage epsilon15 / タイプ: virus / ID: 1 / NCBI-ID: 215158 / 生物種: Salmonella phage epsilon15 / ウイルスタイプ: VIRION / ウイルス・単離状態: STRAIN / ウイルス・エンベロープ: No / ウイルス・中空状態: No |
|---|---|
| 宿主 | 生物種:  Salmonella (サルモネラ菌) / 別称: BACTERIA(EUBACTERIA) Salmonella (サルモネラ菌) / 別称: BACTERIA(EUBACTERIA) |
| ウイルス殻 | Shell ID: 1 / 名称: shell / 直径: 700 Å / T番号(三角分割数): 7 |
| ウイルス殻 | Shell ID: 2 / 名称: shell / 直径: 700 Å / T番号(三角分割数): 7 |
| ウイルス殻 | Shell ID: 3 / 名称: shell / 直径: 700 Å / T番号(三角分割数): 7 |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 / 詳細: 10 mM Tris pH7.5, 25 mM NaCl and 5 mM MgCl2 |
|---|---|
| グリッド | 詳細: Quantifoil R2/2 grid |
| 凍結 | 凍結剤: ETHANE / 装置: OTHER / 詳細: Vitrification instrument: Vitrobot |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | JEOL 3000SFF |
|---|---|
| 温度 | 平均: 4.2 K |
| 日付 | 2004年10月10日 |
| 撮影 | カテゴリ: FILM / フィルム・検出器のモデル: KODAK SO-163 FILM / デジタル化 - スキャナー: OTHER / デジタル化 - サンプリング間隔: 6.35 µm / 実像数: 200 / 平均電子線量: 25 e/Å2 / 詳細: Scanned by Nikon CoolScan 9000ED / ビット/ピクセル: 14 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 1.6 mm / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 0.5 µm / 倍率(公称値): 60000 |
| 試料ステージ | 試料ホルダー: Topentry / 試料ホルダーモデル: OTHER |
- 画像解析
画像解析
| CTF補正 | 詳細: per particle |
|---|---|
| 最終 再構成 | 想定した対称性 - 点群: I (正20面体型対称) / アルゴリズム: OTHER / 解像度のタイプ: BY AUTHOR / 解像度: 9.5 Å / 解像度の算出法: FSC 0.5 CUT-OFF / ソフトウェア - 名称: SAVR / 使用した粒子像数: 6000 |
 ムービー
ムービー コントローラー
コントローラー









 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)