+検索条件
-Structure paper
| タイトル | Structures of Coxsackievirus A10 unveil the molecular mechanisms of receptor binding and viral uncoating. |
|---|---|
| ジャーナル・号・ページ | Nat Commun, Vol. 9, Issue 1, Page 4985, Year 2018 |
| 掲載日 | 2018年11月26日 |
 著者 著者 | Ling Zhu / Yao Sun / Jinyan Fan / Bin Zhu / Lei Cao / Qiang Gao / Yanjun Zhang / Hongrong Liu / Zihe Rao / Xiangxi Wang /  |
| PubMed 要旨 | Coxsackievirus A10 (CVA10), a human type-A Enterovirus (HEV-A), can cause diseases ranging from hand-foot-and-mouth disease to polio-myelitis-like disease. CVA10, together with some other HEV-As, ...Coxsackievirus A10 (CVA10), a human type-A Enterovirus (HEV-A), can cause diseases ranging from hand-foot-and-mouth disease to polio-myelitis-like disease. CVA10, together with some other HEV-As, utilizing the molecule KREMEN1 as an entry receptor, constitutes a KREMEN1-dependent subgroup within HEV-As. Currently, there is no vaccine or antiviral therapy available for treating diseases caused by CVA10. The atomic-resolution structure of the CVA10 virion, which is within the KREMEN1-dependent subgroup, shows significant conformational differences in the putative receptor binding sites and serotype-specific epitopes, when compared to the SCARB2-dependent subgroup of HEV-A, such as EV71, highlighting specific differences between the sub-groups. We also report two expanded structures of CVA10, an empty particle and uncoating intermediate at atomic resolution, as well as a medium-resolution genome structure reconstructed using a symmetry-mismatch method. Structural comparisons coupled with previous results, reveal an ordered signal transmission process for enterovirus uncoating, converting exo-genetic receptor-attachment inputs into a generic RNA release mechanism. |
 リンク リンク |  Nat Commun / Nat Commun /  PubMed:30478256 / PubMed:30478256 /  PubMed Central PubMed Central |
| 手法 | EM (単粒子) |
| 解像度 | 2.7 - 12.0 Å |
| 構造データ |  EMDB-9652: |
| 化合物 | 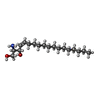 ChemComp-SPH: |
| 由来 |
|
 キーワード キーワード | VIRUS / picornavirus uncoating / receptor binding |
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア 万見文献について
万見文献について










 coxsackievirus a10 (コクサッキーウイルス)
coxsackievirus a10 (コクサッキーウイルス)