+検索条件
-Structure paper
| タイトル | Structural basis for channel gating and blockade in tri-heteromeric GluN1-2B-2D NMDA receptor. |
|---|---|
| ジャーナル・号・ページ | Neuron, Vol. 113, Issue 7, Page 991-1005.e5, Year 2025 |
| 掲載日 | 2025年4月2日 |
 著者 著者 | Hyunook Kang / Max Epstein / Tue G Banke / Riley Perszyk / Noriko Simorowski / Srinu Paladugu / Dennis C Liotta / Stephen F Traynelis / Hiro Furukawa /  |
| PubMed 要旨 | Discrete activation of N-methyl-D-aspartate receptor (NMDAR) subtypes by glutamate and the co-agonist glycine is fundamental to neuroplasticity. A distinct variant, the tri-heteromeric receptor, ...Discrete activation of N-methyl-D-aspartate receptor (NMDAR) subtypes by glutamate and the co-agonist glycine is fundamental to neuroplasticity. A distinct variant, the tri-heteromeric receptor, comprising glycine-binding GluN1 and two types of glutamate-binding GluN2 subunits, exhibits unique pharmacological characteristics, notably enhanced sensitivity to the anti-depressant channel blocker S-(+)-ketamine. Despite its significance, the structural mechanisms underlying ligand gating and channel blockade of tri-heteromeric NMDARs remain poorly understood. Here, we identify and characterize tri-heteromeric GluN1-2B-2D NMDAR in the adult brain, resolving its structures in the activated, inhibited, and S-(+)-ketamine-blocked states. These structures reveal the ligand-dependent conformational dynamics that modulate the tension between the extracellular domain and transmembrane channels, governing channel gating and blockade. Additionally, we demonstrate that the inhibitor (S)-DQP-997-74 selectively decouples linker tension in GluN2D, offering insights into subtype-selective targeting for cognitive modulation. |
 リンク リンク |  Neuron / Neuron /  PubMed:39954679 / PubMed:39954679 /  PubMed Central PubMed Central |
| 手法 | EM (単粒子) |
| 解像度 | 3.28 - 6.07 Å |
| 構造データ |  EMDB-46509: Consensus map of open state GluN1a-2B-2D NMDAR  EMDB-46510: TMD local refined map of open state GluN1a-2B-2D NMDAR  EMDB-46513: Consensus map of Gly-,PPDA bound GluN1a-2B-2D NMDAR  EMDB-46514: ECD local refined map of Gly-,PPDA bound GluN1a-2B-2D NMDAR  EMDB-46516: Consensus map of nonactive state GluN1a-2B-2D NMDAR  EMDB-46517: TMD local refined map of non-active state GluN1a-2B-2D NMDAR  EMDB-46518: ECD local refined map of nonactive state GluN1a-2B-2D NMDAR  EMDB-46519: Consensus map of Gly-,Glu-,(S)-DQP-997-74 bound GluN1a-2B-2D NMDAR  EMDB-46520: TMD local refined map of Gly-,Glu-,(S)-DQP-997-74 bound NMDAR  EMDB-46521: ECD local refined map of Gly-,Glu-,(S)-DQP-997-74 bound NMDAR  EMDB-46522: Consensus map of Gly-,Glu-,(S)-(+)-ketamine bound GluN1a-2B-2D NMDAR  EMDB-46523: TMD local refined map of Gly-,Glu-,(S)-(+)-ketamine bound GluN1a-2B-2D NMDAR  EMDB-46524: ECD local refined map of Gly-,Glu-,(S)-(+)-ketamine bound GluN1a-2B-2D NMDAR EMDB-46526, PDB-9d37: EMDB-46527, PDB-9d38: EMDB-46528, PDB-9d39: EMDB-46529, PDB-9d3a: EMDB-46530, PDB-9d3b: EMDB-46531, PDB-9d3c: |
| 化合物 | 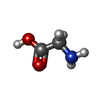 ChemComp-GLY:  ChemComp-NAG:  ChemComp-GLU:  ChemComp-HOH: 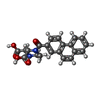 ChemComp-2JL:  PDB-1a15: 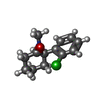 ChemComp-JC9: |
| 由来 |
|
 キーワード キーワード | MEMBRANE PROTEIN / N-methyl-D-aspartate receptor / nonactive / GluN2B / GluN2D / open / NMDAR / PPDA-bound / (S)-DQP-997-74 / (S)-(+)-ketamine |
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア 万見文献について
万見文献について















 homo sapiens (ヒト)
homo sapiens (ヒト)