-検索条件
-検索結果
検索 (著者・登録者: liu & hr)の結果699件中、1から50件目までを表示しています

EMDB-36730: 
SARS-CoV-2 Spike RBD (dimer) in complex with two 2S-1244 nanobodies

EMDB-36735: 
Dimer of SARS-CoV-2 BA.2 spike and IBT-CoV144(C3 symmetry)

EMDB-36740: 
Dimer of SARS-CoV-2 BA.2 spike and IBT-CoV144(C1 symmetry)

EMDB-17296: 
Stabilised BA.1 SARS-CoV-2 spike with H6 nanobodies in '2 up 1 down' RBD conformation

PDB-8oyu: 
Stabilised BA.1 SARS-CoV-2 spike with H6 nanobodies in '2 up 1 down' RBD conformation
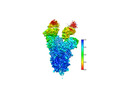
EMDB-37240: 
SARS-CoV-2 Omicron spike in complex with 5817 Fab

EMDB-37241: 
The interface structure of Omicron RBD binding to 5817 Fab

PDB-8khc: 
SARS-CoV-2 Omicron spike in complex with 5817 Fab

PDB-8khd: 
The interface structure of Omicron RBD binding to 5817 Fab

EMDB-17704: 
Subtomogram average of Vaccinia A10 trimer with open center from in vitro cores

EMDB-17708: 
Subtomogram average of Vaccinia A10 trimer with tight center from in vitro cores

EMDB-17753: 
Subtomogram average of Vaccinia A10 trimer from in situ cores

EMDB-41048: 
Lassa GPC Trimer in complex with Fab 8.11G and nanobody D5

PDB-8t5c: 
Lassa GPC Trimer in complex with Fab 8.11G and nanobody D5

EMDB-36844: 
Structure of the bacteriophage lambda tail tip complex

EMDB-36845: 
Structure of the bacteriophage lambda tail tube

EMDB-36846: 
Structure of the bacteriophage lambda neck

EMDB-36847: 
The structure of bacteriophage lambda portal-adaptor

EMDB-36848: 
Structure of the bacteriophage lambda portal vertex

EMDB-29281: 
Cryo-EM structure of STING oligomer bound to cGAMP and NVS-STG2

EMDB-29282: 
Cryo-EM structure of STING oligomer bound to cGAMP, NVS-STG2 and C53

PDB-8flk: 
Cryo-EM structure of STING oligomer bound to cGAMP and NVS-STG2

PDB-8flm: 
Cryo-EM structure of STING oligomer bound to cGAMP, NVS-STG2 and C53

EMDB-29645: 
Cryo-EM structure of an orphan GPCR-Gi protein signaling complex

PDB-8g05: 
Cryo-EM structure of an orphan GPCR-Gi protein signaling complex

EMDB-35257: 
Structure of EP54-C3aR-Go complex

EMDB-35259: 
Structure of Apo-C3aR-Go complex (Glacios)

EMDB-35263: 
Structure of EP54-C3aR-Gq complex

EMDB-35275: 
Structure of C3a-C3aR-Go complex (Composite map)

EMDB-35282: 
Structure of Apo-C3aR-Go complex (Titan)

EMDB-35292: 
Structure of C5a bound human C5aR1 in complex with Go (Composite map)

EMDB-35293: 
C3a-C3aR-Go (C3aR-Go complex only, Original Map)

EMDB-35294: 
C3a-C3aR-Go (C3a only, Original Map)

EMDB-35295: 
C5a-hC5aR1-Go (hC5aR1-Go complex only, Original map)
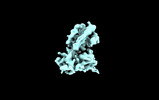
EMDB-35296: 
C5a-hC5aR1-Go complex (C5a only, Original map)

EMDB-36001: 
Structure of EP141-C3aR-Go complex

EMDB-36755: 
Structure of human C5a-desArg bound human C5aR1 in complex with Go

PDB-8i95: 
Structure of EP54-C3aR-Go complex

PDB-8i97: 
Structure of Apo-C3aR-Go complex (Glacios)

PDB-8i9a: 
Structure of EP54-C3aR-Gq complex

PDB-8i9l: 
Structure of C3a-C3aR-Go complex (Composite map)

PDB-8i9s: 
Structure of Apo-C3aR-Go complex (Titan)

PDB-8ia2: 
Structure of C5a bound human C5aR1 in complex with Go (Composite map)

PDB-8j6d: 
Structure of EP141-C3aR-Go complex

PDB-8jzz: 
Structure of human C5a-desArg bound human C5aR1 in complex with Go

EMDB-26583: 
Cryo-EM structure of Antibody 12-16 in complex with prefusion SARS-CoV-2 Spike glycoprotein

PDB-7ukl: 
Cryo-EM structure of Antibody 12-16 in complex with prefusion SARS-CoV-2 Spike glycoprotein

EMDB-28115: 
Western Equine Encephalitis Virus-Like Particle in Complex with SKW19 Fab

EMDB-28116: 
Western Equine Encephalitis Virus-Like Particle in Complex with SKW24 Fab

EMDB-28117: 
Eastern Equine Encephalitis Virus-Like Particle in Complex with SKE26 Fab
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
