+ Open data
Open data
- Basic information
Basic information
| Entry | Database: EMDB / ID: EMD-23272 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| Title | The mature Usutu SAAR-1776, Map A | |||||||||
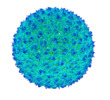
 Map data Map data | Usutu Map A | |||||||||
 Sample Sample |
| |||||||||
 Keywords Keywords | Flavivirus / envelope glycoprotein / VIRUS | |||||||||
| Function / homology |  Function and homology information Function and homology informationsymbiont-mediated suppression of host JAK-STAT cascade via inhibition of STAT2 activity / viral capsid / ribonucleoside triphosphate phosphatase activity / double-stranded RNA binding / methyltransferase cap1 activity / mRNA 5'-cap (guanine-N7-)-methyltransferase activity / RNA helicase activity / protein dimerization activity / symbiont-mediated suppression of host innate immune response / host cell perinuclear region of cytoplasm ...symbiont-mediated suppression of host JAK-STAT cascade via inhibition of STAT2 activity / viral capsid / ribonucleoside triphosphate phosphatase activity / double-stranded RNA binding / methyltransferase cap1 activity / mRNA 5'-cap (guanine-N7-)-methyltransferase activity / RNA helicase activity / protein dimerization activity / symbiont-mediated suppression of host innate immune response / host cell perinuclear region of cytoplasm / host cell endoplasmic reticulum membrane / symbiont-mediated suppression of host type I interferon-mediated signaling pathway / serine-type endopeptidase activity / viral RNA genome replication / RNA-directed RNA polymerase activity / fusion of virus membrane with host endosome membrane / symbiont entry into host cell / virion attachment to host cell / host cell nucleus / virion membrane / structural molecule activity / proteolysis / extracellular region / ATP binding / metal ion binding Similarity search - Function | |||||||||
| Biological species |  Usutu virus Usutu virus | |||||||||
| Method | single particle reconstruction / cryo EM / Resolution: 2.42 Å | |||||||||
 Authors Authors | Khare B / Klose T | |||||||||
| Funding support |  United States, 2 items United States, 2 items
| |||||||||
 Citation Citation |  Journal: Proc Natl Acad Sci U S A / Year: 2021 Journal: Proc Natl Acad Sci U S A / Year: 2021Title: Structure of Usutu virus SAAR-1776 displays fusion loop asymmetry. Authors: Baldeep Khare / Thomas Klose / Qianglin Fang / Michael G Rossmann / Richard J Kuhn /  Abstract: Usutu virus (USUV) is an emerging arbovirus in Europe that has been increasingly identified in asymptomatic humans and donated blood samples and is a cause of increased incidents of neuroinvasive ...Usutu virus (USUV) is an emerging arbovirus in Europe that has been increasingly identified in asymptomatic humans and donated blood samples and is a cause of increased incidents of neuroinvasive human disease. Treatment or prevention options for USUV disease are currently nonexistent, the result of a lack of understanding of the fundamental elements of USUV pathogenesis. Here, we report two structures of the mature USUV virus, determined at a resolution of 2.4 Å, using single-particle cryogenic electron microscopy. Mature USUV is an icosahedral shell of 180 copies of envelope (E) and membrane (M) proteins arranged in the classic herringbone pattern. However, unlike previous reports of flavivirus structures, we observe virus subpopulations and differences in the fusion loop disulfide bond. Presence of a second, unique E glycosylation site could elucidate host interactions, contributing to the broad USUV tissue tropism. The structures provide a basis for exploring USUV interactions with glycosaminoglycans and lectins, the role of the RGD motif as a receptor, and the inability of West Nile virus therapeutic antibody E16 to neutralize the mature USUV strain SAAR-1776. Finally, we identify three lipid binding sites and predict key residues that likely participate in virus stability and flexibility during membrane fusion. Our findings provide a framework for the development of USUV therapeutics and expand the current knowledge base of flavivirus biology. | |||||||||
| History |
|
- Structure visualization
Structure visualization
| Movie |
 Movie viewer Movie viewer |
|---|---|
| Structure viewer | EM map:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| Supplemental images |
- Downloads & links
Downloads & links
-EMDB archive
| Map data |  emd_23272.map.gz emd_23272.map.gz | 350.2 MB |  EMDB map data format EMDB map data format | |
|---|---|---|---|---|
| Header (meta data) |  emd-23272-v30.xml emd-23272-v30.xml emd-23272.xml emd-23272.xml | 16.8 KB 16.8 KB | Display Display |  EMDB header EMDB header |
| Images |  emd_23272.png emd_23272.png | 250.2 KB | ||
| Filedesc metadata |  emd-23272.cif.gz emd-23272.cif.gz | 6.6 KB | ||
| Archive directory |  http://ftp.pdbj.org/pub/emdb/structures/EMD-23272 http://ftp.pdbj.org/pub/emdb/structures/EMD-23272 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-23272 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-23272 | HTTPS FTP |
-Related structure data
| Related structure data |  7lcgMC  7lchC C: citing same article ( M: atomic model generated by this map |
|---|---|
| Similar structure data |
- Links
Links
| EMDB pages |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| Related items in Molecule of the Month |
- Map
Map
| File |  Download / File: emd_23272.map.gz / Format: CCP4 / Size: 1.9 GB / Type: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) Download / File: emd_23272.map.gz / Format: CCP4 / Size: 1.9 GB / Type: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Annotation | Usutu Map A | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Projections & slices | Image control
Images are generated by Spider. | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Voxel size | X=Y=Z: 0.664 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Density |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Symmetry | Space group: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Details | EMDB XML:
CCP4 map header:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-Supplemental data
- Sample components
Sample components
-Entire : Usutu virus
| Entire | Name:  Usutu virus Usutu virus |
|---|---|
| Components |
|
-Supramolecule #1: Usutu virus
| Supramolecule | Name: Usutu virus / type: virus / ID: 1 / Parent: 0 / Macromolecule list: #1-#2 / Details: Virus purified using Vero cells. / NCBI-ID: 64286 / Sci species name: Usutu virus / Sci species strain: SAAR-1776 / Virus type: VIRION / Virus isolate: STRAIN / Virus enveloped: Yes / Virus empty: No |
|---|---|
| Host (natural) | Organism:  Turdus merula (blackbird) Turdus merula (blackbird) |
-Macromolecule #1: Envelope protein E
| Macromolecule | Name: Envelope protein E / type: protein_or_peptide / ID: 1 / Number of copies: 3 / Enantiomer: LEVO |
|---|---|
| Source (natural) | Organism:  Usutu virus / Strain: SAAR-1776 Usutu virus / Strain: SAAR-1776 |
| Molecular weight | Theoretical: 53.623812 KDa |
| Recombinant expression | Organism:  Chlorocebus aethiops (grivet monkey) Chlorocebus aethiops (grivet monkey) |
| Sequence | String: FNCLGMSNRD FLEGVSGATW VDVVLEGDSC ITIMAKDKPT IDIKMMETEA TNLAEVRSYC YLATVSDVST VSNCPTTGEA HNPKRAEDT YVCKSGVTDR GWGNGCGLFG KGSIDTCANF TCSLKAVGRM IQPENVKYEV GIFIHGSTSS DTHGNYSSQL G ASQAGRFT ...String: FNCLGMSNRD FLEGVSGATW VDVVLEGDSC ITIMAKDKPT IDIKMMETEA TNLAEVRSYC YLATVSDVST VSNCPTTGEA HNPKRAEDT YVCKSGVTDR GWGNGCGLFG KGSIDTCANF TCSLKAVGRM IQPENVKYEV GIFIHGSTSS DTHGNYSSQL G ASQAGRFT ITPNSPAITV KMGDYGEISV ECEPRNGLNT EAYYIMSVGT KHFLVHREWF NDLALPWTSP ASSNWRNREI LL EFEEPHA TKQSVVALGS QEGALHQALA GAVPVSFSSS VKLTSGHLKC RVKMEKLTLK GTTYGMCTEK FSFAKNPADT GHS TVVLEL QYTGSDGPCK IPISIVASLS DLTPIGRMVT ANPYVASSEA NAKVLVEMEP PFGDSYIVVG RGDKQINHHW HKAG SSIGK AFITTIKGAQ RLAALGDPAW DFGSVGGIFN SVGKAVHQVF GGAFRTLFGG MSWITQGLMG ALLLWMGVNA RDRSI ALVM LATGGVLLFL ATSVHA UniProtKB: Genome polyprotein |
-Macromolecule #2: Membrane protein M
| Macromolecule | Name: Membrane protein M / type: protein_or_peptide / ID: 2 / Number of copies: 3 / Enantiomer: LEVO |
|---|---|
| Source (natural) | Organism:  Usutu virus / Strain: SAAR-1776 Usutu virus / Strain: SAAR-1776 |
| Molecular weight | Theoretical: 8.33371 KDa |
| Recombinant expression | Organism:  Chlorocebus aethiops (grivet monkey) Chlorocebus aethiops (grivet monkey) |
| Sequence | String: SIAVQTHGES MLANKKDAWL DSTKASRYLM KTENWIIRNP GYAFVAVLLG WMLGSNNGQR VVFVVLLLLV APAYS UniProtKB: Genome polyprotein |
-Macromolecule #3: TRIMETHYL-[2-[[(2S,3S)-2-(OCTADECANOYLAMINO)-3-OXIDANYL-BUTOXY]-O...
| Macromolecule | Name: TRIMETHYL-[2-[[(2S,3S)-2-(OCTADECANOYLAMINO)-3-OXIDANYL-BUTOXY]-OXIDANYL-PHOSPHORYL]OXYETHYL]AZANIUM type: ligand / ID: 3 / Number of copies: 3 / Formula: 0SM |
|---|---|
| Molecular weight | Theoretical: 537.733 Da |
| Chemical component information |  ChemComp-0SM: |
-Macromolecule #4: (7S)-4-HYDROXY-N,N,N-TRIMETHYL-9-OXO-7-[(PALMITOYLOXY)METHYL]-3,5...
| Macromolecule | Name: (7S)-4-HYDROXY-N,N,N-TRIMETHYL-9-OXO-7-[(PALMITOYLOXY)METHYL]-3,5,8-TRIOXA-4-PHOSPHAHEXACOSAN-1-AMINIUM 4-OXIDE type: ligand / ID: 4 / Number of copies: 3 / Formula: PC7 |
|---|---|
| Molecular weight | Theoretical: 763.1 Da |
| Chemical component information |  ChemComp-PC7: |
-Macromolecule #5: 2-acetamido-2-deoxy-beta-D-glucopyranose
| Macromolecule | Name: 2-acetamido-2-deoxy-beta-D-glucopyranose / type: ligand / ID: 5 / Number of copies: 6 / Formula: NAG |
|---|---|
| Molecular weight | Theoretical: 221.208 Da |
| Chemical component information |  ChemComp-NAG: |
-Experimental details
-Structure determination
| Method | cryo EM |
|---|---|
 Processing Processing | single particle reconstruction |
| Aggregation state | particle |
- Sample preparation
Sample preparation
| Buffer | pH: 8 Component:
Details: 20 mM Tris, 120 mM NaCl, 1 mM EDTA, pH 8.0 | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Grid | Model: PELCO Ultrathin Carbon with Lacey Carbon / Material: COPPER | ||||||||||||
| Vitrification | Cryogen name: ETHANE / Instrument: GATAN CRYOPLUNGE 3 |
- Electron microscopy
Electron microscopy
| Microscope | FEI TITAN KRIOS |
|---|---|
| Specialist optics | Energy filter - Name: GIF Bioquantum / Energy filter - Slit width: 20 eV |
| Image recording | Film or detector model: GATAN K3 BIOQUANTUM (6k x 4k) / Detector mode: SUPER-RESOLUTION / Number grids imaged: 1 / Number real images: 3689 / Average exposure time: 2.08 sec. / Average electron dose: 23.68 e/Å2 |
| Electron beam | Acceleration voltage: 300 kV / Electron source:  FIELD EMISSION GUN FIELD EMISSION GUN |
| Electron optics | C2 aperture diameter: 100.0 µm / Illumination mode: FLOOD BEAM / Imaging mode: BRIGHT FIELD / Cs: 2.7 mm / Nominal defocus max: 2.0 µm / Nominal defocus min: 0.8 µm / Nominal magnification: 64000 |
| Sample stage | Specimen holder model: FEI TITAN KRIOS AUTOGRID HOLDER / Cooling holder cryogen: NITROGEN |
| Experimental equipment |  Model: Titan Krios / Image courtesy: FEI Company |
 Movie
Movie Controller
Controller
















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)






















