+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 6s1w | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Crystal structure of dimeric M-PMV protease D26N mutant | ||||||
 要素 要素 | Gag-Pro-Pol polyprotein | ||||||
 キーワード キーワード |  HYDROLASE (加水分解酵素) / HYDROLASE (加水分解酵素) /  Mason-Pfizer Monkey Virus / M-PMV / Mason-Pfizer Monkey Virus / M-PMV /  retrovirus (レトロウイルス科) / retrovirus (レトロウイルス科) /  retropepsin / retropepsin /  aspartic protease (アスパラギン酸プロテアーゼ) / aspartic protease (アスパラギン酸プロテアーゼ) /  dimerization / flap structure / apo dimerization / flap structure / apo | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 dUTP diphosphatase / dUTP diphosphatase /  dUTP diphosphatase activity / dUTP diphosphatase activity /  加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; アスパラギン酸プロテアーゼ / 加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; アスパラギン酸プロテアーゼ /  リボヌクレアーゼH / RNA stem-loop binding / DNA integration / リボヌクレアーゼH / RNA stem-loop binding / DNA integration /  逆転写酵素 / viral genome integration into host DNA / establishment of integrated proviral latency / 逆転写酵素 / viral genome integration into host DNA / establishment of integrated proviral latency /  RNA-directed DNA polymerase activity ... RNA-directed DNA polymerase activity ... dUTP diphosphatase / dUTP diphosphatase /  dUTP diphosphatase activity / dUTP diphosphatase activity /  加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; アスパラギン酸プロテアーゼ / 加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; アスパラギン酸プロテアーゼ /  リボヌクレアーゼH / RNA stem-loop binding / DNA integration / リボヌクレアーゼH / RNA stem-loop binding / DNA integration /  逆転写酵素 / viral genome integration into host DNA / establishment of integrated proviral latency / 逆転写酵素 / viral genome integration into host DNA / establishment of integrated proviral latency /  RNA-directed DNA polymerase activity / RNA-DNA hybrid ribonuclease activity / RNA-directed DNA polymerase activity / RNA-DNA hybrid ribonuclease activity /  転移酵素; リンを含む基を移すもの; 核酸を移すもの / viral nucleocapsid / DNA recombination / structural constituent of virion / 転移酵素; リンを含む基を移すもの; 核酸を移すもの / viral nucleocapsid / DNA recombination / structural constituent of virion /  加水分解酵素; エステル加水分解酵素 / 加水分解酵素; エステル加水分解酵素 /  DNAポリメラーゼ / aspartic-type endopeptidase activity / DNAポリメラーゼ / aspartic-type endopeptidase activity /  DNA-directed DNA polymerase activity / symbiont entry into host cell / DNA-directed DNA polymerase activity / symbiont entry into host cell /  タンパク質分解 / タンパク質分解 /  DNA binding / zinc ion binding DNA binding / zinc ion binding類似検索 - 分子機能 | ||||||
| 生物種 |   Mason-Pfizer monkey virus (ウイルス) Mason-Pfizer monkey virus (ウイルス) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.98 Å 分子置換 / 解像度: 1.98 Å | ||||||
 データ登録者 データ登録者 | Wosicki, S. / Gilski, M. / Jaskolski, M. / Zabranska, H. / Pichova, I. | ||||||
| 資金援助 |  チェコ, 1件 チェコ, 1件
| ||||||
 引用 引用 |  ジャーナル: Acta Crystallogr D Struct Biol / 年: 2019 ジャーナル: Acta Crystallogr D Struct Biol / 年: 2019タイトル: Comparison of a retroviral protease in monomeric and dimeric states. 著者: Wosicki, S. / Gilski, M. / Zabranska, H. / Pichova, I. / Jaskolski, M. #1:  ジャーナル: Nat.Struct.Mol.Biol. / 年: 2011 ジャーナル: Nat.Struct.Mol.Biol. / 年: 2011タイトル: Crystal structure of a monomeric retroviral protease solved by protein folding game players. 著者: Khatib, F. / DiMaio, F. / Cooper, S. / Kazmierczyk, M. / Gilski, M. / Krzywda, S. / Zabranska, H. / Pichova, I. / Thompson, J. / Popovic, Z. / Jaskolski, M. / Baker, D. #2: ジャーナル: Acta Crystallogr.,Sect.D / 年: 2011 タイトル: High-resolution structure of a retroviral protease folded as a monomer. 著者: Gilski, M. / Kazmierczyk, M. / Krzywda, S. / Zabranska, H. / Cooper, S. / Popovic, Z. / Khatib, F. / DiMaio, F. / Thompson, J. / Baker, D. / Pichova, I. / Jaskolski, M. #3: ジャーナル: Nature / 年: 1989 タイトル: Crystal structure of a retroviral protease proves relationship to aspartic protease family. 著者: Miller, M. / Jaskolski, M. / Rao, J.K. / Leis, J. / Wlodawer, A. #4:  ジャーナル: Science / 年: 1989 ジャーナル: Science / 年: 1989タイトル: Conserved folding in retroviral proteases: crystal structure of a synthetic HIV-1 protease. 著者: Wlodawer, A. / Miller, M. / Jaskolski, M. / Sathyanarayana, B.K. / Baldwin, E. / Weber, I.T. / Selk, L.M. / Clawson, L. / Schneider, J. / Kent, S.B. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  6s1w.cif.gz 6s1w.cif.gz | 102.3 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb6s1w.ent.gz pdb6s1w.ent.gz | 78.7 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  6s1w.json.gz 6s1w.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/s1/6s1w https://data.pdbj.org/pub/pdb/validation_reports/s1/6s1w ftp://data.pdbj.org/pub/pdb/validation_reports/s1/6s1w ftp://data.pdbj.org/pub/pdb/validation_reports/s1/6s1w | HTTPS FTP |
|---|
-関連構造データ
| 関連構造データ | 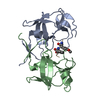 6s1uSC  6s1vC S: 精密化の開始モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| 実験データセット #1 | データ参照:  10.18150/repod.7575322 / データの種類: diffraction image data / Metadata reference: 10.18150/repod.7575322 10.18150/repod.7575322 / データの種類: diffraction image data / Metadata reference: 10.18150/repod.7575322 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||||||||||||
| 単位格子 |
| ||||||||||||||||||
| 非結晶学的対称性 (NCS) | NCSドメイン:
NCSドメイン領域: Component-ID: 0 / Ens-ID: 1 / Beg auth comp-ID: TRP / Beg label comp-ID: TRP / End auth comp-ID: PRO / End label comp-ID: PRO / Refine code: 0 / Auth seq-ID: 1 - 108 / Label seq-ID: 1 - 108
|
- 要素
要素
| #1: タンパク質 | 分子量: 12963.964 Da / 分子数: 2 / 変異: D26N; ENGINEERED MUTATION / 由来タイプ: 組換発現 詳細: Gaps in the sequence indicate residues that were not modeled because of poor electron density. 由来: (組換発現)   Mason-Pfizer monkey virus (ウイルス) Mason-Pfizer monkey virus (ウイルス)遺伝子: gag-pro-pol / プラスミド: pBPS13ATG 発現宿主:   Escherichia coli 'BL21-Gold(DE3)pLysS AG' (大腸菌) Escherichia coli 'BL21-Gold(DE3)pLysS AG' (大腸菌)参照: UniProt: P07572, dUTP diphosphatase, 加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; アスパラギン酸プロテアーゼ, 逆転写酵素, ...参照: UniProt: P07572,  dUTP diphosphatase, dUTP diphosphatase,  加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; アスパラギン酸プロテアーゼ, 加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; アスパラギン酸プロテアーゼ,  逆転写酵素, 逆転写酵素,  DNAポリメラーゼ, DNAポリメラーゼ,  リボヌクレアーゼH, リボヌクレアーゼH,  転移酵素; リンを含む基を移すもの; 核酸を移すもの, 転移酵素; リンを含む基を移すもの; 核酸を移すもの,  加水分解酵素; エステル加水分解酵素 加水分解酵素; エステル加水分解酵素#2: 水 | ChemComp-HOH / |  水 水 |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.37 Å3/Da / 溶媒含有率: 48.17 % / 解説: plate |
|---|---|
結晶化 | 温度: 292 K / 手法: 蒸気拡散法, ハンギングドロップ法 / pH: 5.6 詳細: Protein solution: 4.1 mg/mL protein, 5 mM TCEP, 10 mM Tris buffer pH 7.4; Reservoir solution: 0.1 M sodium citrate buffer, 15% propan-2-ol, 5 mM TCEP; |
-データ収集
| 回折 | 平均測定温度: 100 K / Serial crystal experiment: N |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  BESSY BESSY  / ビームライン: 14.1 / 波長: 0.91841 Å / ビームライン: 14.1 / 波長: 0.91841 Å |
| 検出器 | タイプ: DECTRIS PILATUS 6M / 検出器: PIXEL / 日付: 2013年3月28日 |
| 放射 | モノクロメーター: Double Crystal Monochromator, Si-111 crystal プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長 : 0.91841 Å / 相対比: 1 : 0.91841 Å / 相対比: 1 |
| 反射 | 解像度: 1.98→48.91 Å / Num. obs: 17123 / % possible obs: 98.9 % / 冗長度: 3.62 % / Biso Wilson estimate: 25 Å2 / CC1/2: 0.997 / Rmerge(I) obs: 0.119 / Rrim(I) all: 0.139 / Net I/σ(I): 8.24 |
| 反射 シェル | 解像度: 1.98→2.1 Å / 冗長度: 3.4 % / Rmerge(I) obs: 0.627 / Mean I/σ(I) obs: 2.03 / Num. unique obs: 2594 / CC1/2: 0.521 / Rrim(I) all: 0.737 / % possible all: 94.3 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法 : :  分子置換 分子置換開始モデル: 6S1U, chain A 解像度: 1.98→48.8 Å / Cor.coef. Fo:Fc: 0.955 / Cor.coef. Fo:Fc free: 0.911 / SU B: 13.585 / SU ML: 0.169 / 交差検証法: FREE R-VALUE / ESU R: 0.183 / ESU R Free: 0.178 / 詳細: HYDROGEN ATOMS WERE ADDED AT RIDING POSITIONS
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | イオンプローブ半径: 0.8 Å / 減衰半径: 0.8 Å / VDWプローブ半径: 1.2 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 34.024 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 1.98→48.8 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー





















 PDBj
PDBj


