-検索条件
-検索結果
検索 (著者・登録者: johnson & a)の結果681件中、1から50件目までを表示しています
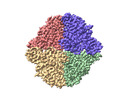
EMDB-42478: 
Trehalose Synthase (TreS) of Mycobacterium tuberculosis in complex with 6-TreAz compound

PDB-8uqv: 
Trehalose Synthase (TreS) of Mycobacterium tuberculosis in complex with 6-TreAz compound

EMDB-40208: 
Backbone model of de novo-designed chlorophyll-binding nanocage O32-15

EMDB-40209: 
Chlorophyll-binding region of de novo-designed nanocage O32-15

EMDB-28957: 
Cryo-EM structure of the Agrobacterium T-pilus

PDB-8fai: 
Cryo-EM structure of the Agrobacterium T-pilus

EMDB-43508: 
Structure of a bacterial gasdermin small oval pore assembly

EMDB-43509: 
Structure of a bacterial gasdermin medium oval pore assembly

EMDB-43510: 
Structure of a bacterial gasdermin large oval pore assembly

EMDB-43511: 
Structure of a bacterial gasdermin double pore assembly

EMDB-43513: 
Structure of a bacterial gasdermin slinky-like oligomer from a heterogeneous sample

EMDB-42139: 
Cryo-EM structure of the flagellar MotAB stator bound to FliG

EMDB-42376: 
Cryo-EM structure of a single subunit of a Counterclockwise-locked form of the Salmonella enterica Typhimurium flagellar C-ring.

EMDB-42387: 
Cryo-EM structure of a single subunit of a Clockwise-locked form of the Salmonella enterica Typhimurium flagellar C-ring.

EMDB-42439: 
Cryo-EM structure of a Counterclockwise locked form of the Salmonella enterica Typhimurium flagellar C-ring, with C34 symmetry applied

EMDB-42451: 
Cryo-EM structure of a Clockwise locked form of the Salmonella enterica Typhimurium flagellar C-ring, with C34 symmetry applied

PDB-8ucs: 
Cryo-EM structure of the flagellar MotAB stator bound to FliG

PDB-8umd: 
Cryo-EM structure of a single subunit of a Counterclockwise-locked form of the Salmonella enterica Typhimurium flagellar C-ring.

PDB-8umx: 
Cryo-EM structure of a single subunit of a Clockwise-locked form of the Salmonella enterica Typhimurium flagellar C-ring.

PDB-8uox: 
Cryo-EM structure of a Counterclockwise locked form of the Salmonella enterica Typhimurium flagellar C-ring, with C34 symmetry applied
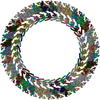
PDB-8upl: 
Cryo-EM structure of a Clockwise locked form of the Salmonella enterica Typhimurium flagellar C-ring, with C34 symmetry applied

EMDB-41370: 
Structure of a class A GPCR/Fab complex

EMDB-41827: 
Structure of a class A GPCR/agonist complex (focused map2)

EMDB-41828: 
Structure of a class A GPCR/agonist complex (focused map1)

EMDB-41829: 
Structure of a class A GPCR/agonist complex

EMDB-41850: 
Structure of a class A GPCR/agonist complex (Consensus map)

PDB-8tlm: 
Structure of a class A GPCR/Fab complex

PDB-8u1u: 
Structure of a class A GPCR/agonist complex

EMDB-41174: 
ssRNA bound SAMHD1 T closed

PDB-8tdv: 
ssRNA bound SAMHD1 T closed

EMDB-41983: 
Structure of the phage immune evasion protein Gad1 bound to the Gabija GajAB complex

PDB-8u7i: 
Structure of the phage immune evasion protein Gad1 bound to the Gabija GajAB complex

EMDB-41175: 
ssRNA bound SAMHD1 T open

PDB-8tdw: 
ssRNA bound SAMHD1 T open

EMDB-29068: 
Cryo-EM structure of the GR-Hsp90-FKBP52 complex

EMDB-29069: 
Cryo-EM structure of the GR-Hsp90-FKBP51 complex

PDB-8ffv: 
Cryo-EM structure of the GR-Hsp90-FKBP52 complex

PDB-8ffw: 
Cryo-EM structure of the GR-Hsp90-FKBP51 complex
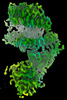
EMDB-29530: 
SARS-CoV-2 XBB.1 spike RBD bound to the human ACE2 ectodomain and the S309 neutralizing antibody Fab fragment
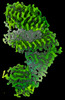
EMDB-29531: 
SARS-CoV-2 BQ.1.1 spike RBD bound to the human ACE2 ectodomain and the S309 neutralizing antibody Fab fragment
EMDB-40240: 
SARS-CoV-2 BN.1 spike RBD bound to the human ACE2 ectodomain and the S309 neutralizing antibody Fab fragment

PDB-8fxb: 
SARS-CoV-2 XBB.1 spike RBD bound to the human ACE2 ectodomain and the S309 neutralizing antibody Fab fragment

PDB-8fxc: 
SARS-CoV-2 BQ.1.1 spike RBD bound to the human ACE2 ectodomain and the S309 neutralizing antibody Fab fragment

PDB-8s9g: 
SARS-CoV-2 BN.1 spike RBD bound to the human ACE2 ectodomain and the S309 neutralizing antibody Fab fragment

EMDB-41153: 
Integrin alpha-v beta-8 in complex with minibinder B8_BP_dsulf

EMDB-41154: 
Integrin alpha-v beta-6 in complex with minibinder B6_BP_dslf

PDB-8tcf: 
Integrin alpha-v beta-8 in complex with minibinder B8_BP_dsulf

PDB-8tcg: 
Integrin alpha-v beta-6 in complex with minibinder B6_BP_dslf

EMDB-28758: 
Calcitonin Receptor in complex with Gs and Pramlintide analogue peptide San45

EMDB-28759: 
Human Amylin3 Receptor in complex with Gs and Pramlintide analogue peptide San385
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
