-検索条件
-検索結果
検索 (著者・登録者: thomas & ak)の結果694件中、1から50件目までを表示しています

EMDB-44123: 
Cryo-EM density of GluK2 amino-terminal domain (GluK2-ATD) from the open-state structure of kainate receptor GluK2 in complex with agonist glutamate and positive allosteric modulator BPAM344 bound to ConA

EMDB-44126: 
Open state of kainate receptor GluK2 in complex with agonist glutamate and positive allosteric modulator BPAM344 bound to two concanavalin A dimers

EMDB-44127: 
Open state of kainate receptor GluK2 in complex with agonist glutamate and positive allosteric modulator BPAM344 bound to one concanavalin A dimer

EMDB-42970: 
Model and map from local refinement of a CAB-A17 - Omicron Ba.1 spike complex

PDB-8v4f: 
Model and map from local refinement of a CAB-A17 - Omicron Ba.1 spike complex

EMDB-19066: 
TREK2 in OGNG/CHS detergent micelle with biparatopic inhibitory nanobody Nb6158

EMDB-19854: 
PHF type tau filament from R406W mutant

EMDB-19855: 
PHF type tau filament from in vitro V337M mutant

PDB-9eog: 
PHF type tau filament from R406W mutant

PDB-9eoh: 
PHF type tau filament from in vitro V337M mutant

EMDB-44124: 
Structure of concanavalin A (ConA) dimer from the open-state structure of kainate receptor GluK2 in complex with agonist glutamate and positive allosteric modulator BPAM344 bound to one ConA dimer. Type II interface between GluK2 ligand-binding domain and ConA

EMDB-44125: 
Structure of concanavalin A (ConA) dimer from the open-state structure of kainate receptor GluK2 in complex with agonist glutamate and positive allosteric modulator BPAM344 bound to two ConA dimers. Type I interface between GluK2 ligand-binding domain and ConA

EMDB-44128: 
Ligand-binding and transmembrane domains of kainate receptor GluK2 in the open state, a complex with agonist glutamate and positive allosteric modulator BPAM344

EMDB-44129: 
Open state of kainate receptor GluK2 in complex with agonist glutamate and positive allosteric modulator BPAM344 bound to two concanavalin A dimers. Composite map.

EMDB-44130: 
Open state of kainate receptor GluK2 in complex with agonist glutamate and positive allosteric modulator BPAM344 bound to one concanavalin A dimer. Composite map.

EMDB-44131: 
Kainate receptor GluK2 in complex with agonist glutamate with pseudo 4-fold symmetrical ligand-binding domain layer

EMDB-44132: 
Kainate receptor GluK2 in complex with agonist glutamate with asymmetric ligand-binding domain layer

PDB-9b33: 
Structure of concanavalin A (ConA) dimer from the open-state structure of kainate receptor GluK2 in complex with agonist glutamate and positive allosteric modulator BPAM344 bound to one ConA dimer. Type II interface between GluK2 ligand-binding domain and ConA

PDB-9b34: 
Structure of concanavalin A (ConA) dimer from the open-state structure of kainate receptor GluK2 in complex with agonist glutamate and positive allosteric modulator BPAM344 bound to two ConA dimers. Type I interface between GluK2 ligand-binding domain and ConA

PDB-9b35: 
Ligand-binding and transmembrane domains of kainate receptor GluK2 in the open state, a complex with agonist glutamate and positive allosteric modulator BPAM344

PDB-9b36: 
Open state of kainate receptor GluK2 in complex with agonist glutamate and positive allosteric modulator BPAM344 bound to two concanavalin A dimers. Composite map.

PDB-9b37: 
Open state of kainate receptor GluK2 in complex with agonist glutamate and positive allosteric modulator BPAM344 bound to one concanavalin A dimer. Composite map.

PDB-9b38: 
Kainate receptor GluK2 in complex with agonist glutamate with pseudo 4-fold symmetrical ligand-binding domain layer

PDB-9b39: 
Kainate receptor GluK2 in complex with agonist glutamate with asymmetric ligand-binding domain layer
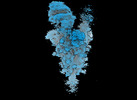
EMDB-18639: 
Locally refined SARS-CoV-2 BA-2.86 Spike receptor binding domain (RBD) complexed with angiotensin converting enzyme 2 (ACE2)

EMDB-18649: 
Local refinement of SARS-CoV-2 BA.2.86 Spike and XBB-7 Fab

EMDB-19002: 
XBB-4 Fab in complex with SARS-CoV-2 BA.2.12.1 Spike Glycoprotein

PDB-8qsq: 
Locally refined SARS-CoV-2 BA-2.86 Spike receptor binding domain (RBD) complexed with angiotensin converting enzyme 2 (ACE2)

PDB-8qtd: 
Local refinement of SARS-CoV-2 BA.2.86 Spike and XBB-7 Fab

PDB-8r8k: 
XBB-4 Fab in complex with SARS-CoV-2 BA.2.12.1 Spike Glycoprotein

EMDB-43683: 
Cryo-EM structure of FLVCR2 in the inward-facing state with choline bound

EMDB-43684: 
Cryo-EM structure of FLVCR2 in the outward-facing state with choline bound

PDB-8vzn: 
Cryo-EM structure of FLVCR2 in the inward-facing state with choline bound

PDB-8vzo: 
Cryo-EM structure of FLVCR2 in the outward-facing state with choline bound
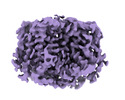
EMDB-41373: 
E. coli MraY mutant-T23P

EMDB-43751: 
TRPM7 structure in complex with anticancer agent CCT128930 in closed state

PDB-8w2l: 
TRPM7 structure in complex with anticancer agent CCT128930 in closed state

EMDB-17863: 
2.7 A cryo-EM structure of in vitro assembled type 1 pilus rod

EMDB-17878: 
2.5 A cryo-EM structure of the in vitro FimD-catalyzed assembly of type 1 pilus rod

PDB-8psv: 
2.7 A cryo-EM structure of in vitro assembled type 1 pilus rod

PDB-8ptu: 
2.5 A cryo-EM structure of the in vitro FimD-catalyzed assembly of type 1 pilus rod

EMDB-18381: 
UFL1 E3 ligase bound 60S ribosome

EMDB-18382: 
UFL1 E3 ligase bound 60S ribosome

PDB-8qfc: 
UFL1 E3 ligase bound 60S ribosome

PDB-8qfd: 
UFL1 E3 ligase bound 60S ribosome

EMDB-40856: 
Single particle reconstruction of the human LINE-1 ORF2p without substrate (apo)
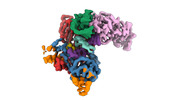
EMDB-40858: 
Structure of LINE-1 ORF2p with template:primer hybrid
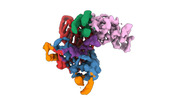
EMDB-40859: 
Structure of LINE-1 ORF2p with an oligo(A) template

PDB-8sxt: 
Structure of LINE-1 ORF2p with template:primer hybrid

PDB-8sxu: 
Structure of LINE-1 ORF2p with an oligo(A) template
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について



 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します
