| 登録情報 | データベース: PDB / ID: 6mso
|
|---|
| タイトル | Crystal structure of mitochondrial fumarate hydratase from Leishmania major in a complex with inhibitor thiomalate |
|---|
 要素 要素 | fumarate hydratase フマル酸ヒドラターゼ フマル酸ヒドラターゼ |
|---|
 キーワード キーワード | LYASE/LYASE inhibitor /  inhibitor (酵素阻害剤) / inhibitor (酵素阻害剤) /  mitochondrial (ミトコンドリア) / mitochondrial (ミトコンドリア) /  fumarate hydratase (フマル酸ヒドラターゼ) / fumarate hydratase (フマル酸ヒドラターゼ) /  LYASE (リアーゼ) / LYASE-LYASE inhibitor complex LYASE (リアーゼ) / LYASE-LYASE inhibitor complex |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 |
|---|
| 生物種 |   Leishmania major (大形リーシュマニア) Leishmania major (大形リーシュマニア) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2.053 Å 分子置換 / 解像度: 2.053 Å |
|---|
 データ登録者 データ登録者 | Feliciano, P.R. / Drennan, C.L. / Nonato, M.C. |
|---|
| 資金援助 |  ブラジル, ブラジル,  米国, 5件 米国, 5件 | 組織 | 認可番号 | 国 |
|---|
| Sao Paulo Research Foundation (FAPESP) | 2014/22246-4 |  ブラジル ブラジル | | Sao Paulo Research Foundation (FAPESP) | 2013/14988-8 |  ブラジル ブラジル | | Sao Paulo Research Foundation (FAPESP) | 2008/08262-6 |  ブラジル ブラジル | | National Institutes of Health/National Institute of General Medical Sciences (NIH/NIGMS) | R35 GM126982 |  米国 米国 | | Howard Hughes Medical Institute (HHMI) | |  米国 米国 |
|
|---|
 引用 引用 |  ジャーナル: ACS Chem. Biol. / 年: 2019 ジャーナル: ACS Chem. Biol. / 年: 2019
タイトル: Crystal Structures of Fumarate Hydratases from Leishmania major in a Complex with Inhibitor 2-Thiomalate.
著者: Feliciano, P.R. / Drennan, C.L. / Nonato, M.C. |
|---|
| 履歴 | | 登録 | 2018年10月17日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2019年1月30日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2019年2月27日 | Group: Data collection / Database references / カテゴリ: citation / citation_author
Item: _citation.journal_volume / _citation.page_first ..._citation.journal_volume / _citation.page_first / _citation.page_last / _citation.title / _citation_author.identifier_ORCID |
|---|
| 改定 1.2 | 2019年11月20日 | Group: Author supporting evidence / カテゴリ: pdbx_audit_support / Item: _pdbx_audit_support.funding_organization |
|---|
| 改定 1.3 | 2023年10月11日 | Group: Data collection / Database references ...Data collection / Database references / Derived calculations / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model / pdbx_struct_conn_angle / struct_conn
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_struct_conn_angle.ptnr1_auth_asym_id / _pdbx_struct_conn_angle.ptnr1_auth_comp_id / _pdbx_struct_conn_angle.ptnr1_auth_seq_id / _pdbx_struct_conn_angle.ptnr1_label_alt_id / _pdbx_struct_conn_angle.ptnr1_label_asym_id / _pdbx_struct_conn_angle.ptnr1_label_atom_id / _pdbx_struct_conn_angle.ptnr1_label_comp_id / _pdbx_struct_conn_angle.ptnr1_label_seq_id / _pdbx_struct_conn_angle.ptnr2_auth_asym_id / _pdbx_struct_conn_angle.ptnr2_label_asym_id / _pdbx_struct_conn_angle.ptnr2_label_atom_id / _pdbx_struct_conn_angle.ptnr3_auth_asym_id / _pdbx_struct_conn_angle.ptnr3_auth_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_seq_id / _pdbx_struct_conn_angle.ptnr3_label_alt_id / _pdbx_struct_conn_angle.ptnr3_label_asym_id / _pdbx_struct_conn_angle.ptnr3_label_atom_id / _pdbx_struct_conn_angle.ptnr3_label_comp_id / _pdbx_struct_conn_angle.value / _struct_conn.pdbx_dist_value / _struct_conn.pdbx_ptnr2_label_alt_id / _struct_conn.ptnr1_auth_asym_id / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_asym_id / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 フマル酸ヒドラターゼ
フマル酸ヒドラターゼ  キーワード
キーワード inhibitor (酵素阻害剤) /
inhibitor (酵素阻害剤) /  mitochondrial (ミトコンドリア) /
mitochondrial (ミトコンドリア) /  fumarate hydratase (フマル酸ヒドラターゼ) /
fumarate hydratase (フマル酸ヒドラターゼ) /  LYASE (リアーゼ) / LYASE-LYASE inhibitor complex
LYASE (リアーゼ) / LYASE-LYASE inhibitor complex 機能・相同性情報
機能・相同性情報 fumarate hydratase activity /
fumarate hydratase activity /  フマル酸ヒドラターゼ / fumarate metabolic process / malate metabolic process /
フマル酸ヒドラターゼ / fumarate metabolic process / malate metabolic process /  クエン酸回路 / 4 iron, 4 sulfur cluster binding / protein homodimerization activity /
クエン酸回路 / 4 iron, 4 sulfur cluster binding / protein homodimerization activity /  ミトコンドリア /
ミトコンドリア /  metal ion binding /
metal ion binding /  細胞質
細胞質
 Leishmania major (大形リーシュマニア)
Leishmania major (大形リーシュマニア) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 2.053 Å
分子置換 / 解像度: 2.053 Å  データ登録者
データ登録者 ブラジル,
ブラジル,  米国, 5件
米国, 5件  引用
引用 ジャーナル: ACS Chem. Biol. / 年: 2019
ジャーナル: ACS Chem. Biol. / 年: 2019 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 6mso.cif.gz
6mso.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb6mso.ent.gz
pdb6mso.ent.gz PDB形式
PDB形式 6mso.json.gz
6mso.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/ms/6mso
https://data.pdbj.org/pub/pdb/validation_reports/ms/6mso ftp://data.pdbj.org/pub/pdb/validation_reports/ms/6mso
ftp://data.pdbj.org/pub/pdb/validation_reports/ms/6mso リンク
リンク 集合体
集合体


 要素
要素 フマル酸ヒドラターゼ
フマル酸ヒドラターゼ
 Leishmania major (大形リーシュマニア)
Leishmania major (大形リーシュマニア)
 Escherichia coli (大腸菌) / 参照: UniProt: Q4QAU9,
Escherichia coli (大腸菌) / 参照: UniProt: Q4QAU9,  フマル酸ヒドラターゼ
フマル酸ヒドラターゼ


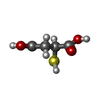





 鉄・硫黄クラスター
鉄・硫黄クラスター グリセリン
グリセリン ポリエチレングリコール
ポリエチレングリコール Thiomalic acid
Thiomalic acid 水
水 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製
 シンクロトロン / サイト:
シンクロトロン / サイト:  APS
APS  / ビームライン: 24-ID-C / 波長: 0.9792 Å
/ ビームライン: 24-ID-C / 波長: 0.9792 Å : 0.9792 Å / 相対比: 1
: 0.9792 Å / 相対比: 1  解析
解析 :
:  分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj




