登録情報 データベース : PDB / ID : 5tieタイトル x-ray structure of acyl-CoA thioesterase I, TesA, mutant M141L/Y145K/L146K at pH 7.5 in complex with octanoic acid Acyl-CoA thioesterase I キーワード / / / / 機能・相同性 生物種 Escherichia coli (大腸菌)手法 / / 解像度 : 1.15 Å データ登録者 Thoden, J.B. / Holden, H.M. / Grisewood, M.J. / Hernandez Lozada, N.J. / Gifford, N.P. / Mendez-Perez, D. / Schoenberger, H.A. / Allan, M.F. / Pfleger, B.F. / Marines, C.D. 資金援助 組織 認可番号 国 National Institutes of Health/National Institute of General Medical Sciences (NIH/NIGMS) GM115921
ジャーナル : ACS Catal / 年 : 2017タイトル : Computational Redesign of Acyl-ACP Thioesterase with Improved Selectivity toward Medium-Chain-Length Fatty Acids.著者 : Grisewood, M.J. / Hernandez Lozada, N.J. / Thoden, J.B. / Gifford, N.P. / Mendez-Perez, D. / Schoenberger, H.A. / Allan, M.F. / Floy, M.E. / Lai, R.Y. / Holden, H.M. / Pfleger, B.F. / Maranas, C.D. 履歴 登録 2016年10月2日 登録サイト / 処理サイト 改定 1.0 2017年4月26日 Provider / タイプ 改定 1.1 2017年9月27日 Group / カテゴリ / Item 改定 1.2 2018年2月14日 Group / カテゴリ / citation_authorItem _citation.journal_abbrev / _citation.journal_volume ... _citation.journal_abbrev / _citation.journal_volume / _citation.page_first / _citation.page_last / _citation.pdbx_database_id_DOI / _citation.pdbx_database_id_PubMed / _citation.title 改定 1.3 2019年12月25日 Group / カテゴリ / Item 改定 1.4 2023年10月4日 Group / Database references / Refinement descriptionカテゴリ chem_comp_atom / chem_comp_bond ... chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model Item / _database_2.pdbx_database_accession
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード HYDROLASE (加水分解酵素) /
HYDROLASE (加水分解酵素) /  thioesterase (チオエステル加水分解酵素) / TesA /
thioesterase (チオエステル加水分解酵素) / TesA /  fatty acid (脂肪酸) /
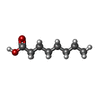
fatty acid (脂肪酸) /  octanoic acid (カプリル酸)
octanoic acid (カプリル酸) 機能・相同性情報
機能・相同性情報 アリールエステラーゼ / phosphatidyl phospholipase B activity /
アリールエステラーゼ / phosphatidyl phospholipase B activity /  lysophospholipase /
lysophospholipase /  : /
: /  パルミトイルCoAヒドロラーゼ /
パルミトイルCoAヒドロラーゼ /  : / : / fatty acyl-CoA hydrolase activity / oleoyl-[acyl-carrier-protein] hydrolase /
: / : / fatty acyl-CoA hydrolase activity / oleoyl-[acyl-carrier-protein] hydrolase /  lysophospholipase activity ...
lysophospholipase activity ... アリールエステラーゼ / phosphatidyl phospholipase B activity /
アリールエステラーゼ / phosphatidyl phospholipase B activity /  lysophospholipase /
lysophospholipase /  : /
: /  パルミトイルCoAヒドロラーゼ /
パルミトイルCoAヒドロラーゼ /  : / : / fatty acyl-CoA hydrolase activity / oleoyl-[acyl-carrier-protein] hydrolase /
: / : / fatty acyl-CoA hydrolase activity / oleoyl-[acyl-carrier-protein] hydrolase /  lysophospholipase activity /
lysophospholipase activity /  加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; セリンエンドペプチターゼ /
加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; セリンエンドペプチターゼ /  arylesterase activity / lipid metabolic process / outer membrane-bounded periplasmic space /
arylesterase activity / lipid metabolic process / outer membrane-bounded periplasmic space /  peptidase activity /
peptidase activity /  タンパク質分解 / identical protein binding
タンパク質分解 / identical protein binding
 Escherichia coli (大腸菌)
Escherichia coli (大腸菌) X線回折 /
X線回折 /  フーリエ合成 / 解像度: 1.15 Å
フーリエ合成 / 解像度: 1.15 Å  データ登録者
データ登録者 米国, 1件
米国, 1件  引用
引用 ジャーナル: ACS Catal / 年: 2017
ジャーナル: ACS Catal / 年: 2017 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 5tie.cif.gz
5tie.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb5tie.ent.gz
pdb5tie.ent.gz PDB形式
PDB形式 5tie.json.gz
5tie.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/ti/5tie
https://data.pdbj.org/pub/pdb/validation_reports/ti/5tie ftp://data.pdbj.org/pub/pdb/validation_reports/ti/5tie
ftp://data.pdbj.org/pub/pdb/validation_reports/ti/5tie リンク
リンク 集合体
集合体
 要素
要素
 Escherichia coli (大腸菌) / 遺伝子: tesA, apeA, pldC, b0494, JW0483 / 発現宿主:
Escherichia coli (大腸菌) / 遺伝子: tesA, apeA, pldC, b0494, JW0483 / 発現宿主: 
 Escherichia coli (大腸菌) / 株 (発現宿主): Rosetta2(DE3)
Escherichia coli (大腸菌) / 株 (発現宿主): Rosetta2(DE3) 加水分解酵素; エステル加水分解酵素; 3価のアルコールのエステル加水分解酵素,
加水分解酵素; エステル加水分解酵素; 3価のアルコールのエステル加水分解酵素,  lysophospholipase
lysophospholipase カプリル酸
カプリル酸 水
水 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製
 回転陽極 / タイプ: RIGAKU RU200 / 波長: 1.5418 Å
回転陽極 / タイプ: RIGAKU RU200 / 波長: 1.5418 Å : 1.5418 Å / 相対比: 1
: 1.5418 Å / 相対比: 1  解析
解析 :
:  フーリエ合成
フーリエ合成 ムービー
ムービー コントローラー
コントローラー
















 PDBj
PDBj