+ データを開く
データを開く
- 基本情報
基本情報
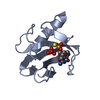
| 登録情報 | データベース: PDB / ID: 3rnt | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | CRYSTAL STRUCTURE OF GUANOSINE-FREE RIBONUCLEASE T1, COMPLEXED WITH VANADATE(V), SUGGESTS CONFORMATIONAL CHANGE UPON SUBSTRATE BINDING | ||||||
 要素 要素 | RIBONUCLEASE T1 | ||||||
 キーワード キーワード | HYDROLASE(ENDORIBONUCLEASE) | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報hyphal tip /  ribonuclease T1 activity / ribonuclease T1 activity /  ribonuclease T1 / cell septum / ribonuclease T1 / cell septum /  endonuclease activity / endonuclease activity /  lyase activity / lyase activity /  RNA binding RNA binding類似検索 - 分子機能 | ||||||
| 生物種 |   Aspergillus oryzae (米麹菌) Aspergillus oryzae (米麹菌) | ||||||
| 手法 |  X線回折 / 解像度: 1.8 Å X線回折 / 解像度: 1.8 Å | ||||||
 データ登録者 データ登録者 | Kostrewa, D. / Choe, H.-W. / Heinemann, U. / Saenger, W. | ||||||
 引用 引用 |  ジャーナル: Biochemistry / 年: 1989 ジャーナル: Biochemistry / 年: 1989タイトル: Crystal structure of guanosine-free ribonuclease T1, complexed with vanadate (V), suggests conformational change upon substrate binding. 著者: Kostrewa, D. / Choe, H.W. / Heinemann, U. / Saenger, W. #1:  ジャーナル: J.Mol.Biol. / 年: 1989 ジャーナル: J.Mol.Biol. / 年: 1989タイトル: Three-Dimensional Structure of Ribonuclease T1 Complexed with Guanylyl-2(Prime),5(Prime)-Guanosine at 1.8 Angstroms Resolution 著者: Koepke, J. / Maslowska, M. / Heinemann, U. / Saenger, W. #2:  ジャーナル: J.Biol.Chem. / 年: 1988 ジャーナル: J.Biol.Chem. / 年: 1988タイトル: Three-Dimensional Structure of the Ribonuclease T1(Asterisk)2(Prime)-Gmp Complex at 1.9-Angstroms Resolution 著者: Arni, R. / Heinemann, U. / Tokuoka, R. / Saenger, W. #3:  ジャーナル: Fresenius Z.Anal.Chem. / 年: 1987 ジャーナル: Fresenius Z.Anal.Chem. / 年: 1987タイトル: Struktur Und Funktion Des Enzyms Ribonuclease T1 (German) 著者: Arni, R. / Heinemann, U. / Saenger, W. #4:  ジャーナル: Acta Crystallogr.,Sect.B / 年: 1987 ジャーナル: Acta Crystallogr.,Sect.B / 年: 1987タイトル: Restrained Least-Squares Refinement of the Crystal Structure of the Ribonuclease T1(Asterisk)2(Prime)-Guanylic Acid Complex at 1.9 Angstroms Resolution 著者: Arni, R. / Heinemann, U. / Maslowska, M. / Tokuoka, R. / Saenger, W. #5:  ジャーナル: Pure Appl.Chem. / 年: 1985 ジャーナル: Pure Appl.Chem. / 年: 1985タイトル: Mechanism of Guanosine Recognition and RNA Hydrolysis by Ribonuclease T1 著者: Heinemann, U. / Saenger, W. #6:  ジャーナル: Trends Biochem.Sci.(Pers. Ed.) / 年: 1983 ジャーナル: Trends Biochem.Sci.(Pers. Ed.) / 年: 1983タイトル: The Structural and Sequence Homology of a Family of Microbial Ribonucleases 著者: Hill, C. / Dodson, G. / Heinemann, U. / Saenger, W. / Mitsui, Y. / Nakamura, K. / Borisov, S. / Tischenko, G. / Polyakov, K. / Pavlovsky, S. #7:  ジャーナル: Jerusalem Symp.Quantum Chem.Biochem. / 年: 1983 ジャーナル: Jerusalem Symp.Quantum Chem.Biochem. / 年: 1983タイトル: Ribonuclease T1. Mechanism of Specific Guanine Recognition and RNA Hydrolysis 著者: Heinemann, U. / Saenger, W. #8:  ジャーナル: J.Biomol.Struct.Dyn. / 年: 1983 ジャーナル: J.Biomol.Struct.Dyn. / 年: 1983タイトル: Crystallographic Study of Mechanism of Ribonuclease T1-Catalysed Specific RNA Hydrolysis 著者: Heinemann, U. / Saenger, W. #9:  ジャーナル: Nature / 年: 1982 ジャーナル: Nature / 年: 1982タイトル: Specific Protein-Nucleic Acid Recognition in Ribonuclease T1-2(Prime)-Guanylic Acid Complex. An X-Ray Study 著者: Heinemann, U. / Saenger, W. #10:  ジャーナル: Eur.J.Biochem. / 年: 1980 ジャーナル: Eur.J.Biochem. / 年: 1980タイトル: Crystallization of a Complex between Ribonuclease T1 and 2(Prime)-Guanylic Acid 著者: Heinemann, U. / Wernitz, M. / Paehler, A. / Saenger, W. / Menke, G. / Rueterjans, H. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  3rnt.cif.gz 3rnt.cif.gz | 33.5 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb3rnt.ent.gz pdb3rnt.ent.gz | 25 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  3rnt.json.gz 3rnt.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/rn/3rnt https://data.pdbj.org/pub/pdb/validation_reports/rn/3rnt ftp://data.pdbj.org/pub/pdb/validation_reports/rn/3rnt ftp://data.pdbj.org/pub/pdb/validation_reports/rn/3rnt | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| 単位格子 |
| ||||||||
| Atom site foot note | 1: RESIDUES 39 AND 55 ARE CIS PROLINES. |
- 要素
要素
| #1: タンパク質 |  分子量: 11094.694 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)   Aspergillus oryzae (米麹菌) / 参照: UniProt: P00651, EC: 3.1.27.3 Aspergillus oryzae (米麹菌) / 参照: UniProt: P00651, EC: 3.1.27.3 |
|---|---|
| #2: 化合物 | ChemComp-CA / |
| #3: 化合物 | ChemComp-VO4 /  バナジン酸塩 バナジン酸塩 |
| #4: 水 | ChemComp-HOH /  水 水 |
-実験情報
-実験
| 実験 | 手法:  X線回折 X線回折 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.11 Å3/Da / 溶媒含有率: 41.65 % | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
結晶化 | *PLUS pH: 5 / 手法: microdialysis | ||||||||||||||||||||||||||||||||||||
| 溶液の組成 | *PLUS
|
-データ収集
| 反射 | *PLUS 最高解像度: 1.8 Å / Num. obs: 7134 / % possible obs: 77 % / Observed criterion σ(F): 1 / Num. measured all: 11536 |
|---|---|
| 反射 シェル | *PLUS 最高解像度: 1.8 Å / 最低解像度: 2 Å / % possible obs: 59 % |
- 解析
解析
| ソフトウェア | 名称: PROFFT / 分類: 精密化 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 解像度: 1.8→10 Å / σ(I): 0 /
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 1.8→10 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 | *PLUS σ(I): 1 / Rfactor obs: 0.137 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | *PLUS | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | *PLUS |
 ムービー
ムービー コントローラー
コントローラー












 PDBj
PDBj