+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 3erp | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Structure of IDP01002, a putative oxidoreductase from and essential gene of Salmonella typhimurium | ||||||
 要素 要素 | Putative oxidoreductase | ||||||
 キーワード キーワード | OXIDOREDUCTASE / FUNDED BY THE NATIONAL INSTITUTE OF ALLERGY AND INFECTIOUS DISEASES OF NIH CONTRACT NUMBER HHSN272200700058C / predicted oxidoreductase / essential gene / Salmonella / molecular replacement / Structural Genomics / Center for Structural Genomics of Infectious Diseases / CSGID | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 | ||||||
| 生物種 |  Salmonella enterica subsp. enterica serovar Typhimurium (サルモネラ菌) Salmonella enterica subsp. enterica serovar Typhimurium (サルモネラ菌) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.55 Å 分子置換 / 解像度: 1.55 Å | ||||||
 データ登録者 データ登録者 | Singer, A.U. / Minasov, G. / Evdokimova, E. / Brunzelle, J.S. / Kudritska, M. / Edwards, A.M. / Anderson, W.F. / Savchenko, A. / Center for Structural Genomics of Infectious Diseases (CSGID) | ||||||
 引用 引用 |  ジャーナル: Appl.Environ.Microbiol. / 年: 2017 ジャーナル: Appl.Environ.Microbiol. / 年: 2017タイトル: Structural and biochemical studies of novel aldo-keto reductases for the biocatalytic conversion of 3-hydroxybutanal to 1,3-butanediol. 著者: Kim, T. / Flick, R. / Brunzelle, J. / Singer, A. / Evdokimova, E. / Brown, G. / Joo, J.C. / Minasov, G.A. / Anderson, W.F. / Mahadevan, R. / Savchenko, A. / Yakunin, A.F. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  3erp.cif.gz 3erp.cif.gz | 175.4 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb3erp.ent.gz pdb3erp.ent.gz | 137.4 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  3erp.json.gz 3erp.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  3erp_validation.pdf.gz 3erp_validation.pdf.gz | 478 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  3erp_full_validation.pdf.gz 3erp_full_validation.pdf.gz | 489.4 KB | 表示 | |
| XML形式データ |  3erp_validation.xml.gz 3erp_validation.xml.gz | 36.1 KB | 表示 | |
| CIF形式データ |  3erp_validation.cif.gz 3erp_validation.cif.gz | 56 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/er/3erp https://data.pdbj.org/pub/pdb/validation_reports/er/3erp ftp://data.pdbj.org/pub/pdb/validation_reports/er/3erp ftp://data.pdbj.org/pub/pdb/validation_reports/er/3erp | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||
| 2 | 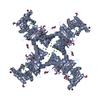
| ||||||||
| 3 | 
| ||||||||
| 単位格子 |
| ||||||||
| Components on special symmetry positions |
|
- 要素
要素
-タンパク質 , 1種, 2分子 AB
| #1: タンパク質 | 分子量: 39862.121 Da / 分子数: 2 / 由来タイプ: 組換発現 / 詳細: no TEV cleavage 由来: (組換発現)  Salmonella enterica subsp. enterica serovar Typhimurium (サルモネラ菌) Salmonella enterica subsp. enterica serovar Typhimurium (サルモネラ菌)株: LT2 / 遺伝子: STM2406 / プラスミド: p15TvLic / 発現宿主:  |
|---|
-非ポリマー , 6種, 868分子 


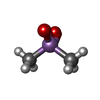







| #2: 化合物 | | #3: 化合物 | #4: 化合物 | ChemComp-CL / #5: 化合物 | #6: 化合物 | ChemComp-EDO / #7: 水 | ChemComp-HOH / | |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 3.05 Å3/Da / 溶媒含有率: 59.69 % |
|---|---|
| 結晶化 | 温度: 295 K / 手法: 蒸発脱水法 / pH: 6.5 詳細: crystallized in 0.2 M Calcium Acetate, 9% PEG8000 and 0.1 M Sodium Cacodylate. Cryoprotected with 25% ethylene glycol., pH 6.5, EVAPORATION, temperature 295K |
-データ収集
| 回折 | 平均測定温度: 100 K |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  APS APS  / ビームライン: 21-ID-G / 波長: 0.97856 Å / ビームライン: 21-ID-G / 波長: 0.97856 Å |
| 検出器 | タイプ: MARMOSAIC 300 mm CCD / 検出器: CCD / 日付: 2008年2月2日 / 詳細: mirrors |
| 放射 | モノクロメーター: C(111) / プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 0.97856 Å / 相対比: 1 |
| 反射 | 解像度: 1.55→30 Å / Num. all: 136598 / Num. obs: 132754 / % possible obs: 97.2 % / Observed criterion σ(F): 0 / Observed criterion σ(I): 0 / 冗長度: 5.2 % / Biso Wilson estimate: 17.8 Å2 / Rmerge(I) obs: 0.06 / Net I/σ(I): 23.08 |
| 反射 シェル | 解像度: 1.55→1.61 Å / 冗長度: 4.6 % / Rmerge(I) obs: 0.477 / Mean I/σ(I) obs: 2.62 / Num. unique all: 13638 / % possible all: 80.3 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 分子置換開始モデル: PDB code 1ZSX was used for MR on a crystal diffracting to 2.15 A on our RAXIS4 home source. The protein atoms from the model refined from that crystal were used for rigid body ...開始モデル: PDB code 1ZSX was used for MR on a crystal diffracting to 2.15 A on our RAXIS4 home source. The protein atoms from the model refined from that crystal were used for rigid body refinement with the new data diffracting to 1.55 A. 解像度: 1.55→29.96 Å / Cor.coef. Fo:Fc: 0.974 / Cor.coef. Fo:Fc free: 0.965 / SU B: 1.166 / SU ML: 0.042 / 交差検証法: THROUGHOUT / σ(F): 0 / σ(I): 0 / ESU R: 0.063 / ESU R Free: 0.065 / 立体化学のターゲット値: MAXIMUM LIKELIHOOD / 詳細: HYDROGENS HAVE BEEN ADDED IN THE RIDING POSITIONS
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | イオンプローブ半径: 0.8 Å / 減衰半径: 0.8 Å / VDWプローブ半径: 1.2 Å / 溶媒モデル: BABINET MODEL WITH MASK | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 23.404 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 1.55→29.96 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル | 解像度: 1.554→1.594 Å / Total num. of bins used: 20
|
 ムービー
ムービー コントローラー
コントローラー











 PDBj
PDBj









