+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 2juu | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | allo-ThrA3 DKP-insulin | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード |  HORMONE (ホルモン) / HORMONE (ホルモン) /  Insulin (インスリン) / allo-ThrA3 / Insulin (インスリン) / allo-ThrA3 /  Carbohydrate metabolism (炭水化物代謝) / Cleavage on pair of basic residues / Carbohydrate metabolism (炭水化物代謝) / Cleavage on pair of basic residues /  Diabetes mellitus (糖尿病) / Disease mutation / Diabetes mellitus (糖尿病) / Disease mutation /  Glucose metabolism (炭水化物代謝) / Glucose metabolism (炭水化物代謝) /  Pharmaceutical (医薬品) / Pharmaceutical (医薬品) /  Secreted (分泌) Secreted (分泌) | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報negative regulation of NAD(P)H oxidase activity / negative regulation of glycogen catabolic process / regulation of cellular amino acid metabolic process / Signaling by Insulin receptor / IRS activation / nitric oxide-cGMP-mediated signaling / negative regulation of fatty acid metabolic process / Insulin processing / negative regulation of feeding behavior /  regulation of protein secretion ...negative regulation of NAD(P)H oxidase activity / negative regulation of glycogen catabolic process / regulation of cellular amino acid metabolic process / Signaling by Insulin receptor / IRS activation / nitric oxide-cGMP-mediated signaling / negative regulation of fatty acid metabolic process / Insulin processing / negative regulation of feeding behavior / regulation of protein secretion ...negative regulation of NAD(P)H oxidase activity / negative regulation of glycogen catabolic process / regulation of cellular amino acid metabolic process / Signaling by Insulin receptor / IRS activation / nitric oxide-cGMP-mediated signaling / negative regulation of fatty acid metabolic process / Insulin processing / negative regulation of feeding behavior /  regulation of protein secretion / positive regulation of peptide hormone secretion / regulation of protein secretion / positive regulation of peptide hormone secretion /  Regulation of gene expression in beta cells / positive regulation of respiratory burst / positive regulation of dendritic spine maintenance / alpha-beta T cell activation / negative regulation of acute inflammatory response / negative regulation of respiratory burst involved in inflammatory response / negative regulation of protein secretion / fatty acid homeostasis / Synthesis, secretion, and deacylation of Ghrelin / positive regulation of glycogen biosynthetic process / positive regulation of lipid biosynthetic process / Signal attenuation / FOXO-mediated transcription of oxidative stress, metabolic and neuronal genes / negative regulation of gluconeogenesis / positive regulation of nitric oxide mediated signal transduction / regulation of protein localization to plasma membrane / COPI-mediated anterograde transport / negative regulation of lipid catabolic process / negative regulation of oxidative stress-induced intrinsic apoptotic signaling pathway / positive regulation of insulin receptor signaling pathway / negative regulation of reactive oxygen species biosynthetic process / Regulation of gene expression in beta cells / positive regulation of respiratory burst / positive regulation of dendritic spine maintenance / alpha-beta T cell activation / negative regulation of acute inflammatory response / negative regulation of respiratory burst involved in inflammatory response / negative regulation of protein secretion / fatty acid homeostasis / Synthesis, secretion, and deacylation of Ghrelin / positive regulation of glycogen biosynthetic process / positive regulation of lipid biosynthetic process / Signal attenuation / FOXO-mediated transcription of oxidative stress, metabolic and neuronal genes / negative regulation of gluconeogenesis / positive regulation of nitric oxide mediated signal transduction / regulation of protein localization to plasma membrane / COPI-mediated anterograde transport / negative regulation of lipid catabolic process / negative regulation of oxidative stress-induced intrinsic apoptotic signaling pathway / positive regulation of insulin receptor signaling pathway / negative regulation of reactive oxygen species biosynthetic process /  小胞 / positive regulation of protein autophosphorylation / Insulin receptor recycling / 小胞 / positive regulation of protein autophosphorylation / Insulin receptor recycling /  insulin-like growth factor receptor binding / NPAS4 regulates expression of target genes / positive regulation of protein metabolic process / neuron projection maintenance / endoplasmic reticulum-Golgi intermediate compartment membrane / positive regulation of brown fat cell differentiation / activation of protein kinase B activity / positive regulation of glycolytic process / Insulin receptor signalling cascade / positive regulation of mitotic nuclear division / Regulation of insulin secretion / positive regulation of nitric-oxide synthase activity / positive regulation of long-term synaptic potentiation / endosome lumen / positive regulation of cytokine production / acute-phase response / positive regulation of protein secretion / regulation of transmembrane transporter activity / positive regulation of cell differentiation / positive regulation of glucose import / negative regulation of proteolysis / insulin-like growth factor receptor binding / NPAS4 regulates expression of target genes / positive regulation of protein metabolic process / neuron projection maintenance / endoplasmic reticulum-Golgi intermediate compartment membrane / positive regulation of brown fat cell differentiation / activation of protein kinase B activity / positive regulation of glycolytic process / Insulin receptor signalling cascade / positive regulation of mitotic nuclear division / Regulation of insulin secretion / positive regulation of nitric-oxide synthase activity / positive regulation of long-term synaptic potentiation / endosome lumen / positive regulation of cytokine production / acute-phase response / positive regulation of protein secretion / regulation of transmembrane transporter activity / positive regulation of cell differentiation / positive regulation of glucose import / negative regulation of proteolysis /  regulation of synaptic plasticity / regulation of synaptic plasticity /  wound healing / wound healing /  insulin receptor binding / negative regulation of protein catabolic process / positive regulation of neuron projection development / insulin receptor binding / negative regulation of protein catabolic process / positive regulation of neuron projection development /  hormone activity / hormone activity /  認識 / Golgi lumen / 認識 / Golgi lumen /  vasodilation / positive regulation of protein localization to nucleus / glucose metabolic process / vasodilation / positive regulation of protein localization to nucleus / glucose metabolic process /  regulation of protein localization / regulation of protein localization /  glucose homeostasis / cell-cell signaling / insulin receptor signaling pathway / positive regulation of NF-kappaB transcription factor activity / PI5P, PP2A and IER3 Regulate PI3K/AKT Signaling / positive regulation of cell growth / secretory granule lumen / glucose homeostasis / cell-cell signaling / insulin receptor signaling pathway / positive regulation of NF-kappaB transcription factor activity / PI5P, PP2A and IER3 Regulate PI3K/AKT Signaling / positive regulation of cell growth / secretory granule lumen /  protease binding / positive regulation of MAPK cascade / positive regulation of phosphatidylinositol 3-kinase/protein kinase B signal transduction / positive regulation of cell migration / G protein-coupled receptor signaling pathway / Amyloid fiber formation / protease binding / positive regulation of MAPK cascade / positive regulation of phosphatidylinositol 3-kinase/protein kinase B signal transduction / positive regulation of cell migration / G protein-coupled receptor signaling pathway / Amyloid fiber formation /  小胞体 / 小胞体 /  ゴルジ体 / negative regulation of gene expression / positive regulation of cell population proliferation / positive regulation of gene expression / regulation of DNA-templated transcription / ゴルジ体 / negative regulation of gene expression / positive regulation of cell population proliferation / positive regulation of gene expression / regulation of DNA-templated transcription /  extracellular space / extracellular region / identical protein binding extracellular space / extracellular region / identical protein binding類似検索 - 分子機能 | ||||||
| 手法 |  溶液NMR / DGSA-distance geometry simulated annealing 溶液NMR / DGSA-distance geometry simulated annealing | ||||||
 データ登録者 データ登録者 | Huang, K. / Chan, S. / Hua, Q. / Chu, Y. / Wang, R. / Klaproth, B. / Jia, W. / Whittaker, J. / De Meyts, P. / Nakagawa, S.H. ...Huang, K. / Chan, S. / Hua, Q. / Chu, Y. / Wang, R. / Klaproth, B. / Jia, W. / Whittaker, J. / De Meyts, P. / Nakagawa, S.H. / Steiner, D.F. / Katsoyannis, P.G. / Weiss, M.A. | ||||||
 引用 引用 |  ジャーナル: J.Biol.Chem. / 年: 2007 ジャーナル: J.Biol.Chem. / 年: 2007タイトル: The A-chain of Insulin Contacts the Insert Domain of the Insulin Receptor: PHOTO-CROSS-LINKING AND MUTAGENESIS OF A DIABETES-RELATED CREVICE. 著者: Huang, K. / Chan, S.J. / Hua, Q.X. / Chu, Y.C. / Wang, R.Y. / Klaproth, B. / Jia, W. / Whittaker, J. / De Meyts, P. / Nakagawa, S.H. / Steiner, D.F. / Katsoyannis, P.G. / Weiss, M.A. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
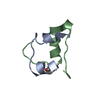
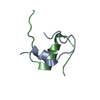
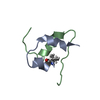
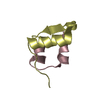
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  2juu.cif.gz 2juu.cif.gz | 227.7 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb2juu.ent.gz pdb2juu.ent.gz | 197.9 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  2juu.json.gz 2juu.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/ju/2juu https://data.pdbj.org/pub/pdb/validation_reports/ju/2juu ftp://data.pdbj.org/pub/pdb/validation_reports/ju/2juu ftp://data.pdbj.org/pub/pdb/validation_reports/ju/2juu | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||
| NMR アンサンブル |
|
- 要素
要素
| #1: タンパク質・ペプチド | 分子量: 2385.671 Da / 分子数: 1 / 変異: V3T / 由来タイプ: 合成 / 参照: UniProt: P01308 |
|---|---|
| #2: タンパク質・ペプチド | 分子量: 3410.894 Da / 分子数: 1 / 変異: H10D,P28K,K29P / 由来タイプ: 合成 / 参照: UniProt: P01308 |
-実験情報
-実験
| 実験 | 手法:  溶液NMR 溶液NMR | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| NMR実験 |
|
- 試料調製
試料調製
| 詳細 |
| ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 試料 |
| ||||||||||||||||||||||||
| 試料状態 |
|
-NMR測定
| NMRスペクトロメーター |
|
|---|
- 解析
解析
| NMR software |
| ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 手法: DGSA-distance geometry simulated annealing / ソフトェア番号: 1 | ||||||||||||
| 代表構造 | 選択基準: closest to the average | ||||||||||||
| NMRアンサンブル | コンフォーマー選択の基準: structures with the lowest energy 計算したコンフォーマーの数: 50 / 登録したコンフォーマーの数: 15 |
 ムービー
ムービー コントローラー
コントローラー











 PDBj
PDBj

















