+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-6320 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
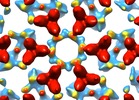
| タイトル | Structure of bacterial chemotaxis signaling CheA2-hexamer core complex by cryo-electron tomography and subvolume averaging | |||||||||
 マップデータ マップデータ | Structure of bacterial chemotaxis signaling CheA2-hexamer core complex by cryo-electron tomography and subvolume averaging | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Bacterial chemotaxis /  Signal transduction (シグナル伝達) / Signal transduction (シグナル伝達) /  cryo-Electron Tomography / cryo-Electron Tomography /  Molecular dynamics simulation (分子動力学法) / all-atom Molecular dynamics simulation (分子動力学法) / all-atom | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報negative regulation of protein modification process / detection of chemical stimulus / methyl accepting chemotaxis protein complex / protein histidine kinase binding / positive regulation of post-translational protein modification / bacterial-type flagellum-dependent swimming motility / cell tip / regulation of bacterial-type flagellum-dependent cell motility /  aerotaxis / protein histidine kinase activity ...negative regulation of protein modification process / detection of chemical stimulus / methyl accepting chemotaxis protein complex / protein histidine kinase binding / positive regulation of post-translational protein modification / bacterial-type flagellum-dependent swimming motility / cell tip / regulation of bacterial-type flagellum-dependent cell motility / aerotaxis / protein histidine kinase activity ...negative regulation of protein modification process / detection of chemical stimulus / methyl accepting chemotaxis protein complex / protein histidine kinase binding / positive regulation of post-translational protein modification / bacterial-type flagellum-dependent swimming motility / cell tip / regulation of bacterial-type flagellum-dependent cell motility /  aerotaxis / protein histidine kinase activity / aerotaxis / protein histidine kinase activity /  regulation of chemotaxis / regulation of chemotaxis /  thermotaxis / signal complex assembly / thermotaxis / signal complex assembly /  histidine kinase / phosphorelay sensor kinase activity / phosphorelay signal transduction system / establishment of localization in cell / cellular response to amino acid stimulus / protein homooligomerization / histidine kinase / phosphorelay sensor kinase activity / phosphorelay signal transduction system / establishment of localization in cell / cellular response to amino acid stimulus / protein homooligomerization /  走化性 / transmembrane signaling receptor activity / protein domain specific binding / 走化性 / transmembrane signaling receptor activity / protein domain specific binding /  リン酸化 / リン酸化 /  シグナル伝達 / protein homodimerization activity / シグナル伝達 / protein homodimerization activity /  ATP binding / identical protein binding / ATP binding / identical protein binding /  細胞膜 / 細胞膜 /  細胞質基質 / 細胞質基質 /  細胞質 細胞質類似検索 - 分子機能 | |||||||||
| 生物種 |   Escherichia coli (大腸菌) Escherichia coli (大腸菌) | |||||||||
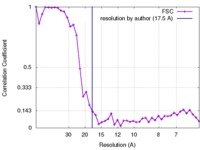
| 手法 | サブトモグラム平均法 /  クライオ電子顕微鏡法 / 解像度: 17.5 Å クライオ電子顕微鏡法 / 解像度: 17.5 Å | |||||||||
 データ登録者 データ登録者 | Cassidy CK / Himes BA / Alvarez FJ / Ma J / Zhou G / Perilla JR / Schulten K / Zhang P | |||||||||
 引用 引用 |  ジャーナル: Elife / 年: 2015 ジャーナル: Elife / 年: 2015タイトル: CryoEM and computer simulations reveal a novel kinase conformational switch in bacterial chemotaxis signaling. 著者: C Keith Cassidy / Benjamin A Himes / Frances J Alvarez / Jun Ma / Gongpu Zhao / Juan R Perilla / Klaus Schulten / Peijun Zhang /  要旨: Chemotactic responses in bacteria require large, highly ordered arrays of sensory proteins to mediate the signal transduction that ultimately controls cell motility. A mechanistic understanding of ...Chemotactic responses in bacteria require large, highly ordered arrays of sensory proteins to mediate the signal transduction that ultimately controls cell motility. A mechanistic understanding of the molecular events underlying signaling, however, has been hampered by the lack of a high-resolution structural description of the extended array. Here, we report a novel reconstitution of the array, involving the receptor signaling domain, histidine kinase CheA, and adaptor protein CheW, as well as a density map of the core-signaling unit at 11.3 Å resolution, obtained by cryo-electron tomography and sub-tomogram averaging. Extracting key structural constraints from our density map, we computationally construct and refine an atomic model of the core array structure, exposing novel interfaces between the component proteins. Using all-atom molecular dynamics simulations, we further reveal a distinctive conformational change in CheA. Mutagenesis and chemical cross-linking experiments confirm the importance of the conformational dynamics of CheA for chemotactic function. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_6320.map.gz emd_6320.map.gz | 3.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-6320-v30.xml emd-6320-v30.xml emd-6320.xml emd-6320.xml | 13.4 KB 13.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_6320_fsc.xml emd_6320_fsc.xml | 3.8 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_6320.png emd_6320.png | 354.1 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-6320 http://ftp.pdbj.org/pub/emdb/structures/EMD-6320 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-6320 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-6320 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_6320.map.gz / 形式: CCP4 / 大きさ: 4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_6320.map.gz / 形式: CCP4 / 大きさ: 4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Structure of bacterial chemotaxis signaling CheA2-hexamer core complex by cryo-electron tomography and subvolume averaging | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 3.01 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : tarCF CheA CheW
| 全体 | 名称: tarCF CheA CheW |
|---|---|
| 要素 |
|
-超分子 #1000: tarCF CheA CheW
| 超分子 | 名称: tarCF CheA CheW / タイプ: sample / ID: 1000 集合状態: Hexamer of (CheA dimer, dimer of tarCF trimers of dimers, 2 CheW subunits) Number unique components: 3 |
|---|---|
| 分子量 | 理論値: 3.32 MDa |
-分子 #1: Chemotaxis protein CheA
| 分子 | 名称: Chemotaxis protein CheA / タイプ: protein_or_peptide / ID: 1 / Name.synonym: Bacterial Chemotaxis Histidine Kinase CheA / コピー数: 12 / 集合状態: Dimer / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli (大腸菌) / 細胞中の位置: Inner Membrane Escherichia coli (大腸菌) / 細胞中の位置: Inner Membrane |
| 分子量 | 理論値: 71.384 KDa |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) / 組換株: RP3098 / 組換プラスミド: pKJ9 Escherichia coli (大腸菌) / 組換株: RP3098 / 組換プラスミド: pKJ9 |
| 配列 | UniProtKB:  Chemotaxis protein CheA Chemotaxis protein CheA |
-分子 #2: Chemotaxis protein CheW
| 分子 | 名称: Chemotaxis protein CheW / タイプ: protein_or_peptide / ID: 2 / コピー数: 2 / 集合状態: monomeric / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli (大腸菌) / 細胞中の位置: Inner Membrane Escherichia coli (大腸菌) / 細胞中の位置: Inner Membrane |
| 分子量 | 理論値: 18.083 KDa |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) / 組換株: RP3098 / 組換プラスミド: PPA770 Escherichia coli (大腸菌) / 組換株: RP3098 / 組換プラスミド: PPA770 |
| 配列 | UniProtKB:  Chemotaxis protein CheW Chemotaxis protein CheW |
-分子 #3: Methyl-accepting chemotaxis protein II
| 分子 | 名称: Methyl-accepting chemotaxis protein II / タイプ: protein_or_peptide / ID: 3 / Name.synonym: tarCF 詳細: Cytoplasmic fragment of wild-type aspartate receptor コピー数: 6 / 集合状態: trimer of dimers / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli (大腸菌) / 細胞中の位置: Inner Membrane Escherichia coli (大腸菌) / 細胞中の位置: Inner Membrane |
| 分子量 | 理論値: 31.209 KDa |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) / 組換株: RP3098 / 組換プラスミド: pHTCF Escherichia coli (大腸菌) / 組換株: RP3098 / 組換プラスミド: pHTCF |
| 配列 | UniProtKB: Methyl-accepting chemotaxis protein II |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | サブトモグラム平均法 |
| 試料の集合状態 | 2D array |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 / 詳細: 75 mM Tris-HCl, 100 mM KCl, 5 mM MgCl2 |
|---|---|
| グリッド | 詳細: Perforated R2/2 Quantifoil grids precoated with 10 nm fiducial gold beads on the backside of the grid |
| 凍結 | 凍結剤: ETHANE / 装置: HOMEMADE PLUNGER 手法: Single-sided blotting to avoid disruption of the monolayer |
| 詳細 | Pseudo-crystalline 2D monolayer reconstituted on a lipid monolayer |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI POLARA 300 |
|---|---|
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 倍率(補正後): 49834 / 照射モード: SPOT SCAN / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.0 mm / 最大 デフォーカス(公称値): 8.0 µm / 最小 デフォーカス(公称値): 4.0 µm / 倍率(公称値): 39000 Bright-field microscopy / Cs: 2.0 mm / 最大 デフォーカス(公称値): 8.0 µm / 最小 デフォーカス(公称値): 4.0 µm / 倍率(公称値): 39000 |
| 試料ステージ | 試料ホルダーモデル: OTHER / Tilt series - Axis1 - Min angle: -70 ° / Tilt series - Axis1 - Max angle: 70 ° |
| 日付 | 2009年1月7日 |
| 撮影 | カテゴリ: CCD フィルム・検出器のモデル: GATAN ULTRASCAN 4000 (4k x 4k) 実像数: 60 / 平均電子線量: 60 e/Å2 / ビット/ピクセル: 16 |
| 実験機器 |  モデル: Tecnai Polara / 画像提供: FEI Company |
- 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | PDB ID: |
|---|---|
| 精密化 | 空間: REAL / プロトコル: FLEXIBLE FIT |
 ムービー
ムービー コントローラー
コントローラー