+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of Na+,K+-ATPase in the E2P state formed by ATP | |||||||||||||||||||||
 マップデータ マップデータ | ||||||||||||||||||||||
 試料 試料 |
| |||||||||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報regulation of monoatomic ion transport / P-type potassium transmembrane transporter activity / sodium:potassium-exchanging ATPase complex / ion channel regulator activity / sodium ion transport / monoatomic ion transport / potassium ion transport /  ATP hydrolysis activity / ATP hydrolysis activity /  ATP binding / ATP binding /  生体膜 ...regulation of monoatomic ion transport / P-type potassium transmembrane transporter activity / sodium:potassium-exchanging ATPase complex / ion channel regulator activity / sodium ion transport / monoatomic ion transport / potassium ion transport / 生体膜 ...regulation of monoatomic ion transport / P-type potassium transmembrane transporter activity / sodium:potassium-exchanging ATPase complex / ion channel regulator activity / sodium ion transport / monoatomic ion transport / potassium ion transport /  ATP hydrolysis activity / ATP hydrolysis activity /  ATP binding / ATP binding /  生体膜 / 生体膜 /  metal ion binding / metal ion binding /  細胞膜 細胞膜類似検索 - 分子機能 | |||||||||||||||||||||
| 生物種 |   Squalus acanthias (アブラツノザメ) / Squalus acanthias (アブラツノザメ) /   spiny dogfish (アブラツノザメ) spiny dogfish (アブラツノザメ) | |||||||||||||||||||||
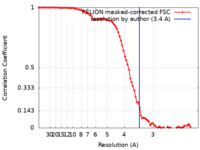
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.4 Å クライオ電子顕微鏡法 / 解像度: 3.4 Å | |||||||||||||||||||||
 データ登録者 データ登録者 | Kanai R / Cornelius F / Vilsen B / Toyoshima C | |||||||||||||||||||||
| 資金援助 |  日本, 日本,  デンマーク, 6件 デンマーク, 6件
| |||||||||||||||||||||
 引用 引用 |  ジャーナル: Proc Natl Acad Sci U S A / 年: 2022 ジャーナル: Proc Natl Acad Sci U S A / 年: 2022タイトル: Cryoelectron microscopy of Na,K-ATPase in the two E2P states with and without cardiotonic steroids. 著者: Ryuta Kanai / Flemming Cornelius / Bente Vilsen / Chikashi Toyoshima /   要旨: Cryoelectron microscopy (cryo-EM) was applied to Na+,K+-ATPase (NKA) to determine the structures of two E2P states, one (E2PATP) formed by ATP and Mg2+ in the forward reaction, and the other (E2PPi) ...Cryoelectron microscopy (cryo-EM) was applied to Na+,K+-ATPase (NKA) to determine the structures of two E2P states, one (E2PATP) formed by ATP and Mg2+ in the forward reaction, and the other (E2PPi) formed by inorganic phosphate (Pi) and Mg2+ in the backward reaction, with and without ouabain or istaroxime, representatives of classical and new-generation cardiotonic steroids (CTSs). These two E2P states exhibit different biochemical properties. In particular, K+-sensitive acceleration of the dephosphorylation reaction is not observed with E2PPi, attributed to the presence of a Mg2+ ion in the transmembrane cation binding sites. The cryo-EM structures of NKA demonstrate that the two E2P structures are nearly identical but Mg2+ in the transmembrane binding cavity is identified only in E2PPi, corroborating the idea that it should be denoted as E2PPi·Mg2+. We can now explain why the absence of transmembrane Mg2+ in E2PATP confers the K+ sensitivity in dephosphorylation. In addition, we show that ATP bridges the actuator (A) and nucleotide binding (N) domains, stabilizing the E2PATP state; CTS binding causes hardly any changes in the structure of NKA, both in E2PATP and E2PPi·Mg2+, indicating that the binding mechanism is conformational selection; and istaroxime binds to NKA, extending its aminoalkyloxime group deep into the cation binding site. This orientation is upside down compared to that of classical CTSs with respect to the steroid ring. Notably, mobile parts of NKA are resolved substantially better in the electron microscopy (EM) maps than in previous X-ray structures, including sugars sticking out from the β-subunit and many phospholipid molecules. | |||||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
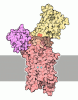
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_32894.map.gz emd_32894.map.gz | 48.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-32894-v30.xml emd-32894-v30.xml emd-32894.xml emd-32894.xml | 19.8 KB 19.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_32894_fsc.xml emd_32894_fsc.xml | 8.6 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_32894.png emd_32894.png | 136.5 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-32894 http://ftp.pdbj.org/pub/emdb/structures/EMD-32894 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-32894 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-32894 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7wyuMC  7wysC  7wytC  7wyvC  7wywC  7wyxC  7wyyC  7wyzC  7wz0C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_32894.map.gz / 形式: CCP4 / 大きさ: 52.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_32894.map.gz / 形式: CCP4 / 大きさ: 52.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.076 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
- 試料の構成要素
試料の構成要素
+全体 : Sodium/potassium-transporting ATPase
+超分子 #1: Sodium/potassium-transporting ATPase
+分子 #1: Sodium/potassium-transporting ATPase subunit alpha
+分子 #2: Na+,K+-ATPase beta subunit
+分子 #3: FXYD domain-containing ion transport regulator
+分子 #8: MAGNESIUM ION
+分子 #9: SODIUM ION
+分子 #10: ADENOSINE-5'-TRIPHOSPHATE
+分子 #11: CHOLESTEROL
+分子 #12: 1,2-DIOLEOYL-SN-GLYCERO-3-PHOSPHOCHOLINE
+分子 #13: water
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 1.5 mg/mL | |||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.5 構成要素:
| |||||||||||||||||||||
| グリッド | モデル: C-flat-1.2/1.3 / 材質: COPPER / メッシュ: 300 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY / 支持フィルム - Film thickness: 20.0 nm / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 雰囲気: AIR | |||||||||||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 99.9 % / チャンバー内温度: 279 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 50.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 1.0 µm Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 1.0 µm |
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 60.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー