+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM Structure of human ABCA7 in PE/Ch nanodiscs | |||||||||
 マップデータ マップデータ | human ABCA7 in Brain Polar Phosphatidylethanolamine (PE)/Cholesterol (Ch) nanodiscs | |||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報plasma membrane raft organization / apolipoprotein A-I receptor activity / positive regulation of engulfment of apoptotic cell / phospholipid transporter activity / negative regulation of amyloid precursor protein biosynthetic process /  ABC transporters in lipid homeostasis / ABC transporters in lipid homeostasis /  floppase activity / phosphatidylserine floppase activity / amyloid-beta clearance by cellular catabolic process / positive regulation of phospholipid efflux ...plasma membrane raft organization / apolipoprotein A-I receptor activity / positive regulation of engulfment of apoptotic cell / phospholipid transporter activity / negative regulation of amyloid precursor protein biosynthetic process / floppase activity / phosphatidylserine floppase activity / amyloid-beta clearance by cellular catabolic process / positive regulation of phospholipid efflux ...plasma membrane raft organization / apolipoprotein A-I receptor activity / positive regulation of engulfment of apoptotic cell / phospholipid transporter activity / negative regulation of amyloid precursor protein biosynthetic process /  ABC transporters in lipid homeostasis / ABC transporters in lipid homeostasis /  floppase activity / phosphatidylserine floppase activity / amyloid-beta clearance by cellular catabolic process / positive regulation of phospholipid efflux / peptide cross-linking / phosphatidylcholine floppase activity / phospholipid efflux / negative regulation of endocytosis / positive regulation of amyloid-beta clearance / high-density lipoprotein particle assembly / positive regulation of protein localization to cell surface / P-type phospholipid transporter / apolipoprotein A-I-mediated signaling pathway / regulation of amyloid precursor protein catabolic process / phospholipid translocation / cholesterol efflux / phagocytic cup / negative regulation of MAPK cascade / negative regulation of PERK-mediated unfolded protein response / negative regulation of amyloid-beta formation / glial cell projection / amyloid-beta formation / regulation of lipid metabolic process / protein localization to nucleus / ATPase-coupled transmembrane transporter activity / positive regulation of cholesterol efflux / ABC-type transporter activity / floppase activity / phosphatidylserine floppase activity / amyloid-beta clearance by cellular catabolic process / positive regulation of phospholipid efflux / peptide cross-linking / phosphatidylcholine floppase activity / phospholipid efflux / negative regulation of endocytosis / positive regulation of amyloid-beta clearance / high-density lipoprotein particle assembly / positive regulation of protein localization to cell surface / P-type phospholipid transporter / apolipoprotein A-I-mediated signaling pathway / regulation of amyloid precursor protein catabolic process / phospholipid translocation / cholesterol efflux / phagocytic cup / negative regulation of MAPK cascade / negative regulation of PERK-mediated unfolded protein response / negative regulation of amyloid-beta formation / glial cell projection / amyloid-beta formation / regulation of lipid metabolic process / protein localization to nucleus / ATPase-coupled transmembrane transporter activity / positive regulation of cholesterol efflux / ABC-type transporter activity /  食作用 / positive regulation of phagocytosis / 食作用 / positive regulation of phagocytosis /  visual learning / visual learning /  記憶 / ruffle membrane / 記憶 / ruffle membrane /  細胞結合 / early endosome membrane / positive regulation of ERK1 and ERK2 cascade / 細胞結合 / early endosome membrane / positive regulation of ERK1 and ERK2 cascade /  ゴルジ体 / intracellular membrane-bounded organelle / ゴルジ体 / intracellular membrane-bounded organelle /  ゴルジ体 / ゴルジ体 /  細胞膜 / 細胞膜 /  小胞体 / 小胞体 /  ATP hydrolysis activity / ATP hydrolysis activity /  ATP binding / ATP binding /  細胞膜 細胞膜類似検索 - 分子機能 | |||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 4.0 Å クライオ電子顕微鏡法 / 解像度: 4.0 Å | |||||||||
 データ登録者 データ登録者 | Alam A / Le LTM / Thompson JR | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: EMBO J / 年: 2023 ジャーナル: EMBO J / 年: 2023タイトル: Cryo-EM structures of human ABCA7 provide insights into its phospholipid translocation mechanisms. 著者: Le Thi My Le / James Robert Thompson / Sepehr Dehghani-Ghahnaviyeh / Shashank Pant / Phuoc Xuan Dang / Jarrod Bradley French / Takahisa Kanikeyo / Emad Tajkhorshid / Amer Alam /  要旨: Phospholipid extrusion by ABC subfamily A (ABCA) exporters is central to cellular physiology, although the specifics of the underlying substrate interactions and transport mechanisms remain poorly ...Phospholipid extrusion by ABC subfamily A (ABCA) exporters is central to cellular physiology, although the specifics of the underlying substrate interactions and transport mechanisms remain poorly resolved at the molecular level. Here we report cryo-EM structures of lipid-embedded human ABCA7 in an open state and in a nucleotide-bound, closed state at resolutions between 3.6 and 4.0 Å. The former reveals an ordered patch of bilayer lipids traversing the transmembrane domain (TMD), while the latter reveals a lipid-free, closed TMD with a small extracellular opening. These structures offer a structural framework for both substrate entry and exit from the ABCA7 TMD and highlight conserved rigid-body motions that underlie the associated conformational transitions. Combined with functional analysis and molecular dynamics (MD) simulations, our data also shed light on lipid partitioning into the ABCA7 TMD and localized membrane perturbations that underlie ABCA7 function and have broader implications for other ABCA family transporters. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_28047.map.gz emd_28047.map.gz | 202.2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-28047-v30.xml emd-28047-v30.xml emd-28047.xml emd-28047.xml | 21.9 KB 21.9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_28047.png emd_28047.png | 42.9 KB | ||
| その他 |  emd_28047_additional_1.map.gz emd_28047_additional_1.map.gz emd_28047_half_map_1.map.gz emd_28047_half_map_1.map.gz emd_28047_half_map_2.map.gz emd_28047_half_map_2.map.gz | 128.5 MB 171.1 MB 171 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-28047 http://ftp.pdbj.org/pub/emdb/structures/EMD-28047 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-28047 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-28047 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_28047.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_28047.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | human ABCA7 in Brain Polar Phosphatidylethanolamine (PE)/Cholesterol (Ch) nanodiscs | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.889 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-追加マップ: Local Resolution filtered map of human ABCA7 in...
| ファイル | emd_28047_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Local Resolution filtered map of human ABCA7 in Brain Polar Phosphatidylethanolamine (PE)/Cholesterol (Ch) nanodiscs | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
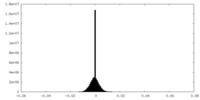
| 密度ヒストグラム |
-ハーフマップ: Refinement half Map 1
| ファイル | emd_28047_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Refinement half Map 1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
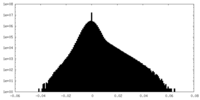
| 密度ヒストグラム |
-ハーフマップ: Refinement half Map 2
| ファイル | emd_28047_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Refinement half Map 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Human ABCA7 in Porcine BPL/Ch/MSP1D1 nanodiscs
| 全体 | 名称: Human ABCA7 in Porcine BPL/Ch/MSP1D1 nanodiscs |
|---|---|
| 要素 |
|
-超分子 #1: Human ABCA7 in Porcine BPL/Ch/MSP1D1 nanodiscs
| 超分子 | 名称: Human ABCA7 in Porcine BPL/Ch/MSP1D1 nanodiscs / タイプ: complex / ID: 1 / キメラ: Yes / 親要素: 0 / 含まれる分子: #1 詳細: Human ABCA7 recombinantly expressed in HEK293 TREX cell line and reconstituted in MSP1D1 nanodiscs comprising 4:1 mixture of Porcine Brain Polar Lipids:Cholesterol |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 234.35 KDa |
-分子 #1: Phospholipid-transporting ATPase ABCA7
| 分子 | 名称: Phospholipid-transporting ATPase ABCA7 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO / EC番号: P-type phospholipid transporter |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 234.598578 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MAFWTQLMLL LWKNFMYRRR QPVQLLVELL WPLFLFFILV AVRHSHPPLE HHECHFPNKP LPSAGTVPWL QGLICNVNNT CFPQLTPGE EPGRLSNFND SLVSRLLADA RTVLGGASAH RTLAGLGKLI ATLRAARSTA QPQPTKQSPL EPPMLDVAEL L TSLLRTES ...文字列: MAFWTQLMLL LWKNFMYRRR QPVQLLVELL WPLFLFFILV AVRHSHPPLE HHECHFPNKP LPSAGTVPWL QGLICNVNNT CFPQLTPGE EPGRLSNFND SLVSRLLADA RTVLGGASAH RTLAGLGKLI ATLRAARSTA QPQPTKQSPL EPPMLDVAEL L TSLLRTES LGLALGQAQE PLHSLLEAAE DLAQELLALR SLVELRALLQ RPRGTSGPLE LLSEALCSVR GPSSTVGPSL NW YEASDLM ELVGQEPESA LPDSSLSPAC SELIGALDSH PLSRLLWRRL KPLILGKLLF APDTPFTRKL MAQVNRTFEE LTL LRDVRE VWEMLGPRIF TFMNDSSNVA MLQRLLQMQD EGRRQPRPGG RDHMEALRSF LDPGSGGYSW QDAHADVGHL VGTL GRVTE CLSLDKLEAA PSEAALVSRA LQLLAEHRFW AGVVFLGPED SSDPTEHPTP DLGPGHVRIK IRMDIDVVTR TNKIR DRFW DPGPAADPLT DLRYVWGGFV YLQDLVERAA VRVLSGANPR AGLYLQQMPY PCYVDDVFLR VLSRSLPLFL TLAWIY SVT LTVKAVVREK ETRLRDTMRA MGLSRAVLWL GWFLSCLGPF LLSAALLVLV LKLGDILPYS HPGVVFLFLA AFAVATV TQ SFLLSAFFSR ANLAAACGGL AYFSLYLPYV LCVAWRDRLP AGGRVAASLL SPVAFGFGCE SLALLEEQGE GAQWHNVG T RPTADVFSLA QVSGLLLLDA ALYGLATWYL EAVCPGQYGI PEPWNFPFRR SYWCGPRPPK SPAPCPTPLD PKVLVEEAP PGLSPGVSVR SLEKRFPGSP QPALRGLSLD FYQGHITAFL GHNGAGKTTT LSILSGLFPP SGGSAFILGH DVRSSMAAIR PHLGVCPQY NVLFDMLTVD EHVWFYGRLK GLSAAVVGPE QDRLLQDVGL VSKQSVQTRH LSGGMQRKLS VAIAFVGGSQ V VILDEPTA GVDPASRRGI WELLLKYREG RTLILSTHHL DEAELLGDRV AVVAGGRLCC CGSPLFLRRH LGSGYYLTLV KA RLPLTTN EKADTDMEGS VDTRQEKKNG SQGSRVGTPQ LLALVQHWVP GARLVEELPH ELVLVLPYTG AHDGSFATLF REL DTRLAE LRLTGYGISD TSLEEIFLKV VEECAADTDM EDGSCGQHLC TGIAGLDVTL RLKMPPQETA LENGEPAGSA PETD QGSGP DAVGRVQGWA LTRQQLQALL LKRFLLARRS RRGLFAQIVL PALFVGLALV FSLIVPPFGH YPALRLSPTM YGAQV SFFS EDAPGDPGRA RLLEALLQEA GLEEPPVQHS SHRFSAPEVP AEVAKVLASG NWTPESPSPA CQCSRPGARR LLPDCP AAA GGPPPPQAVT GSGEVVQNLT GRNLSDFLVK TYPRLVRQGL KTKKWVNEVR YGGFSLGGRD PGLPSGQELG RSVEELW AL LSPLPGGALD RVLKNLTAWA HSLDAQDSLK IWFNNKGWHS MVAFVNRASN AILRAHLPPG PARHAHSITT LNHPLNLT K EQLSEGALMA SSVDVLVSIC VVFAMSFVPA SFTLVLIEER VTRAKHLQLM GGLSPTLYWL GNFLWDMCNY LVPACIVVL IFLAFQQRAY VAPANLPALL LLLLLYGWSI TPLMYPASFF FSVPSTAYVV LTCINLFIGI NGSMATFVLE LFSDQKLQEV SRILKQVFL IFPHFCLGRG LIDMVRNQAM ADAFERLGDR QFQSPLRWEV VGKNLLAMVI QGPLFLLFTL LLQHRSQLLP Q PRVRSLPL LGEEDEDVAR ERERVVQGAT QGDVLVLRNL TKVYRGQRMP AVDRLCLGIP PGECFGLLGV NGAGKTSTFR MV TGDTLAS RGEAVLAGHS VAREPSAAHL SMGYCPQSDA IFELLTGREH LELLARLRGV PEAQVAQTAG SGLARLGLSW YAD RPAGTY SGGNKRKLAT ALALVGDPAV VFLDEPTTGM DPSARRFLWN SLLAVVREGR SVMLTSHSME ECEALCSRLA IMVN GRFRC LGSPQHLKGR FAAGHTLTLR VPAARSQPAA AFVAAEFPGA ELREAHGGRL RFQLPPGGRC ALARVFGELA VHGAE HGVE DFSVSQTMLE EVFLYFSKDQ GKDEDTEEQK EAGVGVDPAP GLQHPKRVSQ FLDDPSTAET VL |
-分子 #4: 2-acetamido-2-deoxy-beta-D-glucopyranose
| 分子 | 名称: 2-acetamido-2-deoxy-beta-D-glucopyranose / タイプ: ligand / ID: 4 / コピー数: 5 / 式: NAG |
|---|---|
| 分子量 | 理論値: 221.208 Da |
| Chemical component information |  ChemComp-NAG: |
-分子 #5: UNKNOWN LIGAND
| 分子 | 名称: UNKNOWN LIGAND / タイプ: ligand / ID: 5 / コピー数: 20 / 式: UNL |
|---|---|
| 分子量 | 理論値: 622.834 Da |
| Chemical component information | 
ChemComp-UNL: |
-分子 #6: PHOSPHOTHIOPHOSPHORIC ACID-ADENYLATE ESTER
| 分子 | 名称: PHOSPHOTHIOPHOSPHORIC ACID-ADENYLATE ESTER / タイプ: ligand / ID: 6 / コピー数: 2 / 式: AGS |
|---|---|
| 分子量 | 理論値: 523.247 Da |
| Chemical component information |  ChemComp-AGS: |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.5 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 詳細: 25mM HEPES pH 7.5, 150mM NaCl, 5mM ATP gammaS, 10mM Magnesium Chloride |
| グリッド | モデル: Quantifoil R1.2/1.3 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 90 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / 最大 デフォーカス(公称値): 2.4 µm / 最小 デフォーカス(公称値): 0.8 µm Bright-field microscopy / 最大 デフォーカス(公称値): 2.4 µm / 最小 デフォーカス(公称値): 0.8 µm |
| 撮影 | フィルム・検出器のモデル: FEI FALCON III (4k x 4k) 検出モード: COUNTING / 平均露光時間: 60.0 sec. / 平均電子線量: 60.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: EMDB MAP EMDB ID: |
|---|---|
| 初期 角度割当 | タイプ: PROJECTION MATCHING / ソフトウェア - 名称: RELION (ver. 3.1) |
| 最終 3次元分類 | クラス数: 1 / ソフトウェア - 名称: RELION (ver. 3.1/4.0) |
| 最終 角度割当 | タイプ: PROJECTION MATCHING / ソフトウェア - 名称: RELION (ver. 3.1) |
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 4.0 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: RELION (ver. 3.1/4.0) / 使用した粒子像数: 50704 |
 ムービー
ムービー コントローラー
コントローラー















 Z
Z Y
Y X
X