+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-23495 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM of the SLFN12-PDE3A complex: Consensus subset model | |||||||||
 マップデータ マップデータ | Primary Relion refinement output | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード |  complex / velcrin / complex / velcrin /  molecular glue / DNMDP / molecular glue / DNMDP /  RNA BINDING PROTEIN (RNA結合タンパク質) RNA BINDING PROTEIN (RNA結合タンパク質) | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報cGMP-inhibited cyclic-nucleotide phosphodiesterase activity /  estrogen binding / estrogen binding /  regulation of ribonuclease activity / positive regulation of oocyte development / regulation of meiotic nuclear division / rRNA catabolic process / cellular response to cGMP / regulation of ribonuclease activity / positive regulation of oocyte development / regulation of meiotic nuclear division / rRNA catabolic process / cellular response to cGMP /  oocyte maturation / positive regulation of vascular permeability / negative regulation of vascular permeability ...cGMP-inhibited cyclic-nucleotide phosphodiesterase activity / oocyte maturation / positive regulation of vascular permeability / negative regulation of vascular permeability ...cGMP-inhibited cyclic-nucleotide phosphodiesterase activity /  estrogen binding / estrogen binding /  regulation of ribonuclease activity / positive regulation of oocyte development / regulation of meiotic nuclear division / rRNA catabolic process / cellular response to cGMP / regulation of ribonuclease activity / positive regulation of oocyte development / regulation of meiotic nuclear division / rRNA catabolic process / cellular response to cGMP /  oocyte maturation / positive regulation of vascular permeability / negative regulation of vascular permeability / negative regulation of cAMP-mediated signaling / oocyte maturation / positive regulation of vascular permeability / negative regulation of vascular permeability / negative regulation of cAMP-mediated signaling /  3',5'-cyclic-nucleotide phosphodiesterase / cGMP-mediated signaling / nuclear estrogen receptor activity / 3',5'-cyclic-nucleotide phosphodiesterase / cGMP-mediated signaling / nuclear estrogen receptor activity /  3',5'-cyclic-GMP phosphodiesterase activity / cAMP-mediated signaling / 3',5'-cyclic-GMP phosphodiesterase activity / cAMP-mediated signaling /  3',5'-cyclic-nucleotide phosphodiesterase activity / 3',5'-cyclic-nucleotide phosphodiesterase activity /  3',5'-cyclic-AMP phosphodiesterase activity / RNA nuclease activity / cellular response to transforming growth factor beta stimulus / apoptotic signaling pathway / lipid metabolic process / 3',5'-cyclic-AMP phosphodiesterase activity / RNA nuclease activity / cellular response to transforming growth factor beta stimulus / apoptotic signaling pathway / lipid metabolic process /  ribosome binding / G alpha (s) signalling events / ribosome binding / G alpha (s) signalling events /  加水分解酵素; エステル加水分解酵素 / response to xenobiotic stimulus / G protein-coupled receptor signaling pathway / negative regulation of apoptotic process / 加水分解酵素; エステル加水分解酵素 / response to xenobiotic stimulus / G protein-coupled receptor signaling pathway / negative regulation of apoptotic process /  生体膜 / 生体膜 /  metal ion binding / metal ion binding /  細胞核 / 細胞核 /  細胞質基質 細胞質基質類似検索 - 分子機能 | |||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
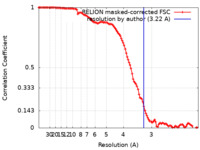
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.22 Å クライオ電子顕微鏡法 / 解像度: 3.22 Å | |||||||||
 データ登録者 データ登録者 | Fuller JR / Garvie CW / Lemke CT | |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2021 ジャーナル: Nat Commun / 年: 2021タイトル: Structure of PDE3A-SLFN12 complex reveals requirements for activation of SLFN12 RNase. 著者: Colin W Garvie / Xiaoyun Wu / Malvina Papanastasiou / Sooncheol Lee / James Fuller / Gavin R Schnitzler / Steven W Horner / Andrew Baker / Terry Zhang / James P Mullahoo / Lindsay Westlake / ...著者: Colin W Garvie / Xiaoyun Wu / Malvina Papanastasiou / Sooncheol Lee / James Fuller / Gavin R Schnitzler / Steven W Horner / Andrew Baker / Terry Zhang / James P Mullahoo / Lindsay Westlake / Stephanie H Hoyt / Marcus Toetzl / Matthew J Ranaghan / Luc de Waal / Joseph McGaunn / Bethany Kaplan / Federica Piccioni / Xiaoping Yang / Martin Lange / Adrian Tersteegen / Donald Raymond / Timothy A Lewis / Steven A Carr / Andrew D Cherniack / Christopher T Lemke / Matthew Meyerson / Heidi Greulich /   要旨: DNMDP and related compounds, or velcrins, induce complex formation between the phosphodiesterase PDE3A and the SLFN12 protein, leading to a cytotoxic response in cancer cells that express elevated ...DNMDP and related compounds, or velcrins, induce complex formation between the phosphodiesterase PDE3A and the SLFN12 protein, leading to a cytotoxic response in cancer cells that express elevated levels of both proteins. The mechanisms by which velcrins induce complex formation, and how the PDE3A-SLFN12 complex causes cancer cell death, are not fully understood. Here, we show that PDE3A and SLFN12 form a heterotetramer stabilized by binding of DNMDP. Interactions between the C-terminal alpha helix of SLFN12 and residues near the active site of PDE3A are required for complex formation, and are further stabilized by interactions between SLFN12 and DNMDP. Moreover, we demonstrate that SLFN12 is an RNase, that PDE3A binding increases SLFN12 RNase activity, and that SLFN12 RNase activity is required for DNMDP response. This new mechanistic understanding will facilitate development of velcrin compounds into new cancer therapies. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_23495.map.gz emd_23495.map.gz | 100.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-23495-v30.xml emd-23495-v30.xml emd-23495.xml emd-23495.xml | 25.7 KB 25.7 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_23495_fsc.xml emd_23495_fsc.xml | 11.5 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_23495.png emd_23495.png | 88.9 KB | ||
| マスクデータ |  emd_23495_msk_1.map emd_23495_msk_1.map | 129.7 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-23495.cif.gz emd-23495.cif.gz | 7.8 KB | ||
| その他 |  emd_23495_additional_1.map.gz emd_23495_additional_1.map.gz emd_23495_half_map_1.map.gz emd_23495_half_map_1.map.gz emd_23495_half_map_2.map.gz emd_23495_half_map_2.map.gz | 76.4 MB 100.7 MB 100.9 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-23495 http://ftp.pdbj.org/pub/emdb/structures/EMD-23495 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-23495 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-23495 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_23495.map.gz / 形式: CCP4 / 大きさ: 129.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_23495.map.gz / 形式: CCP4 / 大きさ: 129.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Primary Relion refinement output | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.063 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_23495_msk_1.map emd_23495_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
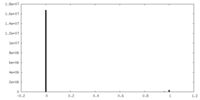
| 投影像・断面図 |
| ||||||||||||
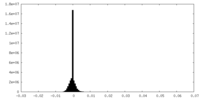
| 密度ヒストグラム |
-追加マップ: Primary map, sharpened by an automatically-determined B-factor (-98.5043)...
| ファイル | emd_23495_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Primary map, sharpened by an automatically-determined B-factor (-98.5043) and filtered to local resolution, using the Relion local resolution implementation. | ||||||||||||
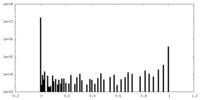
| 投影像・断面図 |
| ||||||||||||
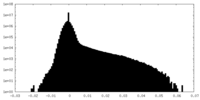
| 密度ヒストグラム |
-ハーフマップ: Half-map 2 from Relion refinement
| ファイル | emd_23495_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half-map 2 from Relion refinement | ||||||||||||
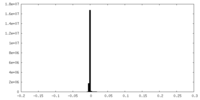
| 投影像・断面図 |
| ||||||||||||
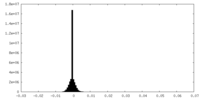
| 密度ヒストグラム |
-ハーフマップ: Half-map 1 from Relion refinement
| ファイル | emd_23495_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half-map 1 from Relion refinement | ||||||||||||
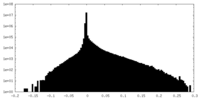
| 投影像・断面図 |
| ||||||||||||
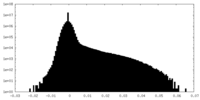
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : SLFN12-PDE3A complex, consensus subset model
| 全体 | 名称: SLFN12-PDE3A complex, consensus subset model |
|---|---|
| 要素 |
|
-超分子 #1: SLFN12-PDE3A complex, consensus subset model
| 超分子 | 名称: SLFN12-PDE3A complex, consensus subset model / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: Schlafen family member 12
| 分子 | 名称: Schlafen family member 12 / タイプ: protein_or_peptide / ID: 1 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 67.383734 KDa |
| 組換発現 | 生物種:  unidentified baculovirus (ウイルス) unidentified baculovirus (ウイルス) |
| 配列 | 文字列: GGGGSMNISV DLETNYAELV LDVGRVTLGE NSRKKMKDCK LRKKQNESVS RAMCALLNSG GGVIKAEIEN EDYSYTKDGI GLDLENSFS NILLFVPEYL DFMQNGNYFL IFVKSWSLNT SGLRITTLSS NLYKRDITSA KVMNATAALE FLKDMKKTRG R LYLRPELL ...文字列: GGGGSMNISV DLETNYAELV LDVGRVTLGE NSRKKMKDCK LRKKQNESVS RAMCALLNSG GGVIKAEIEN EDYSYTKDGI GLDLENSFS NILLFVPEYL DFMQNGNYFL IFVKSWSLNT SGLRITTLSS NLYKRDITSA KVMNATAALE FLKDMKKTRG R LYLRPELL AKRPCVDIQE ENNMKALAGV FFDRTELDRK EKLTFTESTH VEIKNFSTEK LLQRIKEILP QYVSAFANTD GG YLFIGLN EDKEIIGFKA EMSDLDDLER EIEKSIRKMP VHHFCMEKKK INYSCKFLGV YDKGSLCGYV CALRVERFCC AVF AKEPDS WHVKDNRVMQ LTRKEWIQFM VEAEPKFSSS YEEVISQINT SLPAPHSWPL LEWQRQRHHC PGLSGRITYT PENL CRKLF LQHEGLKQLI CEEMDSVRKG SLIFSRSWSV DLGLQENHKV LCDALLISQD SPPVLYTFHM VQDEEFKGYS TQTAL TLKQ KLAKIGGYTK KVCVMTKIFY LSPEGMTSCQ YDLRSQVIYP ESYYFTRRKY LLKALFKALK RLKSLRDQFS FAENLY QII GIDCFQKNDK KMFKSCRRLT UniProtKB: Ribonuclease SLFN12 |
-分子 #2: cGMP-inhibited 3',5'-cyclic phosphodiesterase A
| 分子 | 名称: cGMP-inhibited 3',5'-cyclic phosphodiesterase A / タイプ: protein_or_peptide / ID: 2 / コピー数: 2 / 光学異性体: LEVO / EC番号:  3',5'-cyclic-nucleotide phosphodiesterase 3',5'-cyclic-nucleotide phosphodiesterase |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 57.352996 KDa |
| 組換発現 | 生物種:  unidentified baculovirus (ウイルス) unidentified baculovirus (ウイルス) |
| 配列 | 文字列: GEDETECLRE PLRKASACST YAPETMMFLD KPILAPEPLV MDNLDSIMEQ LNTWNFPIFD LVENIGRKCG RILSQVSYRL FEDMGLFEA FKIPIREFMN YFHALEIGYR DIPYHNRIHA TDVLHAVWYL TTQPIPGLST VINDHGSTSD SDSDSGFTHG H MGYVFSKT ...文字列: GEDETECLRE PLRKASACST YAPETMMFLD KPILAPEPLV MDNLDSIMEQ LNTWNFPIFD LVENIGRKCG RILSQVSYRL FEDMGLFEA FKIPIREFMN YFHALEIGYR DIPYHNRIHA TDVLHAVWYL TTQPIPGLST VINDHGSTSD SDSDSGFTHG H MGYVFSKT YNVTDDKYGC LSGNIPALEL MALYVAAAMH DYDHPGRTNA FLVATSAPQA VLYNDRSVLE NHHAAAAWNL FM SRPEYNF LINLDHVEFK HFRFLVIEAI LATDLKKHFD FVAKFNGKVN DDVGIDWTNE NDRLLVCQMC IKLADINGPA KCK ELHLQW TDGIVNEFYE QGDEEASLGL PISPFMDRSA PQLANLQESF ISHIVGPLCN SYDSAGLMPG KWVEDSDESG DTDD PEEEE EEAPAPNEEE TCENNESPKK KTFKRRKIYC QITQHLLQNH KMWKKVIEEE QRLAGIENQS LDQTPQSHSS EQIQA IKEE EEEKGKPRGE EIPTQKPDQ UniProtKB: cGMP-inhibited 3',5'-cyclic phosphodiesterase 3A |
-分子 #3: ZINC ION
| 分子 | 名称: ZINC ION / タイプ: ligand / ID: 3 / コピー数: 2 / 式: ZN |
|---|---|
| 分子量 | 理論値: 65.409 Da |
-分子 #4: MANGANESE (II) ION
| 分子 | 名称: MANGANESE (II) ION / タイプ: ligand / ID: 4 / コピー数: 2 / 式: MN |
|---|---|
| 分子量 | 理論値: 54.938 Da |
-分子 #5: MAGNESIUM ION
| 分子 | 名称: MAGNESIUM ION / タイプ: ligand / ID: 5 / コピー数: 2 / 式: MG |
|---|---|
| 分子量 | 理論値: 24.305 Da |
-分子 #6: (4~{R})-3-[4-(diethylamino)-3-[oxidanyl(oxidanylidene)-$l^{4}-aza...
| 分子 | 名称: (4~{R})-3-[4-(diethylamino)-3-[oxidanyl(oxidanylidene)-$l^{4}-azanyl]phenyl]-4-methyl-4,5-dihydro-1~{H}-pyridazin-6-one タイプ: ligand / ID: 6 / コピー数: 2 / 式: X5M |
|---|---|
| 分子量 | 理論値: 305.352 Da |
| Chemical component information | 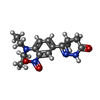 ChemComp-X5M: |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.6 mg/mL | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.4 構成要素:
詳細: 0.0038% NP-40s detergent (CAS 9016-45-9) added immediately prior to plunge freezing | |||||||||||||||
| グリッド | モデル: C-flat / 材質: GOLD / メッシュ: 400 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY ARRAY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 45 sec. / 前処理 - 雰囲気: AIR | |||||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 291 K / 装置: FEI VITROBOT MARK IV / 詳細: 4.5 second blot time. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 70.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.7 mm / 倍率(公称値): 81000 Bright-field microscopy / Cs: 2.7 mm / 倍率(公称値): 81000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) デジタル化 - サイズ - 横: 5760 pixel / デジタル化 - サイズ - 縦: 4092 pixel / 撮影したグリッド数: 1 / 実像数: 3163 / 平均電子線量: 50.0 e/Å2 詳細: Exposures were collected in super-resolution mode, as movies fractionated over 40 frames |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | PDB ID: Chain - Source name: PDB / Chain - Initial model type: experimental model |
|---|---|
| 詳細 | The model was generated by rigid body fitting of the SLFN12 and PDE3A bodies (from multi-body refinement and deposited separately) into this map using UCSF Chimera and Coot, followed by local refinement in Coot of the linkers between the bodies to ameliorate backbone geometry. |
| 精密化 | 空間: REAL |
| 得られたモデル |  PDB-7lrd: |
 ムービー
ムービー コントローラー
コントローラー




















 Z
Z Y
Y X
X