+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-22288 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
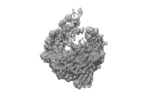
| タイトル | SARS-CoV-2 RdRp/RNA complex | |||||||||
 マップデータ マップデータ | SARS-CoV-2 RdRp/RNA complex | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | SARS-CoV-2 / RNA polymerase / nsp12 / nsp7 / nsp8 / VIRAL PROTEIN / TRANSFERASE-HYDROLASE complex | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報protein guanylyltransferase activity / RNA endonuclease activity producing 3'-phosphomonoesters, hydrolytic mechanism / mRNA guanylyltransferase activity / 5'-3' RNA helicase activity / 付加脱離酵素(リアーゼ); P-Oリアーゼ類; - / Assembly of the SARS-CoV-2 Replication-Transcription Complex (RTC) / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of TBK1 activity / Maturation of replicase proteins / ISG15-specific peptidase activity / TRAF3-dependent IRF activation pathway ...protein guanylyltransferase activity / RNA endonuclease activity producing 3'-phosphomonoesters, hydrolytic mechanism / mRNA guanylyltransferase activity / 5'-3' RNA helicase activity / 付加脱離酵素(リアーゼ); P-Oリアーゼ類; - / Assembly of the SARS-CoV-2 Replication-Transcription Complex (RTC) / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of TBK1 activity / Maturation of replicase proteins / ISG15-specific peptidase activity / TRAF3-dependent IRF activation pathway / Transcription of SARS-CoV-2 sgRNAs / snRNP Assembly / Translation of Replicase and Assembly of the Replication Transcription Complex / Replication of the SARS-CoV-2 genome / 加水分解酵素; エステル加水分解酵素; 5'-リン酸モノエステル産生エキソリボヌクレアーゼ / host cell endoplasmic reticulum-Golgi intermediate compartment / double membrane vesicle viral factory outer membrane / 3'-5'-RNA exonuclease activity / 5'-3' DNA helicase activity / SARS coronavirus main proteinase / host cell endosome / symbiont-mediated degradation of host mRNA / mRNA guanylyltransferase / symbiont-mediated suppression of host ISG15-protein conjugation / symbiont-mediated suppression of host toll-like receptor signaling pathway / G-quadruplex RNA binding / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of IRF3 activity / omega peptidase activity / SARS-CoV-2 modulates host translation machinery / mRNA (guanine-N7)-methyltransferase / methyltransferase cap1 / host cell Golgi apparatus / symbiont-mediated suppression of host NF-kappaB cascade / symbiont-mediated perturbation of host ubiquitin-like protein modification / DNA helicase / methyltransferase cap1 activity / ubiquitinyl hydrolase 1 / mRNA 5'-cap (guanine-N7-)-methyltransferase activity / cysteine-type deubiquitinase activity / forked DNA-dependent helicase activity / single-stranded 3'-5' DNA helicase activity / four-way junction helicase activity / double-stranded DNA helicase activity / 加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素; システインプロテアーゼ / single-stranded RNA binding / host cell perinuclear region of cytoplasm / regulation of autophagy / viral protein processing / lyase activity / host cell endoplasmic reticulum membrane / RNA helicase / symbiont-mediated suppression of host type I interferon-mediated signaling pathway / symbiont-mediated suppression of host gene expression / copper ion binding / viral translational frameshifting / symbiont-mediated activation of host autophagy / RNA-directed RNA polymerase / cysteine-type endopeptidase activity / viral RNA genome replication / RNA-directed RNA polymerase activity / DNA-templated transcription / lipid binding / host cell nucleus / SARS-CoV-2 activates/modulates innate and adaptive immune responses / ATP hydrolysis activity / proteolysis / RNA binding / zinc ion binding / ATP binding / membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.4 Å | |||||||||
 データ登録者 データ登録者 | Liu B / Shi W | |||||||||
 引用 引用 |  ジャーナル: To Be Published ジャーナル: To Be Publishedタイトル: Structure of SARS-CoV-2 RdRp/RNA complex at 3.4 Angstroms resolution 著者: Liu B / Shi W / Yang Y | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_22288.map.gz emd_22288.map.gz | 19.3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-22288-v30.xml emd-22288-v30.xml emd-22288.xml emd-22288.xml | 16.3 KB 16.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_22288.png emd_22288.png | 52 KB | ||
| Filedesc metadata |  emd-22288.cif.gz emd-22288.cif.gz | 6.3 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-22288 http://ftp.pdbj.org/pub/emdb/structures/EMD-22288 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-22288 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-22288 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_22288_validation.pdf.gz emd_22288_validation.pdf.gz | 460.7 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_22288_full_validation.pdf.gz emd_22288_full_validation.pdf.gz | 460.3 KB | 表示 | |
| XML形式データ |  emd_22288_validation.xml.gz emd_22288_validation.xml.gz | 6 KB | 表示 | |
| CIF形式データ |  emd_22288_validation.cif.gz emd_22288_validation.cif.gz | 6.8 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22288 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22288 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22288 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-22288 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_22288.map.gz / 形式: CCP4 / 大きさ: 38.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_22288.map.gz / 形式: CCP4 / 大きさ: 38.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | SARS-CoV-2 RdRp/RNA complex | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.89 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : SARS-CoV-2 RdRp/RNA complex
| 全体 | 名称: SARS-CoV-2 RdRp/RNA complex |
|---|---|
| 要素 |
|
-超分子 #1: SARS-CoV-2 RdRp/RNA complex
| 超分子 | 名称: SARS-CoV-2 RdRp/RNA complex / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#4 |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 160 KDa |
-分子 #1: RNA-directed RNA polymerase
| 分子 | 名称: RNA-directed RNA polymerase / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO / EC番号: RNA-directed RNA polymerase |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 107.983328 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MSADAQSFLN RVCGVSAARL TPCGTGTSTD VVYRAFDIYN DKVAGFAKFL KTNCCRFQEK DEDDNLIDSY FVVKRHTFSN YQHEETIYN LLKDCPAVAK HDFFKFRIDG DMVPHISRQR LTKYTMADLV YALRHFDEGN CDTLKEILVT YNCCDDDYFN K KDWYDFVE ...文字列: MSADAQSFLN RVCGVSAARL TPCGTGTSTD VVYRAFDIYN DKVAGFAKFL KTNCCRFQEK DEDDNLIDSY FVVKRHTFSN YQHEETIYN LLKDCPAVAK HDFFKFRIDG DMVPHISRQR LTKYTMADLV YALRHFDEGN CDTLKEILVT YNCCDDDYFN K KDWYDFVE NPDILRVYAN LGERVRQALL KTVQFCDAMR NAGIVGVLTL DNQDLNGNWY DFGDFIQTTP GSGVPVVDSY YS LLMPILT LTRALTAESH VDTDLTKPYI KWDLLKYDFT EERLKLFDRY FKYWDQTYHP NCVNCLDDRC ILHCANFNVL FST VFPPTS FGPLVRKIFV DGVPFVVSTG YHFRELGVVH NQDVNLHSSR LSFKELLVYA ADPAMHAASG NLLLDKRTTC FSVA ALTNN VAFQTVKPGN FNKDFYDFAV SKGFFKEGSS VELKHFFFAQ DGNAAISDYD YYRYNLPTMC DIRQLLFVVE VVDKY FDCY DGGCINANQV IVNNLDKSAG FPFNKWGKAR LYYDSMSYED QDALFAYTKR NVIPTITQMN LKYAISAKNR ARTVAG VSI CSTMTNRQFH QKLLKSIAAT RGATVVIGTS KFYGGWHNML KTVYSDVENP HLMGWDYPKC DRAMPNMLRI MASLVLA RK HTTCCSLSHR FYRLANECAQ VLSEMVMCGG SLYVKPGGTS SGDATTAYAN SVFNICQAVT ANVNALLSTD GNKIADKY V RNLQHRLYEC LYRNRDVDTD FVNEFYAYLR KHFSMMILSD DAVVCFNSTY ASQGLVASIK NFKSVLYYQN NVFMSEAKC WTETDLTKGP HEFCSQHTML VKQGDDYVYL PYPDPSRILG AGCFVDDIVK TDGTLMIERF VSLAIDAYPL TKHPNQEYAD VFHLYLQYI RKLHDELTGH MLDMYSVMLT NDNTSRYWEP EFYEAMYTPH TVLQLEHHHH HH UniProtKB: Replicase polyprotein 1ab |
-分子 #2: Non-structural protein 8
| 分子 | 名称: Non-structural protein 8 / タイプ: protein_or_peptide / ID: 2 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 23.105396 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MAIASEFSSL PSYAAFATAQ EAYEQAVANG DSEVVLKKLK KSLNVAKSEF DRDAAMQRKL EKMADQAMTQ MYKQARSEDK RAKVTSAMQ TMLFTMLRKL DNDALNNIIN NARDGCVPLN IIPLTTAAKL MVVIPDYNTY KNTCDGTTFT YASALWEIQQ V VDADSKIV ...文字列: MAIASEFSSL PSYAAFATAQ EAYEQAVANG DSEVVLKKLK KSLNVAKSEF DRDAAMQRKL EKMADQAMTQ MYKQARSEDK RAKVTSAMQ TMLFTMLRKL DNDALNNIIN NARDGCVPLN IIPLTTAAKL MVVIPDYNTY KNTCDGTTFT YASALWEIQQ V VDADSKIV QLSEISMDNS PNLAWPLIVT ALRANSAVKL QLEHHHHHH UniProtKB: Replicase polyprotein 1ab |
-分子 #3: Non-structural protein 7
| 分子 | 名称: Non-structural protein 7 / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 10.451153 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MSKMSDVKCT SVVLLSVLQQ LRVESSSKLW AQCVQLHNDI LLAKDTTEAF EKMVSLLSVL LSMQGAVDIN KLCEEMLDNR ATLQLEHHH HHH UniProtKB: Replicase polyprotein 1ab |
-分子 #4: RNA (5'-R(*GP*UP*GP*GP*GP*CP*CP*CP*A)-3')
| 分子 | 名称: RNA (5'-R(*GP*UP*GP*GP*GP*CP*CP*CP*A)-3') / タイプ: rna / ID: 4 / コピー数: 2 |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 2.886783 KDa |
| 配列 | 文字列: GUGGGCCCA |
-分子 #5: ZINC ION
| 分子 | 名称: ZINC ION / タイプ: ligand / ID: 5 / コピー数: 2 / 式: ZN |
|---|---|
| 分子量 | 理論値: 65.409 Da |
-分子 #6: MAGNESIUM ION
| 分子 | 名称: MAGNESIUM ION / タイプ: ligand / ID: 6 / コピー数: 1 / 式: MG |
|---|---|
| 分子量 | 理論値: 24.305 Da |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.7 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 |
| グリッド | モデル: Quantifoil R2/2 / 材質: COPPER / メッシュ: 200 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 60 sec. / 前処理 - 雰囲気: OTHER |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | #0 - Image recording ID: 1 #0 - フィルム・検出器のモデル: FEI FALCON III (4k x 4k) #0 - 検出モード: COUNTING / #0 - 平均電子線量: 30.0 e/Å2 / #1 - Image recording ID: 2 #1 - フィルム・検出器のモデル: FEI FALCON III (4k x 4k) #1 - 平均電子線量: 30.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 100.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.4 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 96000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT |
|---|---|
| 得られたモデル |  PDB-6xqb: |
 ムービー
ムービー コントローラー
コントローラー






















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)





















