+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-1578 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Bacillus subtilis RNA polymerase NusA complex | |||||||||
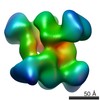
 マップデータ マップデータ | RNAP_NusA complex from Bacillus subtilis | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | RNAP NusA Transcription elongation Firmicutes | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / ネガティブ染色法 / 解像度: 22.0 Å | |||||||||
 データ登録者 データ登録者 | Yang X / Molimau S / Doherty GP / Marles-Wright J / Rothnagel R / Hankamer B / Lewis RJ / Lewis PJ | |||||||||
 引用 引用 |  ジャーナル: EMBO Rep / 年: 2009 ジャーナル: EMBO Rep / 年: 2009タイトル: The structure of bacterial RNA polymerase in complex with the essential transcription elongation factor NusA. 著者: Xiao Yang / Seeseei Molimau / Geoff P Doherty / Elecia B Johnston / Jon Marles-Wright / Rosalba Rothnagel / Ben Hankamer / Richard J Lewis / Peter J Lewis /  要旨: There are three stages of transcribing DNA into RNA. These stages are initiation, elongation and termination, and they are well-understood biochemically. However, despite the plethora of structural ...There are three stages of transcribing DNA into RNA. These stages are initiation, elongation and termination, and they are well-understood biochemically. However, despite the plethora of structural information made available on RNA polymerase in the last decade, little is available for RNA polymerase in complex with transcription elongation factors. To understand the mechanisms of transcriptional regulation, we describe the first structure, to our knowledge, for a bacterial RNA polymerase in complex with an essential transcription elongation factor. The resulting structure formed between the RNA polymerase and NusA from Bacillus subtilis provides important insights into the transition from an initiation complex to an elongation complex, and how NusA is able to modulate transcription elongation and termination. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_1578.map.gz emd_1578.map.gz | 1.1 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-1578-v30.xml emd-1578-v30.xml emd-1578.xml emd-1578.xml | 9 KB 9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  1578.gif 1578.gif | 48.5 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-1578 http://ftp.pdbj.org/pub/emdb/structures/EMD-1578 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-1578 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-1578 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_1578_validation.pdf.gz emd_1578_validation.pdf.gz | 230.2 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_1578_full_validation.pdf.gz emd_1578_full_validation.pdf.gz | 229.3 KB | 表示 | |
| XML形式データ |  emd_1578_validation.xml.gz emd_1578_validation.xml.gz | 5.2 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1578 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1578 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1578 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1578 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_1578.map.gz / 形式: CCP4 / 大きさ: 1.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_1578.map.gz / 形式: CCP4 / 大きさ: 1.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | RNAP_NusA complex from Bacillus subtilis | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 3.9 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : RNAP_NusA complex
| 全体 | 名称: RNAP_NusA complex |
|---|---|
| 要素 |
|
-超分子 #1000: RNAP_NusA complex
| 超分子 | 名称: RNAP_NusA complex / タイプ: sample / ID: 1000 / 詳細: Monodisperse / 集合状態: Dimeric / Number unique components: 2 |
|---|---|
| 分子量 | 実験値: 440 KDa / 理論値: 440 KDa / 手法: Gel filtration |
-分子 #1: RNA polymerase
| 分子 | 名称: RNA polymerase / タイプ: protein_or_peptide / ID: 1 / Name.synonym: RNAP / 詳細: Negative staining / コピー数: 1 / 集合状態: Monomer / 組換発現: No |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 実験値: 400 KDa / 理論値: 400 KDa |
-分子 #2: NusA
| 分子 | 名称: NusA / タイプ: protein_or_peptide / ID: 2 / Name.synonym: NusA / 詳細: Negative staining / コピー数: 1 / 集合状態: Monomer / 組換発現: No |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 実験値: 40 KDa / 理論値: 40 KDa |
-実験情報
-構造解析
| 手法 | ネガティブ染色法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.8 詳細: 20 mM Tris-HCl pH 7.8, 150 mM NaCl, 10 mM MgCl2, 5% (v/v) glycerol and 1 mM DTT |
|---|---|
| 染色 | タイプ: NEGATIVE / 詳細: 1% Uranyl acetate |
| グリッド | 詳細: Home made carbon |
| 凍結 | 凍結剤: NONE / 装置: OTHER |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TECNAI F30 |
|---|---|
| 撮影 | デジタル化 - サンプリング間隔: 3.9 µm / 実像数: 524 / ビット/ピクセル: 16 |
| 電子線 | 加速電圧: 300 kV / 電子線源: OTHER |
| 電子光学系 | 照射モード: OTHER / 撮影モード: OTHER |
| 試料ステージ | 試料ホルダー: Eucentric / 試料ホルダーモデル: GATAN LIQUID NITROGEN |
| 実験機器 |  モデル: Tecnai F30 / 画像提供: FEI Company |
- 画像解析
画像解析
| 最終 再構成 | 想定した対称性 - 点群: C1 (非対称) / 解像度のタイプ: BY AUTHOR / 解像度: 22.0 Å / 解像度の算出法: FSC 0.5 CUT-OFF / ソフトウェア - 名称: EMAN / 使用した粒子像数: 15027 |
|---|
 ムービー
ムービー コントローラー
コントローラー



 UCSF Chimera
UCSF Chimera