+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | 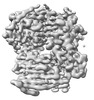 | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Eukaryotic Mre11-Rad50-Nbs1 complex catalytic head | ||||||||||||
 マップデータ マップデータ | MRN head, Ref3D | ||||||||||||
 試料 試料 |
| ||||||||||||
 キーワード キーワード |  DNA repair (DNA修復) / DNA repair (DNA修復) /  complex / complex /  ATPase (ATPアーゼ) / coiled-coils / ATPase (ATPアーゼ) / coiled-coils /  HYDROLASE (加水分解酵素) HYDROLASE (加水分解酵素) | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 Mre11 complex / 3'-5'-DNA exonuclease activity / DNA endonuclease activity / meiotic cell cycle / double-strand break repair / manganese ion binding Mre11 complex / 3'-5'-DNA exonuclease activity / DNA endonuclease activity / meiotic cell cycle / double-strand break repair / manganese ion binding類似検索 - 分子機能 | ||||||||||||
| 生物種 |   Chaetomium thermophilum (菌類) / Chaetomium thermophilum (菌類) /   Thermochaetoides thermophila (菌類) Thermochaetoides thermophila (菌類) | ||||||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 4.0 Å クライオ電子顕微鏡法 / 解像度: 4.0 Å | ||||||||||||
 データ登録者 データ登録者 | Stakyte K / Rotheneder M / Bartho JD / Lammens K / Hopfner KP | ||||||||||||
| 資金援助 |  ドイツ, 3件 ドイツ, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Mol Cell / 年: 2023 ジャーナル: Mol Cell / 年: 2023タイトル: Cryo-EM structure of the Mre11-Rad50-Nbs1 complex reveals the molecular mechanism of scaffolding functions. 著者: Matthias Rotheneder / Kristina Stakyte / Erik van de Logt / Joseph D Bartho / Katja Lammens / Yilan Fan / Aaron Alt / Brigitte Kessler / Christophe Jung / Wynand P Roos / Barbara ...著者: Matthias Rotheneder / Kristina Stakyte / Erik van de Logt / Joseph D Bartho / Katja Lammens / Yilan Fan / Aaron Alt / Brigitte Kessler / Christophe Jung / Wynand P Roos / Barbara Steigenberger / Karl-Peter Hopfner /  要旨: The DNA double-strand break repair complex Mre11-Rad50-Nbs1 (MRN) detects and nucleolytically processes DNA ends, activates the ATM kinase, and tethers DNA at break sites. How MRN can act both as ...The DNA double-strand break repair complex Mre11-Rad50-Nbs1 (MRN) detects and nucleolytically processes DNA ends, activates the ATM kinase, and tethers DNA at break sites. How MRN can act both as nuclease and scaffold protein is not well understood. The cryo-EM structure of MRN from Chaetomium thermophilum reveals a 2:2:1 complex with a single Nbs1 wrapping around the autoinhibited Mre11 nuclease dimer. MRN has two DNA-binding modes, one ATP-dependent mode for loading onto DNA ends and one ATP-independent mode through Mre11's C terminus, suggesting how it may interact with DSBs and intact DNA. MRNs two 60-nm-long coiled-coil domains form a linear rod structure, the apex of which is assembled by the two joined zinc-hook motifs. Apices from two MRN complexes can further dimerize, forming 120-nm spanning MRN-MRN structures. Our results illustrate the architecture of MRN and suggest how it mechanistically integrates catalytic and tethering functions. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_14880.map.gz emd_14880.map.gz | 131.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-14880-v30.xml emd-14880-v30.xml emd-14880.xml emd-14880.xml | 20.6 KB 20.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_14880_fsc.xml emd_14880_fsc.xml | 12.5 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_14880.png emd_14880.png | 105.5 KB | ||
| マスクデータ |  emd_14880_msk_1.map emd_14880_msk_1.map | 166.4 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-14880.cif.gz emd-14880.cif.gz | 7.1 KB | ||
| その他 |  emd_14880_half_map_1.map.gz emd_14880_half_map_1.map.gz emd_14880_half_map_2.map.gz emd_14880_half_map_2.map.gz | 131.5 MB 132 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-14880 http://ftp.pdbj.org/pub/emdb/structures/EMD-14880 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-14880 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-14880 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7zqyC  7zr1C  8bahC C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_14880.map.gz / 形式: CCP4 / 大きさ: 166.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_14880.map.gz / 形式: CCP4 / 大きさ: 166.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | MRN head, Ref3D | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.059 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_14880_msk_1.map emd_14880_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: MRN head, Half map A
| ファイル | emd_14880_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | MRN head, Half map A | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: MRN head, Half map B
| ファイル | emd_14880_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | MRN head, Half map B | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Chaetomium thermophilum Mre11-Rad50-Nbs1 complex bound to ATPyS
| 全体 | 名称: Chaetomium thermophilum Mre11-Rad50-Nbs1 complex bound to ATPyS |
|---|---|
| 要素 |
|
-超分子 #1: Chaetomium thermophilum Mre11-Rad50-Nbs1 complex bound to ATPyS
| 超分子 | 名称: Chaetomium thermophilum Mre11-Rad50-Nbs1 complex bound to ATPyS タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:   Chaetomium thermophilum (菌類) Chaetomium thermophilum (菌類) |
-分子 #1: Double-strand break repair protein
| 分子 | 名称: Double-strand break repair protein / タイプ: protein_or_peptide / ID: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Thermochaetoides thermophila (菌類) / 株: DSM 1495 / CBS 144.50 / IMI 039719 Thermochaetoides thermophila (菌類) / 株: DSM 1495 / CBS 144.50 / IMI 039719 |
| 組換発現 | 生物種:   Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MPQTAGPDTI RILVSTDNHV GYEERDPIRK DDSWRTFDEI MQLARTKDVD MVLLGGDLFH DNKPSRKAMY QVMRSLRKNC LGMKPCELEF LSDPAEVFEG AFPHVNYYDP DINVSIPVFS IHGNHDDPSG DGHLCSLDLL QVAGLVNYFG RVPEADNIHV KPILLQKGKT ...文字列: MPQTAGPDTI RILVSTDNHV GYEERDPIRK DDSWRTFDEI MQLARTKDVD MVLLGGDLFH DNKPSRKAMY QVMRSLRKNC LGMKPCELEF LSDPAEVFEG AFPHVNYYDP DINVSIPVFS IHGNHDDPSG DGHLCSLDLL QVAGLVNYFG RVPEADNIHV KPILLQKGKT KLALYGMSNV RDERIHRTFR DNKVRFYRPS QQTGDWFNLL TLHQNHYAHT PTGYLSENML PDFLDLVIWG HEHECLIDPK KNPETGFHVM QPGSSIATSL VPGEAVPKHI AILSITGKSF EVEKIPLRTV RPFVIREITL ATDKRFKGLE KKQDNRQEVT KRLMQIVEEM IAEANEMWRS LHEDSQDDED EEQPLPLIRL KVEYSSPEGT KFEVENPQRF SNRFAGKVAN QNDVVHFYRK KTGTTRKPKE GKRELPEGIA EALEDSDSIS VDALVQEFFA QQSLKILPQA PFGDAVNQFV SKDDKHAVEM FVMDSLSSQV RGLLQLDDDK INEGLDSHIE DFRKVMEKNF LSGQQKQAQR RRRFKEKPEG WDSDLNGHWT LQPEAIEELS SSPEPAKEGG RVRPASRITV GDEDNLFEEE EFVQKTTAKR APTTRATRKT AAATRATTAT KASAPAKKSI AAPRGRKRAN PFQDSAEEEE DVIMDDDDDY KPAPPVKAPP PKPARETQTR GAPKTRQTTL NFSQAERPTR TTQKAIEISD DEISEDDAFE SMPARKSKRY UniProtKB: Double-strand break repair protein |
-分子 #2: DH domain-containing protein
| 分子 | 名称: DH domain-containing protein / タイプ: protein_or_peptide / ID: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Thermochaetoides thermophila (菌類) / 株: DSM 1495 / CBS 144.50 / IMI 039719 Thermochaetoides thermophila (菌類) / 株: DSM 1495 / CBS 144.50 / IMI 039719 |
| 組換発現 | 生物種:   Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MSKIEKLSIL GVRSFGPHHP ETIAFNTPLT LIVGYNGSGK TTVIECLKYA TTGELPPNST RNGAFIHDPD LVGEKEVRAQ VKLSFRSTIG ESYVVTRNIQ LLVQRNNKRT QKTLEGSLLL RNNGERTVIS TRVAELDKLV SEKLGVPPAI LDAVIFCHQD DSLWPMSEPA ...文字列: MSKIEKLSIL GVRSFGPHHP ETIAFNTPLT LIVGYNGSGK TTVIECLKYA TTGELPPNST RNGAFIHDPD LVGEKEVRAQ VKLSFRSTIG ESYVVTRNIQ LLVQRNNKRT QKTLEGSLLL RNNGERTVIS TRVAELDKLV SEKLGVPPAI LDAVIFCHQD DSLWPMSEPA ALKKRFDEIF EAQKYTKVIE NIRLLKKKKG DELKILKERE VQDKANKERA EKVDRLMAQL TREILEAREK CNELSKQMEE ESAKIKDKYE QANSFLKIMN DLQTKTEKLE YKKDAIVELR SRIEELPDPD EVLRNTLDEY EQTINRIVAD RDHKAAQFHD LQAELKSARD QHTAKAAEQG KHQSDKEKYE RQLVARERMI REAAERHEIR GYNGDLDDRR IAIFNERIQK ILNDKRRELE RLQRENQEEL DRKTAVIAER ESRKQSVIRD RKAAKDRIIS LGKDMASIQG ELSSIDIDEG TEEMLRAEMK ELQARIEAAK ADEQNANLDA QIKEVNEEIW KLESLSAKLA RELVECTRLA SERAQLDLRR KQLAERKREL EIMTNTWNEQ FSTLLGEGWR PETLERDFSD VLKQQQLLVG EHRKKKDATQ QELKQAEYQL SNARNLHNKL TNEMEACMRA VQTAMKEARD LDSAPPVDEY ITMLETDEKE LAEVETALKL YDELKKHYST IKDRALRFNK CYICDRDFTN QEAAKTRLLE KVAKRLGDEE KKELLEDQAA FMKSLDILRA VRVKYDTYQR LSSELPQLSR EIDSETNRRE DLVRRLEDQD LAFREADNKL QEMETLNKHV MKITQLLKDI SDAEKQVERS QQLSNIETRS ADEINEEQTT CAEQTRAAQA KLTKLTAEKQ RLKDLVRQLE VERLQLENKI SSAVQQLERK KRLQESIARH KEDQNQARNA VQEADEELER LEPEIAGARA ALDEARQACR AKEQKVAAER DAIAQTVSEL NMINSEIQEY LDRGGPSSLA ANQRAIANLE TQMANLEGEM RELTVQINKL NKEIDNSDAK KRNIADNLTY RKNLREKDAL EREIAELEAR NAQEDYDRLI KEAHYLEAHR SKLNADRERL MGMMSTKDEE FRRLNEEYEL DLKDAKAKYK ETHIKVETTK AAIEDLGRGM AAVDHAIMQY HSKMMEQINR TIAELWQSTY QGTDIDTIQI RSDVESTTSS DSGTRRNYNY RVSMVKGDTE MDMRGRCSAG QKVLASIIIR LALAESFCAN CGLIALDEPT TNLDSDNIRS LAESLHGIIK ARQAQGNLQL IVITHDEEFL KYMQCSDFCD DFYRVKRDEK QNSVIVRESI TRITE |
-分子 #3: FHA domain-containing protein
| 分子 | 名称: FHA domain-containing protein / タイプ: protein_or_peptide / ID: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Thermochaetoides thermophila (菌類) / 株: DSM 1495 / CBS 144.50 / IMI 039719 Thermochaetoides thermophila (菌類) / 株: DSM 1495 / CBS 144.50 / IMI 039719 |
| 組換発現 | 生物種:   Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MWILESELFD GKRLWLRPGK TYLFGRTVAE AGQLTISDKT VSRKHLTIHI DNVPEGGGRN LRSRSNVIVE DLESKKGTLV NGVQIRGQKT TLTEDVNEIK LGLCPKTLKI RWHPIVLSFS FTSKELRADP WTNLRDSLEQ LDIKYSAEYE PTTTHVVSKK RNTSKGLQAL ...文字列: MWILESELFD GKRLWLRPGK TYLFGRTVAE AGQLTISDKT VSRKHLTIHI DNVPEGGGRN LRSRSNVIVE DLESKKGTLV NGVQIRGQKT TLTEDVNEIK LGLCPKTLKI RWHPIVLSFS FTSKELRADP WTNLRDSLEQ LDIKYSAEYE PTTTHVVSKK RNTSKGLQAL INGRYIVTDS FINAIVQATE IPEGEEGASS ALEQDFEANW PNPLDHLPPR GEEPGNHTTE TYAPDARRQE VFDGYTFIFY EKKQYDNLFP AISAGKGKAL LKEVVPNRTR VDEFVRYVKS VAGEKGLGSF EDGSEGKGVV VVRYTPKGED SAWYAEFFTK FAQQLDHRPI DQKEFLEAIL ACDASMLRRP LEAMSQPVSV SASVEPQSSE KVRPAVEDRK EVEQSAPKQL QPSAEVPATE ESAPAPHRRE RRTGRSRFKG FDFDDDDIII ETPQAQSSTQ VPALPQVPSA SQDSLFVSQR EPSLAPSEPM LEEEAPCNTR TTRQTHRKRV LSPLPEHDNS ALLDEIAPIT AAVKRRRIEA GQDPVPPLPE PEPEREDEDV EMVEESPPRK GKKGAATTAK GKGKKIKQED EENVLELARR RREEAEAAAA AERQRLAQLG DDDIDYAAIR RLHIIEEIEV RQPEPHGPNR TREQDIADGR WDPRWNGRKN FKRFRRQGET GVRMPVQSVI VPLEEVRTKE YGIGDDYWLE DEEGRVPRRP KETQTQERST IGSVRDGSGF AAAAASGKGK EKDKENEKEV GRPGSSAAAA KQRSKPAPRR TVLTLDSSDE DEDEPSPHAP GIDTISDSEP EVVSSFPSVI PASEPSRSRA AKAAERANAL RSSAHSSQSQ TQQHRESQLS TGSSKIQLTL APGSSSLSFS RSGTAAGRNE NGKRPFGSFV SGESTASGRG MSVESGSVRG ESASKRQKQG SSGGGSFLAT RRKDDGSEEE SEDDELKFRF GRRR |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.27 mg/mL |
|---|---|
| 緩衝液 | pH: 7.6 |
| グリッド | モデル: Quantifoil R2/1 / 材質: COPPER / メッシュ: 200 |
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 50.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.7 mm Bright-field microscopy / Cs: 2.7 mm最大 デフォーカス(公称値): 2.8000000000000003 µm 最小 デフォーカス(公称値): 1.0 µm |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 平均電子線量: 43.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー












 Z
Z Y
Y X
X