+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-12766 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Single particle cryo-EM reconstruction of just the top two rings of a 40-mer assembly of recombinant yeast Hsp26 S207E mutant. | |||||||||
 マップデータ マップデータ | Cryo-EM Single particle Reconstruction of the top two rings of a 40mer oligomer of yeast Hsp26 S207E mutant, containing 16 monomers. This map was used for flexible fitting of the atomic model | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | small heat shock proteins / Hsp26 S207E mutant / CHAPERONE | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報cytoplasmic stress granule / unfolded protein binding / protein folding / cellular response to heat / mRNA binding / mitochondrion / identical protein binding / nucleus / cytoplasm 類似検索 - 分子機能 | |||||||||
| 生物種 |   | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 7.8 Å | |||||||||
 データ登録者 データ登録者 | Muehlhofer M / Peters C / Kriehuber T / Kreuzeder M / Kazman P / Rodina N / Reif B / Haslbeck M / Weinkauf S / Buchner J | |||||||||
| 資金援助 |  ドイツ, 1件 ドイツ, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2021 ジャーナル: Nat Commun / 年: 2021タイトル: Phosphorylation activates the yeast small heat shock protein Hsp26 by weakening domain contacts in the oligomer ensemble. 著者: Moritz Mühlhofer / Carsten Peters / Thomas Kriehuber / Marina Kreuzeder / Pamina Kazman / Natalia Rodina / Bernd Reif / Martin Haslbeck / Sevil Weinkauf / Johannes Buchner /  要旨: Hsp26 is a small heat shock protein (sHsp) from S. cerevisiae. Its chaperone activity is activated by oligomer dissociation at heat shock temperatures. Hsp26 contains 9 phosphorylation sites in ...Hsp26 is a small heat shock protein (sHsp) from S. cerevisiae. Its chaperone activity is activated by oligomer dissociation at heat shock temperatures. Hsp26 contains 9 phosphorylation sites in different structural elements. Our analysis of phospho-mimetic mutations shows that phosphorylation activates Hsp26 at permissive temperatures. The cryo-EM structure of the Hsp26 40mer revealed contacts between the conserved core domain of Hsp26 and the so-called thermosensor domain in the N-terminal part of the protein, which are targeted by phosphorylation. Furthermore, several phosphorylation sites in the C-terminal extension, which link subunits within the oligomer, are sensitive to the introduction of negative charges. In all cases, the intrinsic inhibition of chaperone activity is relieved and the N-terminal domain becomes accessible for substrate protein binding. The weakening of domain interactions within and between subunits by phosphorylation to activate the chaperone activity in response to proteotoxic stresses independent of heat stress could be a general regulation principle of sHsps. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_12766.map.gz emd_12766.map.gz | 85.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-12766-v30.xml emd-12766-v30.xml emd-12766.xml emd-12766.xml | 13.5 KB 13.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
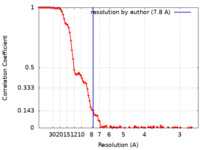
| FSC (解像度算出) |  emd_12766_fsc.xml emd_12766_fsc.xml | 13.3 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_12766.png emd_12766.png | 174.4 KB | ||
| Filedesc metadata |  emd-12766.cif.gz emd-12766.cif.gz | 5.8 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-12766 http://ftp.pdbj.org/pub/emdb/structures/EMD-12766 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-12766 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-12766 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_12766_validation.pdf.gz emd_12766_validation.pdf.gz | 567.2 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_12766_full_validation.pdf.gz emd_12766_full_validation.pdf.gz | 566.8 KB | 表示 | |
| XML形式データ |  emd_12766_validation.xml.gz emd_12766_validation.xml.gz | 11.8 KB | 表示 | |
| CIF形式データ |  emd_12766_validation.cif.gz emd_12766_validation.cif.gz | 15.5 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12766 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12766 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12766 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12766 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_12766.map.gz / 形式: CCP4 / 大きさ: 91.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_12766.map.gz / 形式: CCP4 / 大きさ: 91.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Cryo-EM Single particle Reconstruction of the top two rings of a 40mer oligomer of yeast Hsp26 S207E mutant, containing 16 monomers. This map was used for flexible fitting of the atomic model | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.33 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Top two rings (16 subunits) of a 40mer complex of Hsp26 mutant S2...
| 全体 | 名称: Top two rings (16 subunits) of a 40mer complex of Hsp26 mutant S207E. (use 0.487 as threshold to visualise) |
|---|---|
| 要素 |
|
-超分子 #1: Top two rings (16 subunits) of a 40mer complex of Hsp26 mutant S2...
| 超分子 | 名称: Top two rings (16 subunits) of a 40mer complex of Hsp26 mutant S207E. (use 0.487 as threshold to visualise) タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 382 KDa |
-分子 #1: Heat shock protein 26
| 分子 | 名称: Heat shock protein 26 / タイプ: protein_or_peptide / ID: 1 / コピー数: 5 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  株: ATCC 204508 / S288c |
| 分子量 | 理論値: 23.910586 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MSFNSPFFDF FDNINNEVDA FNRLLGEGGL RGYAPRRQLA NTPAKDSTGK EVARPNNYAG ALYDPRDETL DDWFDNDLSL FPSGFGFPR SVAVPVDILD HDNNYELKVV VPGVKSKKDI DIEYHQNKNQ ILVSGEIPST LNEESKDKVK VKESSSGKFK R VITLPDYP ...文字列: MSFNSPFFDF FDNINNEVDA FNRLLGEGGL RGYAPRRQLA NTPAKDSTGK EVARPNNYAG ALYDPRDETL DDWFDNDLSL FPSGFGFPR SVAVPVDILD HDNNYELKVV VPGVKSKKDI DIEYHQNKNQ ILVSGEIPST LNEESKDKVK VKESSSGKFK R VITLPDYP GVDADNIKAD YANGVLTLTV PKLKPQKDGK NHVKKIEVSS QESWGN UniProtKB: Heat shock protein 26 |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 |
|---|---|
| 凍結 | 凍結剤: ETHANE-PROPANE / チャンバー内湿度: 100 % / チャンバー内温度: 294 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 特殊光学系 | エネルギーフィルター - 名称: GIF Quantum LS / エネルギーフィルター - スリット幅: 20 eV |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 実像数: 5010 / 平均露光時間: 8.0 sec. / 平均電子線量: 45.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm 最大 デフォーカス(公称値): 2.8000000000000003 µm 最小 デフォーカス(公称値): 0.6 µm / 倍率(公称値): 105000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 詳細 | Homology model generated with ITASSER with 1GME as template. Fitted with Chimera and flexibly fitted with NAMD. Residues 63 to 214 present in the model. |
|---|---|
| 精密化 | 空間: REAL / プロトコル: FLEXIBLE FIT / 当てはまり具合の基準: Correlation coefficient |
| 得られたモデル |  PDB-7oa6: |
 ムービー
ムービー コントローラー
コントローラー