+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 9cu1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
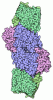
| タイトル | Azotobacter vinelandii filamentous 2:2:1 MoFeP:FeP:FeSII-Complex (termini; C1 symmetry) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
 要素 要素 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
 キーワード キーワード | METAL BINDING PROTEIN / Nitrogenase / FeMoCo / nitrogen / P-cluster | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報molybdenum-iron nitrogenase complex / nitrogenase / nitrogenase activity / nitrogen fixation / iron-sulfur cluster binding / 2 iron, 2 sulfur cluster binding / 4 iron, 4 sulfur cluster binding / ATP binding / metal ion binding / cytoplasm 類似検索 - 分子機能 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 生物種 |  Azotobacter vinelandii (窒素固定) Azotobacter vinelandii (窒素固定) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.83 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
 データ登録者 データ登録者 | Narehood, S.M. / Cook, B.D. / Srisantitham, S. / Eng, V.H. / Shiau, A. / Britt, R.D. / Herzik, M.A. / Tezcan, F.A. | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 資金援助 |  米国, 3件 米国, 3件
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
 引用 引用 |  ジャーナル: Nature / 年: 2025 ジャーナル: Nature / 年: 2025タイトル: Structural basis for the conformational protection of nitrogenase from O. 著者: Sarah M Narehood / Brian D Cook / Suppachai Srisantitham / Vanessa H Eng / Angela A Shiau / Kelly L McGuire / R David Britt / Mark A Herzik / F Akif Tezcan /  要旨: The low reduction potentials required for the reduction of dinitrogen (N) render metal-based nitrogen-fixation catalysts vulnerable to irreversible damage by dioxygen (O). Such O sensitivity ...The low reduction potentials required for the reduction of dinitrogen (N) render metal-based nitrogen-fixation catalysts vulnerable to irreversible damage by dioxygen (O). Such O sensitivity represents a major conundrum for the enzyme nitrogenase, as a large fraction of nitrogen-fixing organisms are either obligate aerobes or closely associated with O-respiring organisms to support the high energy demand of catalytic N reduction. To counter O damage to nitrogenase, diazotrophs use O scavengers, exploit compartmentalization or maintain high respiration rates to minimize intracellular O concentrations. A last line of damage control is provided by the 'conformational protection' mechanism, in which a [2Fe:2S] ferredoxin-family protein termed FeSII (ref. ) is activated under O stress to form an O-resistant complex with the nitrogenase component proteins. Despite previous insights, the molecular basis for the conformational O protection of nitrogenase and the mechanism of FeSII activation are not understood. Here we report the structural characterization of the Azotobacter vinelandii FeSII-nitrogenase complex by cryo-electron microscopy. Our studies reveal a core complex consisting of two molybdenum-iron proteins (MoFePs), two iron proteins (FePs) and one FeSII homodimer, which polymerize into extended filaments. In this three-protein complex, FeSII mediates an extensive network of interactions with MoFeP and FeP to position their iron-sulphur clusters in catalytically inactive but O-protected states. The architecture of the FeSII-nitrogenase complex is confirmed by solution studies, which further indicate that the activation of FeSII involves an oxidation-induced conformational change. | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  9cu1.cif.gz 9cu1.cif.gz | 1 MB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb9cu1.ent.gz pdb9cu1.ent.gz | 872.5 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  9cu1.json.gz 9cu1.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  9cu1_validation.pdf.gz 9cu1_validation.pdf.gz | 2.4 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  9cu1_full_validation.pdf.gz 9cu1_full_validation.pdf.gz | 2.4 MB | 表示 | |
| XML形式データ |  9cu1_validation.xml.gz 9cu1_validation.xml.gz | 157 KB | 表示 | |
| CIF形式データ |  9cu1_validation.cif.gz 9cu1_validation.cif.gz | 245.5 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/cu/9cu1 https://data.pdbj.org/pub/pdb/validation_reports/cu/9cu1 ftp://data.pdbj.org/pub/pdb/validation_reports/cu/9cu1 ftp://data.pdbj.org/pub/pdb/validation_reports/cu/9cu1 | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-Nitrogenase molybdenum-iron protein ... , 2種, 8分子 ACHJBDIK
| #1: タンパク質 | 分子量: 55363.043 Da / 分子数: 4 / 由来タイプ: 天然 / 由来: (天然)  Azotobacter vinelandii (窒素固定) / 参照: UniProt: P07328, nitrogenase Azotobacter vinelandii (窒素固定) / 参照: UniProt: P07328, nitrogenase#2: タンパク質 | 分子量: 59535.879 Da / 分子数: 4 / 由来タイプ: 天然 / 由来: (天然)  Azotobacter vinelandii (窒素固定) / 参照: UniProt: P07329, nitrogenase Azotobacter vinelandii (窒素固定) / 参照: UniProt: P07329, nitrogenase |
|---|
-タンパク質 , 3種, 6分子 EFLMGN
| #3: タンパク質 | 分子量: 31548.240 Da / 分子数: 4 / 由来タイプ: 天然 / 由来: (天然)  Azotobacter vinelandii (窒素固定) / 参照: UniProt: P00459, nitrogenase Azotobacter vinelandii (窒素固定) / 参照: UniProt: P00459, nitrogenase#4: タンパク質 | | 分子量: 13289.330 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)  Azotobacter vinelandii (窒素固定) Azotobacter vinelandii (窒素固定)遺伝子: fesII / 発現宿主:  #5: タンパク質 | | 分子量: 13321.374 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)  Azotobacter vinelandii (窒素固定) Azotobacter vinelandii (窒素固定)遺伝子: fesII / 発現宿主:  |
|---|
-非ポリマー , 9種, 1104分子 












| #6: 化合物 | ChemComp-HCA / #7: 化合物 | ChemComp-ICS / #8: 化合物 | ChemComp-CLF / #9: 化合物 | ChemComp-FE / #10: 化合物 | ChemComp-ADP / #11: 化合物 | ChemComp-MG / #12: 化合物 | #13: 化合物 | #14: 水 | ChemComp-HOH / | |
|---|
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|---|
| Has protein modification | N |
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: Azotobacter vinelandii filamentous 2:2:1 MoFeP:FeP:FeSII-Complex (termini; C1 symmetry) タイプ: COMPLEX / Entity ID: #1-#5 / 由来: NATURAL | ||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 分子量 | 値: 0.626 MDa / 実験値: NO | ||||||||||||||||||||||||||||||
| 由来(天然) | 生物種:  Azotobacter vinelandii (窒素固定) Azotobacter vinelandii (窒素固定) | ||||||||||||||||||||||||||||||
| 緩衝液 | pH: 8 | ||||||||||||||||||||||||||||||
| 緩衝液成分 |
| ||||||||||||||||||||||||||||||
| 試料 | 濃度: 2.5 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES | ||||||||||||||||||||||||||||||
| 試料支持 | グリッドの材料: COPPER / グリッドのサイズ: 300 divisions/in. / グリッドのタイプ: Quantifoil | ||||||||||||||||||||||||||||||
| 急速凍結 | 装置: SPT LABTECH CHAMELEON / 凍結剤: ETHANE / 湿度: 75 % / 凍結前の試料温度: 298.15 K / 詳細: Samples were frozen with the SPT Labtech chameleon |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: TFS KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 倍率(公称値): 165000 X / 最大 デフォーカス(公称値): 2500 nm / 最小 デフォーカス(公称値): 750 nm / Cs: 2.7 mm / アライメント法: COMA FREE |
| 試料ホルダ | 凍結剤: NITROGEN 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER |
| 撮影 | 平均露光時間: 5 sec. / 電子線照射量: 60 e/Å2 フィルム・検出器のモデル: FEI FALCON IV (4k x 4k) 撮影したグリッド数: 3 / 実像数: 8049 |
| 電子光学装置 | エネルギーフィルター名称: TFS Selectris X / エネルギーフィルタースリット幅: 10 eV |
| 画像スキャン | 横: 4096 / 縦: 4096 |
- 解析
解析
| EMソフトウェア |
| ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||||||||||||||
| 粒子像の選択 | 選択した粒子像数: 866869 | ||||||||||||||||||||||||||||||||||||
| 対称性 | 点対称性: C1 (非対称) | ||||||||||||||||||||||||||||||||||||
| 3次元再構成 | 解像度: 2.83 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 30209 / アルゴリズム: FOURIER SPACE / クラス平均像の数: 1 / 対称性のタイプ: POINT | ||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | B value: 29.1 / プロトコル: RIGID BODY FIT / 空間: REAL | ||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | PDB-ID: 7UT7 Accession code: 7UT7 / Source name: PDB / タイプ: experimental model | ||||||||||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー










 PDBj
PDBj