[English] 日本語
 Yorodumi
Yorodumi- PDB-8ooo: Glutamine synthetase from Methanothermococcus thermolithotrophicu... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 8ooo | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| Title | Glutamine synthetase from Methanothermococcus thermolithotrophicus in complex with 2-oxoglutarate and MgATP at 2.15 A resolution | |||||||||
 Components Components | Glutamine synthetase from Methanothermococcus thermolithotrophicus | |||||||||
 Keywords Keywords | LIGASE / Nitrogen-assimilation / methanogenic archaea / allosteric activation / hydrogenotrophic / thermophile / marine / 2-oxoglutarate / glutamate / ATP / allosteric binding site | |||||||||
| Function / homology | 2-OXOGLUTARIC ACID / ADENOSINE-5'-TRIPHOSPHATE / METHOXY-ETHOXYL / DI(HYDROXYETHYL)ETHER Function and homology information Function and homology information | |||||||||
| Biological species |  Methanothermococcus thermolithotrophicus DSM 2095 (archaea) Methanothermococcus thermolithotrophicus DSM 2095 (archaea) | |||||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / Resolution: 2.149 Å MOLECULAR REPLACEMENT / Resolution: 2.149 Å | |||||||||
 Authors Authors | Mueller, M.-C. / Wagner, T. | |||||||||
| Funding support |  Germany, 2items Germany, 2items
| |||||||||
 Citation Citation |  Journal: Commun Biol / Year: 2024 Journal: Commun Biol / Year: 2024Title: Differences in regulation mechanisms of glutamine synthetases from methanogenic archaea unveiled by structural investigations. Authors: Muller, M.C. / Lemaire, O.N. / Kurth, J.M. / Welte, C.U. / Wagner, T. | |||||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  8ooo.cif.gz 8ooo.cif.gz | 2.1 MB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb8ooo.ent.gz pdb8ooo.ent.gz | 1.7 MB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  8ooo.json.gz 8ooo.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/oo/8ooo https://data.pdbj.org/pub/pdb/validation_reports/oo/8ooo ftp://data.pdbj.org/pub/pdb/validation_reports/oo/8ooo ftp://data.pdbj.org/pub/pdb/validation_reports/oo/8ooo | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  8oolC  8oonC  8ooqC  8oowC  8ooxC  8oozC C: citing same article ( |
|---|---|
| Similar structure data | Similarity search - Function & homology  F&H Search F&H Search |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| Unit cell |
|
- Components
Components
-Protein , 1 types, 12 molecules ABCDEFGHIJKL
| #1: Protein | Mass: 50296.039 Da / Num. of mol.: 12 / Source method: isolated from a natural source Source: (natural)  Methanothermococcus thermolithotrophicus DSM 2095 (archaea) Methanothermococcus thermolithotrophicus DSM 2095 (archaea)Cell line: / / Organ: / / Plasmid details: / / Variant: / / Strain: DSM 2095 / Tissue: / / References: glutamine synthetase |
|---|
-Non-polymers , 9 types, 3109 molecules 



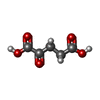












| #2: Chemical | ChemComp-EDO / #3: Chemical | ChemComp-PEG / #4: Chemical | ChemComp-GOL / | #5: Chemical | ChemComp-ATP / #6: Chemical | ChemComp-AKG / #7: Chemical | #8: Chemical | #9: Chemical | #10: Water | ChemComp-HOH / | |
|---|
-Details
| Has ligand of interest | Y |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.53 Å3/Da / Density % sol: 51.5 % / Description: Short thick hexagonal rod |
|---|---|
| Crystal grow | Temperature: 293.15 K / Method: vapor diffusion, sitting drop / pH: 7.6 Details: The enzyme was crystallized at 3.7 mg/ml with a final concentration of 2 mM sodium 2-oxoglutarate, 2 mM ATP and 2 mM MgCl in 25 mM Tris/HCl pH 7.6, 10% v/v glycerol, 150 mM NaCl, 2 mM ...Details: The enzyme was crystallized at 3.7 mg/ml with a final concentration of 2 mM sodium 2-oxoglutarate, 2 mM ATP and 2 mM MgCl in 25 mM Tris/HCl pH 7.6, 10% v/v glycerol, 150 mM NaCl, 2 mM dithiothreitol. The protein was crystallized fresh without any freezing step, and crystallization was performed through the sitting drop method on a 96-Well MRC 2-Drop Crystallization Plates in polystyrene (SWISSCI, United Kingdom) under anaerobic conditions (N2:H2, gas ratio of 97:3). The crystallization reservoir contained 90 ul of mother liquor (20 % w/v polyethylene glycol 3,350 and 200 mM sodium fluoride). The crystallization drop contained 0.6 ul protein with ligands and 0.6 ul precipitant. Crystals were soaked in the mother liquor supplemented with 20 % v/v glycerol prior to freezing in liquid nitrogen. |
-Data collection
| Diffraction | Mean temperature: 100 K / Serial crystal experiment: N |
|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  SLS SLS  / Beamline: X06DA / Wavelength: 1.30511 Å / Beamline: X06DA / Wavelength: 1.30511 Å |
| Detector | Type: DECTRIS PILATUS 2M-F / Detector: PIXEL / Date: Aug 27, 2020 |
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray |
| Radiation wavelength | Wavelength: 1.30511 Å / Relative weight: 1 |
| Reflection | Resolution: 2.148→110.034 Å / Num. obs: 248419 / % possible obs: 92.2 % / Redundancy: 3.6 % / Biso Wilson estimate: 35.99 Å2 / CC1/2: 0.995 / Rmerge(I) obs: 0.11 / Rpim(I) all: 0.068 / Rrim(I) all: 0.13 / Net I/σ(I): 9.3 |
| Reflection shell | Resolution: 2.148→2.297 Å / Redundancy: 3.4 % / Rmerge(I) obs: 0.95 / Mean I/σ(I) obs: 1.3 / Num. unique obs: 12420 / CC1/2: 0.569 / Rpim(I) all: 0.59 / Rrim(I) all: 1.122 / % possible all: 58.8 |
- Processing
Processing
| Software |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  MOLECULAR REPLACEMENT / Resolution: 2.149→42.88 Å / Cor.coef. Fo:Fc: 0.95 / Cor.coef. Fo:Fc free: 0.933 / SU R Cruickshank DPI: 0.361 / Cross valid method: FREE R-VALUE / σ(F): 0 / SU R Blow DPI: 0.365 / SU Rfree Blow DPI: 0.213 / SU Rfree Cruickshank DPI: 0.216 MOLECULAR REPLACEMENT / Resolution: 2.149→42.88 Å / Cor.coef. Fo:Fc: 0.95 / Cor.coef. Fo:Fc free: 0.933 / SU R Cruickshank DPI: 0.361 / Cross valid method: FREE R-VALUE / σ(F): 0 / SU R Blow DPI: 0.365 / SU Rfree Blow DPI: 0.213 / SU Rfree Cruickshank DPI: 0.216 Details: The structure was refined in BUSTER by applying non crystallography symmetry and translation libration screw model.
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso mean: 38.36 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine analyze | Luzzati coordinate error obs: 0.26 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 2.149→42.88 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Resolution: 2.15→2.24 Å / Total num. of bins used: 51
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller


 PDBj
PDBj









