+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7dvd | ||||||
|---|---|---|---|---|---|---|---|
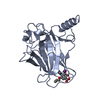
| タイトル | The crystal structure of p53 DNA binding domain and PUMA complex | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | PEPTIDE BINDING PROTEIN / p53 PUMA BH3 peptide complex | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報positive regulation of establishment of protein localization to mitochondrion / positive regulation of endoplasmic reticulum stress-induced intrinsic apoptotic signaling pathway / positive regulation of fibroblast apoptotic process / T cell apoptotic process / BH3-only proteins associate with and inactivate anti-apoptotic BCL-2 members / negative regulation of helicase activity / Loss of function of TP53 in cancer due to loss of tetramerization ability / Regulation of TP53 Expression / signal transduction by p53 class mediator / negative regulation of G1 to G0 transition ...positive regulation of establishment of protein localization to mitochondrion / positive regulation of endoplasmic reticulum stress-induced intrinsic apoptotic signaling pathway / positive regulation of fibroblast apoptotic process / T cell apoptotic process / BH3-only proteins associate with and inactivate anti-apoptotic BCL-2 members / negative regulation of helicase activity / Loss of function of TP53 in cancer due to loss of tetramerization ability / Regulation of TP53 Expression / signal transduction by p53 class mediator / negative regulation of G1 to G0 transition / negative regulation of glucose catabolic process to lactate via pyruvate / Transcriptional activation of cell cycle inhibitor p21 / regulation of intrinsic apoptotic signaling pathway by p53 class mediator / negative regulation of pentose-phosphate shunt / ATP-dependent DNA/DNA annealing activity / Activation of NOXA and translocation to mitochondria / regulation of cell cycle G2/M phase transition / regulation of fibroblast apoptotic process / intrinsic apoptotic signaling pathway in response to hypoxia / oligodendrocyte apoptotic process / negative regulation of miRNA processing / positive regulation of thymocyte apoptotic process / oxidative stress-induced premature senescence / regulation of tissue remodeling / positive regulation of mitochondrial membrane permeability / mRNA transcription / positive regulation of programmed necrotic cell death / bone marrow development / fibroblast apoptotic process / circadian behavior / T cell proliferation involved in immune response / regulation of mitochondrial membrane permeability involved in apoptotic process / germ cell nucleus / RUNX3 regulates CDKN1A transcription / glucose catabolic process to lactate via pyruvate / TP53 Regulates Transcription of Death Receptors and Ligands / TP53 regulates transcription of additional cell cycle genes whose exact role in the p53 pathway remain uncertain / Activation of PUMA and translocation to mitochondria / regulation of DNA damage response, signal transduction by p53 class mediator / histone deacetylase regulator activity / negative regulation of glial cell proliferation / Regulation of TP53 Activity through Association with Co-factors / negative regulation of neuroblast proliferation / execution phase of apoptosis / mitochondrial DNA repair / T cell lineage commitment / Formation of Senescence-Associated Heterochromatin Foci (SAHF) / ER overload response / thymocyte apoptotic process / B cell lineage commitment / TP53 Regulates Transcription of Caspase Activators and Caspases / negative regulation of mitophagy / cardiac septum morphogenesis / negative regulation of DNA replication / entrainment of circadian clock by photoperiod / FOXO-mediated transcription of cell death genes / positive regulation of IRE1-mediated unfolded protein response / negative regulation of telomere maintenance via telomerase / Zygotic genome activation (ZGA) / PI5P Regulates TP53 Acetylation / positive regulation of release of cytochrome c from mitochondria / Association of TriC/CCT with target proteins during biosynthesis / necroptotic process / TP53 Regulates Transcription of Genes Involved in Cytochrome C Release / SUMOylation of transcription factors / TP53 regulates transcription of several additional cell death genes whose specific roles in p53-dependent apoptosis remain uncertain / TFIID-class transcription factor complex binding / intrinsic apoptotic signaling pathway by p53 class mediator / negative regulation of reactive oxygen species metabolic process / rRNA transcription / Transcriptional Regulation by VENTX / replicative senescence / general transcription initiation factor binding / cellular response to UV-C / cellular response to actinomycin D / intrinsic apoptotic signaling pathway in response to endoplasmic reticulum stress / positive regulation of execution phase of apoptosis / positive regulation of RNA polymerase II transcription preinitiation complex assembly / neuroblast proliferation / intrinsic apoptotic signaling pathway in response to DNA damage by p53 class mediator / response to X-ray / hematopoietic stem cell differentiation / Pyroptosis / viral process / embryonic organ development / chromosome organization / type II interferon-mediated signaling pathway / TP53 Regulates Transcription of Genes Involved in G1 Cell Cycle Arrest / somitogenesis / hematopoietic progenitor cell differentiation / glial cell proliferation / negative regulation of fibroblast proliferation / core promoter sequence-specific DNA binding / positive regulation of cardiac muscle cell apoptotic process / negative regulation of stem cell proliferation / cellular response to glucose starvation / mitophagy / cis-regulatory region sequence-specific DNA binding / positive regulation of intrinsic apoptotic signaling pathway / Regulation of TP53 Activity through Acetylation 類似検索 - 分子機能 | ||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2.59 Å 分子置換 / 解像度: 2.59 Å | ||||||
 データ登録者 データ登録者 | Han, C.W. / Lee, H.N. / Jeong, M.S. / Jang, S.B. | ||||||
| 資金援助 |  韓国, 1件 韓国, 1件
| ||||||
 引用 引用 |  ジャーナル: Biochem.Biophys.Res.Commun. / 年: 2021 ジャーナル: Biochem.Biophys.Res.Commun. / 年: 2021タイトル: Structural basis of the p53 DNA binding domain and PUMA complex. 著者: Han, C.W. / Lee, H.N. / Jeong, M.S. / Park, S.Y. / Jang, S.B. #1: ジャーナル: Biochem Biophys Res Commun. / 年: 2012 タイトル: In vitro binding properties of tumor suppressor p53 with PUMA and NOXA 著者: Park, S.Y. / Jang, S.B. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7dvd.cif.gz 7dvd.cif.gz | 207.2 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7dvd.ent.gz pdb7dvd.ent.gz | 132.9 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  7dvd.json.gz 7dvd.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  7dvd_validation.pdf.gz 7dvd_validation.pdf.gz | 1.6 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  7dvd_full_validation.pdf.gz 7dvd_full_validation.pdf.gz | 1.6 MB | 表示 | |
| XML形式データ |  7dvd_validation.xml.gz 7dvd_validation.xml.gz | 30.7 KB | 表示 | |
| CIF形式データ |  7dvd_validation.cif.gz 7dvd_validation.cif.gz | 42.1 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/dv/7dvd https://data.pdbj.org/pub/pdb/validation_reports/dv/7dvd ftp://data.pdbj.org/pub/pdb/validation_reports/dv/7dvd ftp://data.pdbj.org/pub/pdb/validation_reports/dv/7dvd | HTTPS FTP |
-関連構造データ
| 関連構造データ |  2wxrS S: 精密化の開始モデル |
|---|---|
| 類似構造データ |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||||||
| 2 | 
| ||||||||||||
| 3 | 
| ||||||||||||
| 4 | 
| ||||||||||||
| 5 | 
| ||||||||||||
| 単位格子 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 23229.324 Da / 分子数: 4 / 由来タイプ: 組換発現 / 詳細: Zn / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: TP53, P53 / 発現宿主: Homo sapiens (ヒト) / 遺伝子: TP53, P53 / 発現宿主:  #2: タンパク質・ペプチド | | 分子量: 1674.878 Da / 分子数: 1 / 由来タイプ: 合成 / 由来: (合成)  Homo sapiens (ヒト) / 参照: UniProt: Q9BXH1 Homo sapiens (ヒト) / 参照: UniProt: Q9BXH1#3: 化合物 | ChemComp-ZN / #4: 水 | ChemComp-HOH / | 研究の焦点であるリガンドがあるか | Y | Has protein modification | Y | |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 4.66 Å3/Da / 溶媒含有率: 73.59 % |
|---|---|
| 結晶化 | 温度: 293.15 K / 手法: 蒸気拡散法, ハンギングドロップ法 / pH: 7 / 詳細: 0.1 M Tris (pH 7.0) 20% (w/w) PEG-200 MME |
-データ収集
| 回折 | 平均測定温度: 100 K / Serial crystal experiment: N |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: PAL/PLS シンクロトロン / サイト: PAL/PLS  / ビームライン: 7A (6B, 6C1) / 波長: 0.979 Å / ビームライン: 7A (6B, 6C1) / 波長: 0.979 Å |
| 検出器 | タイプ: ADSC QUANTUM 270 / 検出器: CCD / 日付: 2019年7月26日 |
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 0.979 Å / 相対比: 1 |
| 反射 | 解像度: 2.59→50 Å / Num. obs: 62203 / % possible obs: 99.1 % / 冗長度: 3.7 % / Biso Wilson estimate: 39.24 Å2 / CC1/2: 0.915 / Net I/σ(I): 13.506 |
| 反射 シェル | 解像度: 2.5904→2.635 Å / Rmerge(I) obs: 0.323 / Num. unique obs: 2327 |
- 解析
解析
| ソフトウェア |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 分子置換開始モデル: 2WXR 解像度: 2.59→26.28 Å / SU ML: 0.3853 / 交差検証法: FREE R-VALUE / σ(F): 1.45 / 位相誤差: 34.8173 / 立体化学のターゲット値: CDL v1.2
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | 減衰半径: 0.9 Å / VDWプローブ半径: 1.11 Å / 溶媒モデル: FLAT BULK SOLVENT MODEL | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 39.84 Å2 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 2.59→26.28 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル |
|
 ムービー
ムービー コントローラー
コントローラー












 PDBj
PDBj

















