[English] 日本語
 Yorodumi
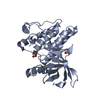
Yorodumi- PDB-6yt6: FOCAL ADHESION KINASE CATALYTIC DOMAIN IN COMPLEX WITH N-Methyl-N... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 6yt6 | ||||||
|---|---|---|---|---|---|---|---|
| Title | FOCAL ADHESION KINASE CATALYTIC DOMAIN IN COMPLEX WITH N-Methyl-N-(3-{[2-(2-oxo-2,3-dihydro-1H-indol-5-ylamino)-pyrimidin-4-ylamino]-methyl}-pyridin-2-yl)-methanesulfonamide | ||||||
 Components Components | Focal adhesion kinase 1 | ||||||
 Keywords Keywords | TRANSFERASE / PROTEIN TYROSINE KINASE / ATP BINDING / TRANSFERASE-INHIBITOR COMPLEX | ||||||
| Function / homology |  Function and homology information Function and homology informationnetrin-activated signaling pathway / regulation of substrate adhesion-dependent cell spreading / regulation of endothelial cell migration / regulation of epithelial cell migration / detection of muscle stretch / positive regulation of cell-cell adhesion mediated by integrin / JUN kinase binding / signal complex assembly / negative regulation of cell adhesion mediated by integrin / positive regulation of macrophage proliferation ...netrin-activated signaling pathway / regulation of substrate adhesion-dependent cell spreading / regulation of endothelial cell migration / regulation of epithelial cell migration / detection of muscle stretch / positive regulation of cell-cell adhesion mediated by integrin / JUN kinase binding / signal complex assembly / negative regulation of cell adhesion mediated by integrin / positive regulation of macrophage proliferation / DCC mediated attractive signaling / Signal regulatory protein family interactions / positive regulation of fibroblast migration / MET activates PTK2 signaling / growth hormone receptor signaling pathway / positive regulation of ubiquitin-dependent protein catabolic process / regulation of focal adhesion assembly / negative regulation of cell-cell adhesion / Apoptotic cleavage of cellular proteins / p130Cas linkage to MAPK signaling for integrins / positive regulation of wound healing / regulation of osteoblast differentiation / Fc-gamma receptor signaling pathway involved in phagocytosis / regulation of cytoskeleton organization / positive regulation of macrophage chemotaxis / establishment of cell polarity / vascular endothelial cell response to oscillatory fluid shear stress / GRB2:SOS provides linkage to MAPK signaling for Integrins / negative regulation of anoikis / positive regulation of epithelial cell migration / Estrogen-dependent nuclear events downstream of ESR-membrane signaling / vascular endothelial growth factor receptor signaling pathway / ephrin receptor signaling pathway / RHO GTPases Activate WASPs and WAVEs / positive regulation of epithelial to mesenchymal transition / regulation of cell adhesion / heart morphogenesis / Integrin signaling / stress fiber / EPHB-mediated forward signaling / NCAM signaling for neurite out-growth / protein tyrosine phosphatase activity / transforming growth factor beta receptor signaling pathway / SH2 domain binding / ciliary tip / Turbulent (oscillatory, disturbed) flow shear stress activates signaling by PIEZO1 and integrins in endothelial cells / placenta development / molecular function activator activity / axon guidance / integrin-mediated signaling pathway / FCGR3A-mediated phagocytosis / non-specific protein-tyrosine kinase / cell motility / non-membrane spanning protein tyrosine kinase activity / Regulation of actin dynamics for phagocytic cup formation / VEGFA-VEGFR2 Pathway / integrin binding / epidermal growth factor receptor signaling pathway / regulation of cell shape / regulation of cell population proliferation / cell migration / RAF/MAP kinase cascade / actin binding / protein tyrosine kinase activity / angiogenesis / cell cortex / protein phosphatase binding / cytoskeleton / positive regulation of phosphatidylinositol 3-kinase/protein kinase B signal transduction / Extra-nuclear estrogen signaling / cilium / positive regulation of cell migration / ciliary basal body / focal adhesion / positive regulation of cell population proliferation / centrosome / protein kinase binding / negative regulation of apoptotic process / perinuclear region of cytoplasm / ATP binding / nucleus / plasma membrane / cytosol Similarity search - Function | ||||||
| Biological species |  Homo sapiens (human) Homo sapiens (human) | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / Resolution: 1.537 Å MOLECULAR REPLACEMENT / Resolution: 1.537 Å | ||||||
 Authors Authors | Musil, D. / Heinrich, T. | ||||||
 Citation Citation |  Journal: Cell Chem Biol / Year: 2021 Journal: Cell Chem Biol / Year: 2021Title: Structure-kinetic relationship reveals the mechanism of selectivity of FAK inhibitors over PYK2. Authors: Berger, B.T. / Amaral, M. / Kokh, D.B. / Nunes-Alves, A. / Musil, D. / Heinrich, T. / Schroder, M. / Neil, R. / Wang, J. / Navratilova, I. / Bomke, J. / Elkins, J.M. / Muller, S. / Frech, M. ...Authors: Berger, B.T. / Amaral, M. / Kokh, D.B. / Nunes-Alves, A. / Musil, D. / Heinrich, T. / Schroder, M. / Neil, R. / Wang, J. / Navratilova, I. / Bomke, J. / Elkins, J.M. / Muller, S. / Frech, M. / Wade, R.C. / Knapp, S. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  6yt6.cif.gz 6yt6.cif.gz | 231.2 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb6yt6.ent.gz pdb6yt6.ent.gz | 184.1 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  6yt6.json.gz 6yt6.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/yt/6yt6 https://data.pdbj.org/pub/pdb/validation_reports/yt/6yt6 ftp://data.pdbj.org/pub/pdb/validation_reports/yt/6yt6 ftp://data.pdbj.org/pub/pdb/validation_reports/yt/6yt6 | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  6yojC  6yq1C  6yr9C  6yvsC  6yvyC  6yxvC  4gu6S S: Starting model for refinement C: citing same article ( |
|---|---|
| Similar structure data |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||
| 2 | 
| ||||||||
| Unit cell |
|
- Components
Components
| #1: Protein | Mass: 32304.221 Da / Num. of mol.: 2 Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Homo sapiens (human) / Gene: PTK2, FAK, FAK1 / Production host: Homo sapiens (human) / Gene: PTK2, FAK, FAK1 / Production host:  Trichoplusia ni (cabbage looper) Trichoplusia ni (cabbage looper)References: UniProt: Q05397, non-specific protein-tyrosine kinase #2: Chemical | #3: Chemical | ChemComp-SO4 / | #4: Water | ChemComp-HOH / | Has ligand of interest | Y | Has protein modification | Y | |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.32 Å3/Da / Density % sol: 46.91 % |
|---|---|
| Crystal grow | Temperature: 294 K / Method: vapor diffusion, hanging drop / pH: 9 / Details: 16-20 % PEG 3350, 0.1 M TRIS, pH 9.0 |
-Data collection
| Diffraction | Mean temperature: 100 K / Serial crystal experiment: N |
|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  SLS SLS  / Beamline: X06SA / Wavelength: 1.00001 Å / Beamline: X06SA / Wavelength: 1.00001 Å |
| Detector | Type: DECTRIS EIGER X 16M / Detector: PIXEL / Date: Dec 12, 2019 |
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray |
| Radiation wavelength | Wavelength: 1.00001 Å / Relative weight: 1 |
| Reflection | Resolution: 1.537→64.35 Å / Num. obs: 56803 / % possible obs: 82.7 % / Redundancy: 1.9 % / CC1/2: 0.999 / Rpim(I) all: 0.028 / Rrim(I) all: 0.04 / Net I/σ(I): 10.5 |
| Reflection shell | Resolution: 1.537→1.639 Å / Num. unique obs: 2838 / CC1/2: 0.522 / Rpim(I) all: 0.764 |
- Processing
Processing
| Software |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  MOLECULAR REPLACEMENT MOLECULAR REPLACEMENTStarting model: 4GU6 Resolution: 1.537→64.35 Å / Cor.coef. Fo:Fc: 0.957 / Cor.coef. Fo:Fc free: 0.945 / SU R Cruickshank DPI: 0.115 / Cross valid method: THROUGHOUT / σ(F): 0 / SU R Blow DPI: 0.116 / SU Rfree Blow DPI: 0.106 / SU Rfree Cruickshank DPI: 0.106
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso max: 82.04 Å2 / Biso mean: 32.88 Å2 / Biso min: 13.12 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine analyze | Luzzati coordinate error obs: 0.23 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: final / Resolution: 1.537→64.35 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Resolution: 1.54→1.6 Å / Rfactor Rfree error: 0 / Total num. of bins used: 51
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller











 PDBj
PDBj