| 登録情報 | データベース: PDB / ID: 6xv4
|
|---|
| タイトル | Neutron structure of ferric ascorbate peroxidase-ascorbate complex |
|---|
 要素 要素 | Ascorbate peroxidase |
|---|
 キーワード キーワード | OXIDOREDUCTASE / ascorbate peroxidase / neutron crystallography / heme peroxidase / proton pathway |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
L-ascorbate peroxidase / L-ascorbate peroxidase activity / hydrogen peroxide catabolic process / cellular response to oxidative stress / heme binding / metal ion binding類似検索 - 分子機能 Class I peroxidase / Heme-binding peroxidase Ccp1-like / Peroxidase; domain 2 / Peroxidase, domain 2 / Peroxidase; domain 1 - #10 / Peroxidase; domain 1 / Peroxidases heam-ligand binding site / Peroxidase, active site / Peroxidases active site signature. / Plant heme peroxidase family profile. ...Class I peroxidase / Heme-binding peroxidase Ccp1-like / Peroxidase; domain 2 / Peroxidase, domain 2 / Peroxidase; domain 1 - #10 / Peroxidase; domain 1 / Peroxidases heam-ligand binding site / Peroxidase, active site / Peroxidases active site signature. / Plant heme peroxidase family profile. / Haem peroxidase / Peroxidase / Peroxidases proximal heme-ligand signature. / Haem peroxidase superfamily / Orthogonal Bundle / Mainly Alpha類似検索 - ドメイン・相同性 ASCORBIC ACID / DEUTERATED WATER / PROTOPORPHYRIN IX CONTAINING FE / : / L-ascorbate peroxidase類似検索 - 構成要素 |
|---|
| 生物種 |   Glycine max (ダイズ) Glycine max (ダイズ) |
|---|
| 手法 |  X線回折 / 中性子回折 / NUCLEAR REACTOR / X線回折 / 中性子回折 / NUCLEAR REACTOR /  分子置換 / 解像度: 1.9 Å 分子置換 / 解像度: 1.9 Å |
|---|
 データ登録者 データ登録者 | Kwon, H. / Basran, J. / Devos, J.M. / Schrader, T.E. / Ostermann, A. / Blakeley, M.P. / Raven, E.L. / Moody, P.C.E. |
|---|
| 資金援助 |  英国, 1件 英国, 1件 | 組織 | 認可番号 | 国 |
|---|
| Biotechnology and Biological Sciences Research Council (BBSRC) | BB/N015940/1 |  英国 英国 |
|
|---|
 引用 引用 |  ジャーナル: Proc.Natl.Acad.Sci.USA / 年: 2020 ジャーナル: Proc.Natl.Acad.Sci.USA / 年: 2020
タイトル: Visualizing the protons in a metalloenzyme electron proton transfer pathway.
著者: Kwon, H. / Basran, J. / Devos, J.M. / Suardiaz, R. / van der Kamp, M.W. / Mulholland, A.J. / Schrader, T.E. / Ostermann, A. / Blakeley, M.P. / Moody, P.C.E. / Raven, E.L. |
|---|
| 履歴 | | 登録 | 2020年1月21日 | 登録サイト: PDBE / 処理サイト: PDBE |
|---|
| 改定 1.0 | 2020年3月18日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2020年4月8日 | Group: Database references / カテゴリ: citation
Item: _citation.journal_volume / _citation.page_first / _citation.page_last |
|---|
| 改定 1.2 | 2020年7月29日 | Group: Data collection / Derived calculations / カテゴリ: chem_comp / struct_site / struct_site_gen / Item: _chem_comp.type / 解説: Carbohydrate remediation / Provider: repository / タイプ: Remediation |
|---|
| 改定 1.3 | 2024年5月1日 | Group: Data collection / Database references ...Data collection / Database references / Refinement description / Structure summary
カテゴリ: chem_comp / chem_comp_atom ...chem_comp / chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model
Item: _chem_comp.pdbx_synonyms / _database_2.pdbx_DOI / _database_2.pdbx_database_accession |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 X線回折 / 中性子回折 / NUCLEAR REACTOR /
X線回折 / 中性子回折 / NUCLEAR REACTOR /  分子置換 / 解像度: 1.9 Å
分子置換 / 解像度: 1.9 Å  データ登録者
データ登録者 英国, 1件
英国, 1件  引用
引用 ジャーナル: Proc.Natl.Acad.Sci.USA / 年: 2020
ジャーナル: Proc.Natl.Acad.Sci.USA / 年: 2020 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 6xv4.cif.gz
6xv4.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb6xv4.ent.gz
pdb6xv4.ent.gz PDB形式
PDB形式 6xv4.json.gz
6xv4.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/xv/6xv4
https://data.pdbj.org/pub/pdb/validation_reports/xv/6xv4 ftp://data.pdbj.org/pub/pdb/validation_reports/xv/6xv4
ftp://data.pdbj.org/pub/pdb/validation_reports/xv/6xv4 リンク
リンク 集合体
集合体

 要素
要素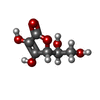






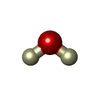



 試料調製
試料調製 解析
解析 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj








