| 登録情報 | データベース: PDB / ID: 6t7z
|
|---|
| タイトル | KEAP1 IN COMPLEX WITH COMPOUND 44 |
|---|
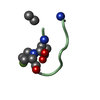
 要素 要素 | - ACE-CYS-ASA-4FB-GLU-THR-GLY-GLU-CYS-NH2
- Kelch-like ECH-associated protein 1
|
|---|
 キーワード キーワード | TRANSCRIPTION / KEAP1 / UBIQUITINYLATION / INRF2 / KIAA0132 / KLHL19 / PROTEROS BIOSTRUCTURES GMBH |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
regulation of epidermal cell differentiation / Nuclear events mediated by NFE2L2 / negative regulation of response to oxidative stress / Cul3-RING ubiquitin ligase complex / ubiquitin-like ligase-substrate adaptor activity / transcription regulator inhibitor activity / inclusion body / cellular response to interleukin-4 / actin filament / centriolar satellite ...regulation of epidermal cell differentiation / Nuclear events mediated by NFE2L2 / negative regulation of response to oxidative stress / Cul3-RING ubiquitin ligase complex / ubiquitin-like ligase-substrate adaptor activity / transcription regulator inhibitor activity / inclusion body / cellular response to interleukin-4 / actin filament / centriolar satellite / disordered domain specific binding / KEAP1-NFE2L2 pathway / Antigen processing: Ubiquitination & Proteasome degradation / positive regulation of proteasomal ubiquitin-dependent protein catabolic process / Neddylation / cellular response to oxidative stress / midbody / ubiquitin-dependent protein catabolic process / in utero embryonic development / Potential therapeutics for SARS / proteasome-mediated ubiquitin-dependent protein catabolic process / RNA polymerase II-specific DNA-binding transcription factor binding / Ub-specific processing proteases / regulation of autophagy / protein ubiquitination / endoplasmic reticulum / negative regulation of transcription by RNA polymerase II / nucleoplasm / identical protein binding / cytoplasm / cytosol類似検索 - 分子機能 Kelch-like ECH-associated protein 1 / : / KLHDC2/KLHL20/DRC7 Kelch-repeats domain / BTB-kelch protein / BTB/Kelch-associated / BTB And C-terminal Kelch / BTB And C-terminal Kelch / Kelch motif / Kelch / Kelch repeat type 1 ...Kelch-like ECH-associated protein 1 / : / KLHDC2/KLHL20/DRC7 Kelch-repeats domain / BTB-kelch protein / BTB/Kelch-associated / BTB And C-terminal Kelch / BTB And C-terminal Kelch / Kelch motif / Kelch / Kelch repeat type 1 / Kelch-type beta propeller / BTB/POZ domain / BTB domain profile. / Broad-Complex, Tramtrack and Bric a brac / BTB/POZ domain / SKP1/BTB/POZ domain superfamily類似検索 - ドメイン・相同性 ACETATE ION / Kelch-like ECH-associated protein 1類似検索 - 構成要素 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト)
synthetic construct (人工物) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2 Å 分子置換 / 解像度: 2 Å |
|---|
 データ登録者 データ登録者 | Colarusso, S. |
|---|
 引用 引用 |  ジャーナル: Bioorg.Med.Chem. / 年: 2020 ジャーナル: Bioorg.Med.Chem. / 年: 2020
タイトル: Optimization of linear and cyclic peptide inhibitors of KEAP1-NRF2 protein-protein interaction.
著者: Colarusso, S. / De Simone, D. / Frattarelli, T. / Andreini, M. / Cerretani, M. / Missineo, A. / Moretti, D. / Tambone, S. / Kempf, G. / Augustin, M. / Steinbacher, S. / Munoz-Sanjuan, I. / ...著者: Colarusso, S. / De Simone, D. / Frattarelli, T. / Andreini, M. / Cerretani, M. / Missineo, A. / Moretti, D. / Tambone, S. / Kempf, G. / Augustin, M. / Steinbacher, S. / Munoz-Sanjuan, I. / Park, L. / Summa, V. / Tomei, L. / Bresciani, A. / Dominguez, C. / Toledo-Sherman, L. / Bianchi, E. |
|---|
| 履歴 | | 登録 | 2019年10月23日 | 登録サイト: PDBE / 処理サイト: PDBE |
|---|
| 改定 1.0 | 2020年9月9日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2020年10月28日 | Group: Database references / カテゴリ: citation / citation_author
Item: _citation.journal_volume / _citation.page_first ..._citation.journal_volume / _citation.page_first / _citation.page_last / _citation.pdbx_database_id_PubMed / _citation.title |
|---|
| 改定 2.0 | 2023年5月24日 | Group: Advisory / Atomic model ...Advisory / Atomic model / Database references / Derived calculations / Non-polymer description / Polymer sequence / Source and taxonomy / Structure summary
カテゴリ: atom_site / chem_comp ...atom_site / chem_comp / database_2 / entity / entity_poly / entity_poly_seq / entity_src_gen / pdbx_entity_src_syn / pdbx_poly_seq_scheme / pdbx_unobs_or_zero_occ_atoms / struct_conn / struct_conn_type / struct_ref_seq / struct_site / struct_site_gen
Item: _atom_site.B_iso_or_equiv / _atom_site.Cartn_x ..._atom_site.B_iso_or_equiv / _atom_site.Cartn_x / _atom_site.Cartn_y / _atom_site.Cartn_z / _atom_site.auth_atom_id / _atom_site.auth_comp_id / _atom_site.auth_seq_id / _atom_site.group_PDB / _atom_site.label_atom_id / _atom_site.label_comp_id / _atom_site.label_seq_id / _atom_site.type_symbol / _chem_comp.formula / _chem_comp.formula_weight / _chem_comp.id / _chem_comp.name / _database_2.pdbx_DOI / _database_2.pdbx_database_accession / _entity.formula_weight / _entity.pdbx_description / _entity_poly.pdbx_seq_one_letter_code / _entity_poly.pdbx_seq_one_letter_code_can / _entity_src_gen.gene_src_common_name / _pdbx_entity_src_syn.pdbx_beg_seq_num / _pdbx_entity_src_syn.pdbx_end_seq_num / _struct_ref_seq.db_align_end / _struct_ref_seq.pdbx_auth_seq_align_end / _struct_ref_seq.seq_align_end |
|---|
| 改定 3.0 | 2024年6月26日 | Group: Atomic model / Data collection ...Atomic model / Data collection / Derived calculations / Non-polymer description / Polymer sequence / Structure summary
カテゴリ: atom_site / chem_comp ...atom_site / chem_comp / chem_comp_atom / chem_comp_bond / entity / entity_poly / entity_poly_seq / pdbx_poly_seq_scheme / struct_conn / struct_site / struct_site_gen
Item: _atom_site.auth_comp_id / _atom_site.group_PDB ..._atom_site.auth_comp_id / _atom_site.group_PDB / _atom_site.label_comp_id / _chem_comp.formula / _chem_comp.formula_weight / _chem_comp.id / _chem_comp.mon_nstd_flag / _chem_comp.name / _chem_comp.type / _entity.formula_weight / _entity_poly.pdbx_seq_one_letter_code / _entity_poly_seq.mon_id / _pdbx_poly_seq_scheme.mon_id / _pdbx_poly_seq_scheme.pdb_mon_id / _struct_site.pdbx_auth_comp_id / _struct_site_gen.auth_comp_id / _struct_site_gen.label_comp_id |
|---|
| 改定 3.1 | 2024年11月6日 | Group: Structure summary
カテゴリ: pdbx_entry_details / pdbx_modification_feature
Item: _pdbx_entry_details.has_protein_modification |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 2 Å
分子置換 / 解像度: 2 Å  データ登録者
データ登録者 引用
引用 ジャーナル: Bioorg.Med.Chem. / 年: 2020
ジャーナル: Bioorg.Med.Chem. / 年: 2020 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 6t7z.cif.gz
6t7z.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb6t7z.ent.gz
pdb6t7z.ent.gz PDB形式
PDB形式 6t7z.json.gz
6t7z.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/t7/6t7z
https://data.pdbj.org/pub/pdb/validation_reports/t7/6t7z ftp://data.pdbj.org/pub/pdb/validation_reports/t7/6t7z
ftp://data.pdbj.org/pub/pdb/validation_reports/t7/6t7z リンク
リンク 集合体
集合体
 要素
要素 Homo sapiens (ヒト) / 遺伝子: KEAP1, INRF2, KIAA0132, KLHL19 / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: KEAP1, INRF2, KIAA0132, KLHL19 / 発現宿主: 
 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  SLS
SLS  / ビームライン: X06SA / 波長: 1.00001 Å
/ ビームライン: X06SA / 波長: 1.00001 Å 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー















 PDBj
PDBj






