| 登録情報 | データベース: PDB / ID: 6rb2
|
|---|
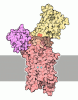
| タイトル | Structure of the (SR)Ca2+-ATPase mutant E340A in the Ca2-E1-CaAMPPCP form |
|---|
 要素 要素 | Sarcoplasmic/endoplasmic reticulum calcium ATPase 1 |
|---|
 キーワード キーワード | HYDROLASE / Mutant E340A / P-type ATPase / Calcium-transporting ATPase / sarcoplasmic reticulum |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
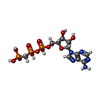
positive regulation of calcium ion import into sarcoplasmic reticulum / positive regulation of ATPase-coupled calcium transmembrane transporter activity / positive regulation of fast-twitch skeletal muscle fiber contraction / H zone / regulation of striated muscle contraction / calcium ion import into sarcoplasmic reticulum / negative regulation of striated muscle contraction / P-type Ca2+ transporter / P-type calcium transporter activity / positive regulation of cardiac muscle cell contraction ...positive regulation of calcium ion import into sarcoplasmic reticulum / positive regulation of ATPase-coupled calcium transmembrane transporter activity / positive regulation of fast-twitch skeletal muscle fiber contraction / H zone / regulation of striated muscle contraction / calcium ion import into sarcoplasmic reticulum / negative regulation of striated muscle contraction / P-type Ca2+ transporter / P-type calcium transporter activity / positive regulation of cardiac muscle cell contraction / I band / endoplasmic reticulum-Golgi intermediate compartment / sarcoplasmic reticulum membrane / sarcoplasmic reticulum / calcium ion transport / calcium ion binding / endoplasmic reticulum membrane / perinuclear region of cytoplasm / endoplasmic reticulum / ATP hydrolysis activity / ATP binding / membrane類似検索 - 分子機能 P-type ATPase, subfamily IIA, SERCA-type / Calcium-transporting ATPase, cytoplasmic domain N / Calcium-transporting ATPase, cytoplasmic domain N / haloacid dehalogenase-like hydrolase / Cation-transporting P-type ATPase, C-terminal / Cation transporting ATPase, C-terminus / Cation transporter/ATPase, N-terminus / Cation-transporting P-type ATPase, N-terminal / Cation transporter/ATPase, N-terminus / P-type ATPase, cytoplasmic domain N ...P-type ATPase, subfamily IIA, SERCA-type / Calcium-transporting ATPase, cytoplasmic domain N / Calcium-transporting ATPase, cytoplasmic domain N / haloacid dehalogenase-like hydrolase / Cation-transporting P-type ATPase, C-terminal / Cation transporting ATPase, C-terminus / Cation transporter/ATPase, N-terminus / Cation-transporting P-type ATPase, N-terminal / Cation transporter/ATPase, N-terminus / P-type ATPase, cytoplasmic domain N / : / P-type ATPase actuator domain / P-type ATPase, haloacid dehalogenase domain / P-type ATPase, phosphorylation site / P-type ATPase, cytoplasmic domain N / E1-E2 ATPases phosphorylation site. / P-type ATPase, A domain superfamily / P-type ATPase / P-type ATPase, transmembrane domain superfamily / HAD superfamily / HAD-like superfamily / 3-Layer(aba) Sandwich / Alpha Beta類似検索 - ドメイン・相同性 PHOSPHOMETHYLPHOSPHONIC ACID ADENYLATE ESTER / : / Sarcoplasmic/endoplasmic reticulum calcium ATPase 1類似検索 - 構成要素 |
|---|
| 生物種 |   Oryctolagus cuniculus (ウサギ) Oryctolagus cuniculus (ウサギ) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 3.20001129942 Å 分子置換 / 解像度: 3.20001129942 Å |
|---|
 データ登録者 データ登録者 | Clausen, J.D. / Montigny, C. / Lenoir, G. / Arnou, B. / Jaxel, C. / Moller, J.V. / Nissen, P. / Andersen, J.P. / Le Maire, M. / Bublitz, M. |
|---|
| 資金援助 |  フランス, 1件 フランス, 1件 | 組織 | 認可番号 | 国 |
|---|
| French Infrastructure for Integrated Structural Biology | ANR-10-INSB-05 |  フランス フランス |
|
|---|
 引用 引用 |  ジャーナル: Proc.Natl.Acad.Sci.USA / 年: 2020 ジャーナル: Proc.Natl.Acad.Sci.USA / 年: 2020
タイトル: The SERCA residue Glu340 mediates interdomain communication that guides Ca 2+ transport.
著者: Geurts, M.M.G. / Clausen, J.D. / Arnou, B. / Montigny, C. / Lenoir, G. / Corey, R.A. / Jaxel, C. / Moller, J.V. / Nissen, P. / Andersen, J.P. / le Maire, M. / Bublitz, M. |
|---|
| 履歴 | | 登録 | 2019年4月9日 | 登録サイト: PDBE / 処理サイト: PDBE |
|---|
| 改定 1.0 | 2020年5月6日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2020年12月9日 | Group: Database references / カテゴリ: citation / citation_author
Item: _citation.country / _citation.journal_abbrev ..._citation.country / _citation.journal_abbrev / _citation.journal_id_ASTM / _citation.journal_id_CSD / _citation.journal_id_ISSN / _citation.pdbx_database_id_DOI / _citation.pdbx_database_id_PubMed / _citation.title / _citation.year |
|---|
| 改定 1.2 | 2020年12月16日 | Group: Database references / カテゴリ: citation / citation_author
Item: _citation.journal_volume / _citation.page_first ..._citation.journal_volume / _citation.page_first / _citation.page_last / _citation_author.identifier_ORCID |
|---|
| 改定 1.3 | 2024年1月24日 | Group: Data collection / Database references / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 3.20001129942 Å
分子置換 / 解像度: 3.20001129942 Å  データ登録者
データ登録者 フランス, 1件
フランス, 1件  引用
引用 ジャーナル: Proc.Natl.Acad.Sci.USA / 年: 2020
ジャーナル: Proc.Natl.Acad.Sci.USA / 年: 2020 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 6rb2.cif.gz
6rb2.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb6rb2.ent.gz
pdb6rb2.ent.gz PDB形式
PDB形式 6rb2.json.gz
6rb2.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/rb/6rb2
https://data.pdbj.org/pub/pdb/validation_reports/rb/6rb2 ftp://data.pdbj.org/pub/pdb/validation_reports/rb/6rb2
ftp://data.pdbj.org/pub/pdb/validation_reports/rb/6rb2
 リンク
リンク 集合体
集合体
 要素
要素

 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  ESRF
ESRF  / ビームライン: ID23-2 / 波長: 0.8729 Å
/ ビームライン: ID23-2 / 波長: 0.8729 Å 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー














 PDBj
PDBj