| 登録情報 | データベース: PDB / ID: 6pdj
|
|---|
| タイトル | Tyrosine-protein kinase LCK bound to Compound 11 |
|---|
 要素 要素 | Tyrosine-protein kinase Lck |
|---|
 キーワード キーワード | SIGNALING PROTEIN/INHIBITOR / inhibitor / SIGNALING PROTEIN / SIGNALING PROTEIN-INHIBITOR complex |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
regulation of lymphocyte activation / positive regulation of leukocyte cell-cell adhesion / CD27 signaling pathway / regulation of regulatory T cell differentiation / gamma-delta T cell differentiation / positive regulation of gamma-delta T cell differentiation / Fc-gamma receptor signaling pathway / FLT3 signaling through SRC family kinases / protein antigen binding / Nef Mediated CD4 Down-regulation ...regulation of lymphocyte activation / positive regulation of leukocyte cell-cell adhesion / CD27 signaling pathway / regulation of regulatory T cell differentiation / gamma-delta T cell differentiation / positive regulation of gamma-delta T cell differentiation / Fc-gamma receptor signaling pathway / FLT3 signaling through SRC family kinases / protein antigen binding / Nef Mediated CD4 Down-regulation / intracellular zinc ion homeostasis / Nef and signal transduction / CD4 receptor binding / positive regulation of heterotypic cell-cell adhesion / Co-stimulation by CD28 / Interleukin-2 signaling / CD28 dependent Vav1 pathway / peptidyl-tyrosine autophosphorylation / Regulation of KIT signaling / leukocyte migration / phospholipase activator activity / Co-inhibition by CTLA4 / CD8 receptor binding / Translocation of ZAP-70 to Immunological synapse / Phosphorylation of CD3 and TCR zeta chains / positive regulation of T cell receptor signaling pathway / pericentriolar material / protein serine/threonine phosphatase activity / PECAM1 interactions / hemopoiesis / RHOH GTPase cycle / Generation of second messenger molecules / T cell differentiation / immunological synapse / Co-inhibition by PD-1 / CD28 dependent PI3K/Akt signaling / T cell receptor binding / phospholipase binding / phosphatidylinositol 3-kinase binding / positive regulation of intrinsic apoptotic signaling pathway / GPVI-mediated activation cascade / T cell costimulation / release of sequestered calcium ion into cytosol / phosphotyrosine residue binding / SH2 domain binding / cell surface receptor protein tyrosine kinase signaling pathway / T cell activation / Signaling by phosphorylated juxtamembrane, extracellular and kinase domain KIT mutants / peptidyl-tyrosine phosphorylation / B cell receptor signaling pathway / non-membrane spanning protein tyrosine kinase activity / non-specific protein-tyrosine kinase / Signaling by SCF-KIT / positive regulation of T cell activation / platelet activation / Constitutive Signaling by Aberrant PI3K in Cancer / Downstream TCR signaling / cell-cell junction / DAP12 signaling / PIP3 activates AKT signaling / T cell receptor signaling pathway / ATPase binding / PI5P, PP2A and IER3 Regulate PI3K/AKT Signaling / protein tyrosine kinase activity / protein phosphatase binding / protein phosphorylation / intracellular signal transduction / membrane raft / response to xenobiotic stimulus / signaling receptor binding / positive regulation of gene expression / protein kinase binding / extracellular exosome / ATP binding / identical protein binding / plasma membrane / cytosol / cytoplasm類似検索 - 分子機能 Lck, SH3 domain / Tyrosine-protein kinase Lck, SH2 domain / : / SH3 domain / SH2 domain / Src homology 2 (SH2) domain profile. / Src homology 2 domains / SH2 domain / Src homology 3 domains / SH2 domain superfamily ...Lck, SH3 domain / Tyrosine-protein kinase Lck, SH2 domain / : / SH3 domain / SH2 domain / Src homology 2 (SH2) domain profile. / Src homology 2 domains / SH2 domain / Src homology 3 domains / SH2 domain superfamily / SH3-like domain superfamily / Src homology 3 (SH3) domain profile. / SH3 domain / Tyrosine-protein kinase, catalytic domain / Tyrosine kinase, catalytic domain / Tyrosine protein kinases specific active-site signature. / Tyrosine-protein kinase, active site / Serine-threonine/tyrosine-protein kinase, catalytic domain / Protein tyrosine and serine/threonine kinase / Phosphorylase Kinase; domain 1 / Phosphorylase Kinase; domain 1 / Transferase(Phosphotransferase) domain 1 / Transferase(Phosphotransferase); domain 1 / Protein kinase, ATP binding site / Protein kinases ATP-binding region signature. / Protein kinase domain profile. / Protein kinase domain / Protein kinase-like domain superfamily / 2-Layer Sandwich / Orthogonal Bundle / Mainly Alpha / Alpha Beta類似検索 - ドメイン・相同性 NICKEL (II) ION / Chem-ODJ / Tyrosine-protein kinase Lck類似検索 - 構成要素 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.81 Å 分子置換 / 解像度: 1.81 Å |
|---|
 データ登録者 データ登録者 | Critton, D.A. |
|---|
 引用 引用 |  ジャーナル: Acs Med.Chem.Lett. / 年: 2019 ジャーナル: Acs Med.Chem.Lett. / 年: 2019
タイトル: Discovery of Pyridazinone and Pyrazolo[1,5-a]pyridine Inhibitors of C-Terminal Src Kinase.
著者: O'Malley, D.P. / Ahuja, V. / Fink, B. / Cao, C. / Wang, C. / Swanson, J. / Wee, S. / Gavai, A.V. / Tokarski, J. / Critton, D. / Paiva, A.A. / Johnson, B.M. / Szapiel, N. / Xie, D. |
|---|
| 履歴 | | 登録 | 2019年6月19日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2019年10月9日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2019年10月30日 | Group: Data collection / Database references / カテゴリ: citation / citation_author
Item: _citation.journal_volume / _citation.page_first ..._citation.journal_volume / _citation.page_first / _citation.page_last / _citation.pdbx_database_id_PubMed / _citation.title / _citation_author.name |
|---|
| 改定 1.2 | 2023年10月11日 | Group: Data collection / Database references ...Data collection / Database references / Derived calculations / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model / pdbx_struct_conn_angle / software / struct_conn / struct_conn_type
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_struct_conn_angle.ptnr1_auth_comp_id / _pdbx_struct_conn_angle.ptnr1_auth_seq_id / _pdbx_struct_conn_angle.ptnr1_label_asym_id / _pdbx_struct_conn_angle.ptnr1_label_atom_id / _pdbx_struct_conn_angle.ptnr1_label_comp_id / _pdbx_struct_conn_angle.ptnr1_label_seq_id / _pdbx_struct_conn_angle.ptnr1_symmetry / _pdbx_struct_conn_angle.ptnr3_auth_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_seq_id / _pdbx_struct_conn_angle.ptnr3_label_asym_id / _pdbx_struct_conn_angle.ptnr3_label_atom_id / _pdbx_struct_conn_angle.ptnr3_label_comp_id / _pdbx_struct_conn_angle.ptnr3_label_seq_id / _pdbx_struct_conn_angle.ptnr3_symmetry / _pdbx_struct_conn_angle.value / _software.name / _struct_conn.conn_type_id / _struct_conn.id / _struct_conn.pdbx_dist_value / _struct_conn.pdbx_leaving_atom_flag / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_conn.ptnr2_label_seq_id / _struct_conn.ptnr2_symmetry / _struct_conn_type.id |
|---|
| 改定 1.3 | 2023年11月15日 | Group: Data collection / カテゴリ: chem_comp_atom / chem_comp_bond / Item: _chem_comp_atom.atom_id / _chem_comp_bond.atom_id_2 |
|---|
| 改定 1.4 | 2024年10月30日 | Group: Structure summary
カテゴリ: pdbx_entry_details / pdbx_modification_feature
Item: _pdbx_entry_details.has_protein_modification |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 1.81 Å
分子置換 / 解像度: 1.81 Å  データ登録者
データ登録者 引用
引用 ジャーナル: Acs Med.Chem.Lett. / 年: 2019
ジャーナル: Acs Med.Chem.Lett. / 年: 2019 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 6pdj.cif.gz
6pdj.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb6pdj.ent.gz
pdb6pdj.ent.gz PDB形式
PDB形式 6pdj.json.gz
6pdj.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 6pdj_validation.pdf.gz
6pdj_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 6pdj_full_validation.pdf.gz
6pdj_full_validation.pdf.gz 6pdj_validation.xml.gz
6pdj_validation.xml.gz 6pdj_validation.cif.gz
6pdj_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/pd/6pdj
https://data.pdbj.org/pub/pdb/validation_reports/pd/6pdj ftp://data.pdbj.org/pub/pdb/validation_reports/pd/6pdj
ftp://data.pdbj.org/pub/pdb/validation_reports/pd/6pdj
 リンク
リンク 集合体
集合体
 要素
要素 Homo sapiens (ヒト) / 遺伝子: LCK
Homo sapiens (ヒト) / 遺伝子: LCK
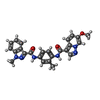
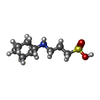







 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  APS
APS  / ビームライン: 17-ID / 波長: 1 Å
/ ビームライン: 17-ID / 波長: 1 Å 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj



















