| 登録情報 | データベース: PDB / ID: 6okw
|
|---|
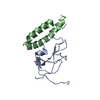
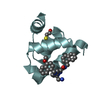
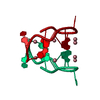
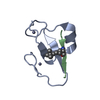
| タイトル | Solution structure of VEK50 |
|---|
 要素 要素 | Plasminogen-binding group A streptococcal M-like protein PAM |
|---|
 キーワード キーワード | PROTEIN BINDING / Plasminogen binding peptide |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
plasminogen activation / extracellular region類似検索 - 分子機能 Plasminogen ligand, VEK-30 / Plasminogen (Pg) ligand in fibrinolytic pathway / : / Streptococcal M proteins D repeats region profile. / : / Streptococcal M proteins C repeat profile. / YSIRK Gram-positive signal peptide類似検索 - ドメイン・相同性 Plasminogen-binding group A streptococcal M-like protein PAM類似検索 - 構成要素 |
|---|
| 生物種 |  Streptococcus pyogenes (化膿レンサ球菌) Streptococcus pyogenes (化膿レンサ球菌) |
|---|
| 手法 | 溶液NMR / simulated annealing |
|---|
 データ登録者 データ登録者 | Yuan, Y. / Castellino, F.J. |
|---|
| 資金援助 |  米国, 1件 米国, 1件 | 組織 | 認可番号 | 国 |
|---|
| National Institutes of Health/National Human Genome Research Institute (NIH/NHGRI) | HL013423 |  米国 米国 |
|
|---|
 引用 引用 |  ジャーナル: J.Struct.Biol. / 年: 2019 ジャーナル: J.Struct.Biol. / 年: 2019
タイトル: Solution structural model of the complex of the binding regions of human plasminogen with its M-protein receptor from Streptococcus pyogenes.
著者: Yuan, Y. / Ayinuola, Y.A. / Singh, D. / Ayinuola, O. / Mayfield, J.A. / Quek, A. / Whisstock, J.C. / Law, R.H.P. / Lee, S.W. / Ploplis, V.A. / Castellino, F.J. |
|---|
| 履歴 | | 登録 | 2019年4月15日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2020年2月26日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2023年6月14日 | Group: Database references / Other / カテゴリ: database_2 / pdbx_database_status
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_database_status.status_code_nmr_data |
|---|
| 改定 1.2 | 2024年5月15日 | Group: Data collection / Database references / カテゴリ: chem_comp_atom / chem_comp_bond / database_2 / Item: _database_2.pdbx_DOI |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Streptococcus pyogenes (化膿レンサ球菌)
Streptococcus pyogenes (化膿レンサ球菌) データ登録者
データ登録者 米国, 1件
米国, 1件  引用
引用 ジャーナル: J.Struct.Biol. / 年: 2019
ジャーナル: J.Struct.Biol. / 年: 2019 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 6okw.cif.gz
6okw.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb6okw.ent.gz
pdb6okw.ent.gz PDB形式
PDB形式 6okw.json.gz
6okw.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 6okw_validation.pdf.gz
6okw_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 6okw_full_validation.pdf.gz
6okw_full_validation.pdf.gz 6okw_validation.xml.gz
6okw_validation.xml.gz 6okw_validation.cif.gz
6okw_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/ok/6okw
https://data.pdbj.org/pub/pdb/validation_reports/ok/6okw ftp://data.pdbj.org/pub/pdb/validation_reports/ok/6okw
ftp://data.pdbj.org/pub/pdb/validation_reports/ok/6okw リンク
リンク 集合体
集合体
 要素
要素 Streptococcus pyogenes (化膿レンサ球菌)
Streptococcus pyogenes (化膿レンサ球菌)
 試料調製
試料調製 解析
解析 ムービー
ムービー コントローラー
コントローラー














 PDBj
PDBj HSQC
HSQC