登録情報 データベース : PDB / ID : 5oqsタイトル Solution structure of antifungal protein NFAP NFAP キーワード / / / 機能・相同性 / / / / / 生物種 Aspergillus fischeri NRRL 181 (カビ)手法 / / データ登録者 Hajdu, D. / Czajlik, A. / Marx, F. / Galgoczy, L. / Batta, G. 資金援助 組織 認可番号 国 NKFIH ANN 110821 European Union GINOP-2.3.2-15-2016-00008 Austrian Science Fund M1776-B20
ジャーナル : Int.J.Biol.Macromol. / 年 : 2019タイトル : Solution structure and novel insights into phylogeny and mode of action of the Neosartorya (Aspergillus) fischeri antifungal protein (NFAP).著者 : Hajdu, D. / Huber, A. / Czajlik, A. / Toth, L. / Kele, Z. / Kocsube, S. / Fizil, A. / Marx, F. / Galgoczy, L. / Batta, G. 履歴 登録 2017年8月14日 登録サイト / 処理サイト 改定 1.0 2018年7月25日 Provider / タイプ 改定 1.1 2019年5月8日 Group / カテゴリ / Item 改定 1.2 2019年8月14日 Group / Database references / Source and taxonomyカテゴリ citation / citation_author ... citation / citation_author / entity_src_gen / pdbx_nmr_spectrometer Item _citation.country / _citation.journal_abbrev ... _citation.country / _citation.journal_abbrev / _citation.journal_id_ASTM / _citation.journal_id_CSD / _citation.journal_id_ISSN / _citation.journal_volume / _citation.page_first / _citation.page_last / _citation.pdbx_database_id_DOI / _citation.pdbx_database_id_PubMed / _citation.title / _citation.year / _entity_src_gen.pdbx_gene_src_scientific_name / _pdbx_nmr_spectrometer.model 改定 1.3 2021年6月23日 Group / Derived calculations / カテゴリ / struct_connItem _pdbx_nmr_spectrometer.field_strength / _struct_conn.pdbx_dist_value ... _pdbx_nmr_spectrometer.field_strength / _struct_conn.pdbx_dist_value / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_seq_id 改定 1.4 2023年6月14日 Group / Other / カテゴリ / pdbx_database_statusItem / _database_2.pdbx_database_accession / _pdbx_database_status.status_code_nmr_data改定 1.5 2024年10月23日 Group / Database references / Structure summaryカテゴリ chem_comp_atom / chem_comp_bond ... chem_comp_atom / chem_comp_bond / database_2 / pdbx_entry_details / pdbx_modification_feature Item
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 データ登録者
データ登録者 ハンガリー,
ハンガリー,  オーストリア, 3件
オーストリア, 3件  引用
引用 ジャーナル: Int.J.Biol.Macromol. / 年: 2019
ジャーナル: Int.J.Biol.Macromol. / 年: 2019 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 5oqs.cif.gz
5oqs.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb5oqs.ent.gz
pdb5oqs.ent.gz PDB形式
PDB形式 5oqs.json.gz
5oqs.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/oq/5oqs
https://data.pdbj.org/pub/pdb/validation_reports/oq/5oqs ftp://data.pdbj.org/pub/pdb/validation_reports/oq/5oqs
ftp://data.pdbj.org/pub/pdb/validation_reports/oq/5oqs リンク
リンク 集合体
集合体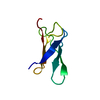
 要素
要素
 Penicillium chrysogenum (菌類) / 株 (発現宿主): Wis. Q176 / 参照: UniProt: A1D8H8
Penicillium chrysogenum (菌類) / 株 (発現宿主): Wis. Q176 / 参照: UniProt: A1D8H8 試料調製
試料調製 解析
解析 ムービー
ムービー コントローラー
コントローラー





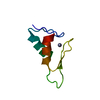







 PDBj
PDBj HSQC
HSQC