+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 5f32 | ||||||
|---|---|---|---|---|---|---|---|
| Title | Crystal structure of human KDM4A in complex with compound 40 | ||||||
 Components Components | Lysine-specific demethylase 4A | ||||||
 Keywords Keywords | OXIDOREDUCTASE / Epigenetics / Demethylase / Inhibitor | ||||||
| Function / homology |  Function and homology information Function and homology information[histone H3]-trimethyl-L-lysine36 demethylase / histone H3K36me2/H3K36me3 demethylase activity / histone H4K20me2 reader activity / histone H3K36 demethylase activity / cardiac muscle hypertrophy in response to stress / [histone H3]-trimethyl-L-lysine9 demethylase / histone H3K9me2/H3K9me3 demethylase activity / histone H3K9 demethylase activity / histone demethylase activity / pericentric heterochromatin ...[histone H3]-trimethyl-L-lysine36 demethylase / histone H3K36me2/H3K36me3 demethylase activity / histone H4K20me2 reader activity / histone H3K36 demethylase activity / cardiac muscle hypertrophy in response to stress / [histone H3]-trimethyl-L-lysine9 demethylase / histone H3K9me2/H3K9me3 demethylase activity / histone H3K9 demethylase activity / histone demethylase activity / pericentric heterochromatin / NR1H3 & NR1H2 regulate gene expression linked to cholesterol transport and efflux / negative regulation of autophagy / HDMs demethylate histones / fibrillar center / Recruitment and ATM-mediated phosphorylation of repair and signaling proteins at DNA double strand breaks / regulation of gene expression / chromatin remodeling / negative regulation of gene expression / negative regulation of DNA-templated transcription / ubiquitin protein ligase binding / chromatin / zinc ion binding / nucleoplasm / nucleus / cytosol Similarity search - Function | ||||||
| Biological species |  Homo sapiens (human) Homo sapiens (human) | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / Resolution: 2.05 Å MOLECULAR REPLACEMENT / Resolution: 2.05 Å | ||||||
 Authors Authors | Le Bihan, Y.-V. / Dempster, S. / Westwood, I.M. / van Montfort, R.L.M. | ||||||
| Funding support |  United Kingdom, 1items United Kingdom, 1items
| ||||||
 Citation Citation |  Journal: J.Med.Chem. / Year: 2016 Journal: J.Med.Chem. / Year: 2016Title: 8-Substituted Pyrido[3,4-d]pyrimidin-4(3H)-one Derivatives As Potent, Cell Permeable, KDM4 (JMJD2) and KDM5 (JARID1) Histone Lysine Demethylase Inhibitors. Authors: Bavetsias, V. / Lanigan, R.M. / Ruda, G.F. / Atrash, B. / McLaughlin, M.G. / Tumber, A. / Mok, N.Y. / Le Bihan, Y.V. / Dempster, S. / Boxall, K.J. / Jeganathan, F. / Hatch, S.B. / Savitsky, ...Authors: Bavetsias, V. / Lanigan, R.M. / Ruda, G.F. / Atrash, B. / McLaughlin, M.G. / Tumber, A. / Mok, N.Y. / Le Bihan, Y.V. / Dempster, S. / Boxall, K.J. / Jeganathan, F. / Hatch, S.B. / Savitsky, P. / Velupillai, S. / Krojer, T. / England, K.S. / Sejberg, J. / Thai, C. / Donovan, A. / Pal, A. / Scozzafava, G. / Bennett, J.M. / Kawamura, A. / Johansson, C. / Szykowska, A. / Gileadi, C. / Burgess-Brown, N.A. / von Delft, F. / Oppermann, U. / Walters, Z. / Shipley, J. / Raynaud, F.I. / Westaway, S.M. / Prinjha, R.K. / Fedorov, O. / Burke, R. / Schofield, C.J. / Westwood, I.M. / Bountra, C. / Muller, S. / van Montfort, R.L. / Brennan, P.E. / Blagg, J. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  5f32.cif.gz 5f32.cif.gz | 587.2 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb5f32.ent.gz pdb5f32.ent.gz | 484.9 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  5f32.json.gz 5f32.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/f3/5f32 https://data.pdbj.org/pub/pdb/validation_reports/f3/5f32 ftp://data.pdbj.org/pub/pdb/validation_reports/f3/5f32 ftp://data.pdbj.org/pub/pdb/validation_reports/f3/5f32 | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  5f2sC  5f2wC  5f37C  5f39C  5f3cC  5f3eC  5f3gC  5f3iC  5f5aC  5f5cC  5f5iC  5fplC  2oq7S S: Starting model for refinement C: citing same article ( |
|---|---|
| Similar structure data |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||
| 2 | 
| ||||||||
| 3 | 
| ||||||||
| 4 | 
| ||||||||
| Unit cell |
|
- Components
Components
-Protein , 1 types, 4 molecules ABCD
| #1: Protein | Mass: 41854.617 Da / Num. of mol.: 4 Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Homo sapiens (human) / Gene: KDM4A, JHDM3A, JMJD2, JMJD2A, KIAA0677 / Plasmid: pNIC28 / Production host: Homo sapiens (human) / Gene: KDM4A, JHDM3A, JMJD2, JMJD2A, KIAA0677 / Plasmid: pNIC28 / Production host:  References: UniProt: O75164, Oxidoreductases; Acting on paired donors, with incorporation or reduction of molecular oxygen; With 2-oxoglutarate as one donor, and incorporation of one atom of oxygen into each donor |
|---|
-Non-polymers , 6 types, 791 molecules 
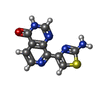









| #2: Chemical | ChemComp-ZN / #3: Chemical | ChemComp-5V7 / #4: Chemical | ChemComp-DMS / #5: Chemical | ChemComp-EDO / #6: Chemical | ChemComp-GOL / #7: Water | ChemComp-HOH / | |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION X-RAY DIFFRACTION |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.45 Å3/Da / Density % sol: 49.84 % |
|---|---|
| Crystal grow | Temperature: 291 K / Method: vapor diffusion, hanging drop / pH: 7.5 Details: Crystallisation solution is 0.1M Bis-Tris-Propane pH7.5, 12-16% PEG-4000. Inhibitor is soaked in crystals by addition directly to the drops of DMSO dissolved compound |
-Data collection
| Diffraction | Mean temperature: 100 K |
|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  Diamond Diamond  / Beamline: I03 / Wavelength: 1.0721 Å / Beamline: I03 / Wavelength: 1.0721 Å |
| Detector | Type: DECTRIS PILATUS3 6M / Detector: PIXEL / Date: Aug 10, 2014 |
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray |
| Radiation wavelength | Wavelength: 1.0721 Å / Relative weight: 1 |
| Reflection | Resolution: 2.05→48.86 Å / Num. obs: 89282 / % possible obs: 88.3 % / Redundancy: 5.9 % / Biso Wilson estimate: 49.61 Å2 / Rmerge(I) obs: 0.079 / Net I/σ(I): 10.3 |
| Reflection shell | Resolution: 2.05→2.1 Å / Redundancy: 1.5 % / Rmerge(I) obs: 0.692 / Mean I/σ(I) obs: 0.5 / % possible all: 43.9 |
- Processing
Processing
| Software |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  MOLECULAR REPLACEMENT MOLECULAR REPLACEMENTStarting model: 2OQ7 Resolution: 2.05→41 Å / Cor.coef. Fo:Fc: 0.9505 / Cor.coef. Fo:Fc free: 0.9396 / SU R Cruickshank DPI: 0.193 / Cross valid method: THROUGHOUT / σ(F): 0 / SU R Blow DPI: 0.195 / SU Rfree Blow DPI: 0.158 / SU Rfree Cruickshank DPI: 0.159
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso mean: 57.78 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine analyze | Luzzati coordinate error obs: 0.243 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: 1 / Resolution: 2.05→41 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Resolution: 2.05→2.1 Å / Total num. of bins used: 20
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller























 PDBj
PDBj








