[English] 日本語
 Yorodumi
Yorodumi- PDB-4m4k: Crystal structure of the Drosphila beta,14galactosyltransferase 7... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 4m4k | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| Title | Crystal structure of the Drosphila beta,14galactosyltransferase 7 mutant D211N complex with manganese, UDP-Gal and xylobiose | |||||||||
 Components Components | Beta-4-galactosyltransferase 7 | |||||||||
 Keywords Keywords | TRANSFERASE / GT-A glycosyltransferase family / UDP-Gal and Xylose / Golgi | |||||||||
| Function / homology |  Function and homology information Function and homology informationxylosylprotein 4-beta-galactosyltransferase / xylosylprotein 4-beta-galactosyltransferase activity / glycosaminoglycan-protein linkage region biosynthetic process / Glycosaminoglycan-protein linkage region biosynthesis / proteoglycan biosynthetic process / chondroitin sulfate proteoglycan biosynthetic process / heparan sulfate proteoglycan biosynthetic process / N-glycan processing / carbohydrate metabolic process / Golgi membrane ...xylosylprotein 4-beta-galactosyltransferase / xylosylprotein 4-beta-galactosyltransferase activity / glycosaminoglycan-protein linkage region biosynthetic process / Glycosaminoglycan-protein linkage region biosynthesis / proteoglycan biosynthetic process / chondroitin sulfate proteoglycan biosynthetic process / heparan sulfate proteoglycan biosynthetic process / N-glycan processing / carbohydrate metabolic process / Golgi membrane / nucleotide binding / Golgi apparatus / metal ion binding Similarity search - Function | |||||||||
| Biological species |  | |||||||||
| Method |  X-RAY DIFFRACTION / Molecular Placement / Resolution: 2.2 Å X-RAY DIFFRACTION / Molecular Placement / Resolution: 2.2 Å | |||||||||
 Authors Authors | Ramakrishnan, B. / Qasba, P.K. | |||||||||
 Citation Citation |  Journal: J.Biol.Chem. / Year: 2013 Journal: J.Biol.Chem. / Year: 2013Title: Crystal Structures of beta-1,4-Galactosyltransferase 7 Enzyme Reveal Conformational Changes and Substrate Binding. Authors: Tsutsui, Y. / Ramakrishnan, B. / Qasba, P.K. | |||||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  4m4k.cif.gz 4m4k.cif.gz | 71.5 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb4m4k.ent.gz pdb4m4k.ent.gz | 49.9 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  4m4k.json.gz 4m4k.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/m4/4m4k https://data.pdbj.org/pub/pdb/validation_reports/m4/4m4k ftp://data.pdbj.org/pub/pdb/validation_reports/m4/4m4k ftp://data.pdbj.org/pub/pdb/validation_reports/m4/4m4k | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  4irpC  4irqC  4lw3C  4lw6SC C: citing same article ( S: Starting model for refinement |
|---|---|
| Similar structure data |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| Unit cell |
|
- Components
Components
-Protein / Sugars , 2 types, 2 molecules A
| #1: Protein | Mass: 33319.305 Da / Num. of mol.: 1 / Fragment: catalytic domain, UNP residues 71-311 / Mutation: D211N Source method: isolated from a genetically manipulated source Details: expressed as inclusion bodies and in vitro refolded Source: (gene. exp.)  Gene: 4galactosyltransferase 7, beta-4GalT7, beta1, beta4GalT7, beta4GalT7-RA, CG11780, Dmel_CG11780 Plasmid: pET23a / Production host:  References: UniProt: Q9VBZ9, Transferases; Glycosyltransferases; Hexosyltransferases, xylosylprotein 4-beta-galactosyltransferase |
|---|---|
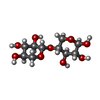
| #2: Polysaccharide | beta-D-xylopyranose-(1-4)-beta-D-xylopyranose / 4beta-beta-xylobiose |
-Non-polymers , 4 types, 177 molecules 





| #3: Chemical | ChemComp-MN / | ||
|---|---|---|---|
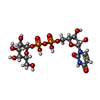
| #4: Chemical | ChemComp-GDU / | ||
| #5: Chemical | | #6: Water | ChemComp-HOH / | |
-Details
| Has protein modification | Y |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 3.37 Å3/Da / Density % sol: 63.52 % |
|---|---|
| Crystal grow | Temperature: 280 K / Method: vapor diffusion, hanging drop / pH: 8 Details: 100 mM HEPES, 5% PEG 6000, 10% MPD, 1M NaCl, 10 mM MnCl2, 10 mM UDP-Gal and 10 mM xylobiose, pH 8.0, VAPOR DIFFUSION, HANGING DROP, temperature 280K |
-Data collection
| Diffraction | Mean temperature: 100 K |
|---|---|
| Diffraction source | Source:  ROTATING ANODE / Type: RIGAKU MICROMAX-007 HF / Wavelength: 1.5418 Å ROTATING ANODE / Type: RIGAKU MICROMAX-007 HF / Wavelength: 1.5418 Å |
| Detector | Type: MAR scanner 345 mm plate / Detector: IMAGE PLATE / Date: Jul 28, 2013 / Details: mirrors |
| Radiation | Monochromator: Graphite / Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray |
| Radiation wavelength | Wavelength: 1.5418 Å / Relative weight: 1 |
| Reflection | Resolution: 2.2→50 Å / Num. all: 24123 / Num. obs: 23650 / % possible obs: 99.9 % / Observed criterion σ(I): 1 / Redundancy: 9.6 % / Rsym value: 0.077 / Net I/σ(I): 24.7 |
| Reflection shell | Resolution: 2.2→2.28 Å / Redundancy: 7.4 % / Mean I/σ(I) obs: 2.2 / Num. unique all: 2345 / Rsym value: 0.66 / % possible all: 99.7 |
- Processing
Processing
| Software |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure: Molecular Placement Starting model: PDB entry 4LW6 Resolution: 2.2→36.976 Å / SU ML: 0.18 / Cross valid method: THROUGHOUT / σ(F): 1.33 / Phase error: 24.32 / Stereochemistry target values: ML
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.9 Å / VDW probe radii: 1.11 Å / Solvent model: FLAT BULK SOLVENT MODEL | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 2.2→36.976 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell |
|
 Movie
Movie Controller
Controller












 PDBj
PDBj