[English] 日本語
 Yorodumi
Yorodumi- PDB-4hbo: Crystal Structure of Rubella virus capsid protein (residues 127-277) -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 4hbo | ||||||
|---|---|---|---|---|---|---|---|
| Title | Crystal Structure of Rubella virus capsid protein (residues 127-277) | ||||||
 Components Components | Capsid protein | ||||||
 Keywords Keywords | VIRAL PROTEIN / partial beta barrel / capsid protein | ||||||
| Function / homology |  Function and homology information Function and homology informationT=4 icosahedral viral capsid / host cell Golgi membrane / host cell mitochondrion / viral nucleocapsid / clathrin-dependent endocytosis of virus by host cell / fusion of virus membrane with host endosome membrane / viral envelope / virion attachment to host cell / virion membrane / RNA binding ...T=4 icosahedral viral capsid / host cell Golgi membrane / host cell mitochondrion / viral nucleocapsid / clathrin-dependent endocytosis of virus by host cell / fusion of virus membrane with host endosome membrane / viral envelope / virion attachment to host cell / virion membrane / RNA binding / membrane / metal ion binding Similarity search - Function | ||||||
| Biological species |  Rubella virus Rubella virus | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / MOLECULAR REPLACEMENT /  molecular replacement / Resolution: 3.241 Å molecular replacement / Resolution: 3.241 Å | ||||||
 Authors Authors | Mangala Prasad, V. / Fokine, A. / Rossmann, M.G. | ||||||
 Citation Citation |  Journal: Proc.Natl.Acad.Sci.USA / Year: 2013 Journal: Proc.Natl.Acad.Sci.USA / Year: 2013Title: Rubella virus capsid protein structure and its role in virus assembly and infection. Authors: Mangala Prasad, V. / Willows, S.D. / Fokine, A. / Battisti, A.J. / Sun, S. / Plevka, P. / Hobman, T.C. / Rossmann, M.G. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  4hbo.cif.gz 4hbo.cif.gz | 178.2 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb4hbo.ent.gz pdb4hbo.ent.gz | 142 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  4hbo.json.gz 4hbo.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/hb/4hbo https://data.pdbj.org/pub/pdb/validation_reports/hb/4hbo ftp://data.pdbj.org/pub/pdb/validation_reports/hb/4hbo ftp://data.pdbj.org/pub/pdb/validation_reports/hb/4hbo | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  4harSC  4hbeC S: Starting model for refinement C: citing same article ( |
|---|---|
| Similar structure data |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 | 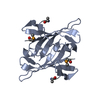
| ||||||||
| 2 | 
| ||||||||
| 3 | 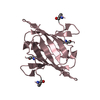
| ||||||||
| 4 | 
| ||||||||
| 5 | 
| ||||||||
| Unit cell |
| ||||||||
| Details | The biological unit is a dimer. There are 5 monomers in the asymmetric unit (chain A, B, C, D and E), which form 5 biological units on application of a 2-fold along 'b' axis. |
- Components
Components
| #1: Protein | Mass: 14987.403 Da / Num. of mol.: 5 / Fragment: C-terminal domain Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Rubella virus / Strain: M33 / Gene: Capsid / Plasmid: pGEX-KG / Production host: Rubella virus / Strain: M33 / Gene: Capsid / Plasmid: pGEX-KG / Production host:  Has protein modification | Y | Sequence details | N-TERMINAL 20 AMINO ACIDS ASN PRO PHE GLN ALA ALA VAL ALA ARG GLY LEU ARG PRO PRO LEU HIS ASP PRO ...N-TERMINAL 20 AMINO ACIDS ASN PRO PHE GLN ALA ALA VAL ALA ARG GLY LEU ARG PRO PRO LEU HIS ASP PRO ASP THR WERE INCLUDED IN CRYSTALLIZ | |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 1.53 Å3/Da / Density % sol: 19.7 % |
|---|---|
| Crystal grow | Temperature: 293 K / Method: vapor diffusion, hanging drop / pH: 7.5 Details: 18% PEG 4000, 20% 2-propanol, 0.1 M Tris, pH 7.5, VAPOR DIFFUSION, HANGING DROP, temperature 293K |
-Data collection
| Diffraction | Mean temperature: 298 K | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  APS APS  / Beamline: 23-ID-D / Wavelength: 0.979 Å / Beamline: 23-ID-D / Wavelength: 0.979 Å | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Detector | Type: MARMOSAIC 300 mm CCD / Detector: CCD / Date: Oct 20, 2011 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation | Monochromator: Si 111 / Protocol: SINGLE WAVELENGTH / Scattering type: x-ray | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation wavelength | Wavelength: 0.979 Å / Relative weight: 1 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection | Resolution: 3.241→50 Å / Num. obs: 7669 / % possible obs: 99 % / Observed criterion σ(F): 0 / Observed criterion σ(I): 0 / Redundancy: 12.7 % / Rmerge(I) obs: 0.107 / Χ2: 1.351 / Net I/σ(I): 7.7 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection shell |
|
-Phasing
| Phasing | Method:  molecular replacement molecular replacement | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| Phasing MR | Model details: Phaser MODE: MR_AUTO
|
- Processing
Processing
| Software |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  MOLECULAR REPLACEMENT MOLECULAR REPLACEMENTStarting model: PDB entry 4HAR Resolution: 3.241→46.617 Å / Occupancy max: 1 / Occupancy min: 1 / FOM work R set: 0.5829 / SU ML: 0.44 / σ(F): 1.4 / Phase error: 44.33 / Stereochemistry target values: ML
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.8 Å / VDW probe radii: 1 Å / Solvent model: FLAT BULK SOLVENT MODEL | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso max: 338.52 Å2 / Biso mean: 96.507 Å2 / Biso min: 20 Å2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 3.241→46.617 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Refine-ID: X-RAY DIFFRACTION / Total num. of bins used: 10
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller












 PDBj
PDBj
