[English] 日本語
 Yorodumi
Yorodumi- PDB-3ti5: Crystal structure of 2009 pandemic H1N1 neuraminidase complexed w... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 3ti5 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| Title | Crystal structure of 2009 pandemic H1N1 neuraminidase complexed with Zanamivir | |||||||||
 Components Components | Neuraminidase | |||||||||
 Keywords Keywords | HYDROLASE/HYDROLASE INHIBITOR / 6-BLADED BETA-PROPELLER / Calcium Binding / Glycosylation / antiviral / HYDROLASE-HYDROLASE INHIBITOR complex | |||||||||
| Function / homology |  Function and homology information Function and homology informationexo-alpha-sialidase / exo-alpha-sialidase activity / viral budding from plasma membrane / carbohydrate metabolic process / host cell plasma membrane / virion membrane / membrane / metal ion binding / identical protein binding Similarity search - Function | |||||||||
| Biological species |   Influenza A virus Influenza A virus | |||||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / Resolution: 1.9 Å MOLECULAR REPLACEMENT / Resolution: 1.9 Å | |||||||||
 Authors Authors | Vavricka, C.J. / Li, Q. / Wu, Y. / Qi, J. / Wang, M. / Liu, Y. / Gao, F. / Liu, J. / Feng, E. / He, J. ...Vavricka, C.J. / Li, Q. / Wu, Y. / Qi, J. / Wang, M. / Liu, Y. / Gao, F. / Liu, J. / Feng, E. / He, J. / Wang, J. / Liu, H. / Jiang, H. / Gao, G.F. | |||||||||
 Citation Citation |  Journal: Plos Pathog. / Year: 2011 Journal: Plos Pathog. / Year: 2011Title: Structural and functional analysis of laninamivir and its octanoate prodrug reveals group specific mechanisms for influenza NA inhibition Authors: Vavricka, C.J. / Li, Q. / Wu, Y. / Qi, J. / Wang, M. / Liu, Y. / Gao, F. / Liu, J. / Feng, E. / He, J. / Wang, J. / Liu, H. / Jiang, H. / Gao, G.F. | |||||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  3ti5.cif.gz 3ti5.cif.gz | 338.4 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb3ti5.ent.gz pdb3ti5.ent.gz | 272.2 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  3ti5.json.gz 3ti5.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/ti/3ti5 https://data.pdbj.org/pub/pdb/validation_reports/ti/3ti5 ftp://data.pdbj.org/pub/pdb/validation_reports/ti/3ti5 ftp://data.pdbj.org/pub/pdb/validation_reports/ti/3ti5 | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  3ti3C  3ti4C  3ti6C  3ti8C  3tiaC  3tibC  3ticC  3nssS S: Starting model for refinement C: citing same article ( |
|---|---|
| Similar structure data |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||||||
| Unit cell |
| ||||||||||||
| Components on special symmetry positions |
|
- Components
Components
-Protein , 1 types, 2 molecules AB
| #1: Protein | Mass: 42727.629 Da / Num. of mol.: 2 / Fragment: UNP residues 82-469 Source method: isolated from a genetically manipulated source Source: (gene. exp.)   Influenza A virus / Strain: A/California/04/2009(H1N1) / Gene: NA / Plasmid: pAcGP67-B / Cell line (production host): SF9 / Production host: Influenza A virus / Strain: A/California/04/2009(H1N1) / Gene: NA / Plasmid: pAcGP67-B / Cell line (production host): SF9 / Production host:  |
|---|
-Sugars , 3 types, 6 molecules 
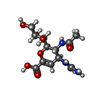

| #2: Polysaccharide | beta-D-mannopyranose-(1-4)-2-acetamido-2-deoxy-beta-D-glucopyranose-(1-4)-2-acetamido-2-deoxy-beta- ...beta-D-mannopyranose-(1-4)-2-acetamido-2-deoxy-beta-D-glucopyranose-(1-4)-2-acetamido-2-deoxy-beta-D-glucopyranose Source method: isolated from a genetically manipulated source | ||
|---|---|---|---|
| #3: Sugar | | #5: Sugar | |
-Non-polymers , 4 types, 775 molecules 






| #4: Chemical | ChemComp-CA / #6: Chemical | #7: Chemical | ChemComp-ACT / #8: Water | ChemComp-HOH / | |
|---|
-Details
| Has protein modification | Y |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.81 Å3/Da / Density % sol: 56.25 % |
|---|---|
| Crystal grow | Temperature: 291 K / Method: vapor diffusion, hanging drop / pH: 6.5 Details: 0.16M calcium acetate hydrate, 0.08M sodium cacodylate trihydrate, 14.4% polyethylene glycol 8000, 20% glycerol , pH 6.5, VAPOR DIFFUSION, HANGING DROP, temperature 291K |
-Data collection
| Diffraction | Mean temperature: 100 K |
|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  SSRF SSRF  / Beamline: BL17U / Wavelength: 0.9795 Å / Beamline: BL17U / Wavelength: 0.9795 Å |
| Detector | Type: MARMOSAIC 225 mm CCD / Detector: CCD / Date: Mar 31, 2010 |
| Radiation | Monochromator: GRAPHITE / Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray |
| Radiation wavelength | Wavelength: 0.9795 Å / Relative weight: 1 |
| Reflection | Resolution: 1.9→50 Å / Num. all: 75374 / Num. obs: 75374 / % possible obs: 99.4 % / Observed criterion σ(F): 2 / Observed criterion σ(I): 2 / Biso Wilson estimate: 11.46 Å2 |
| Reflection shell | Resolution: 1.9→1.97 Å / % possible all: 99.6 |
- Processing
Processing
| Software |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  MOLECULAR REPLACEMENT MOLECULAR REPLACEMENTStarting model: PDB ENTRY 3NSS Resolution: 1.9→36.134 Å / Occupancy max: 1 / Occupancy min: 1 / FOM work R set: 0.9059 / SU ML: 0.2 / σ(F): 0.07 / Phase error: 16.57 / Stereochemistry target values: ML
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.9 Å / VDW probe radii: 1.11 Å / Solvent model: FLAT BULK SOLVENT MODEL / Bsol: 43.154 Å2 / ksol: 0.369 e/Å3 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso max: 83.29 Å2 / Biso mean: 14.1086 Å2 / Biso min: 2.76 Å2
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 1.9→36.134 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Refine-ID: X-RAY DIFFRACTION / Total num. of bins used: 26
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Origin x: 45.6704 Å / Origin y: 22.9678 Å / Origin z: -14.9943 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group | Selection details: all |
 Movie
Movie Controller
Controller






















 PDBj
PDBj






