| 登録情報 | データベース: PDB / ID: 3qqn
|
|---|
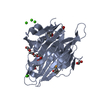
| タイトル | The retinal specific CD147 Ig0 domain: from molecular structure to biological activity |
|---|
 要素 要素 | Basigin |
|---|
 キーワード キーワード | CELL ADHESION / CD147 / EMMPRIN / Immunoglobulin-like domain / beta sheet / Structural Genomics / Berkeley Structural Genomics Center / BSGC |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
Defective SLC16A1 causes symptomatic deficiency in lactate transport (SDLT) / Proton-coupled monocarboxylate transport / positive regulation of matrix metallopeptidase secretion / acrosomal membrane / dendrite self-avoidance / endothelial tube morphogenesis / response to mercury ion / cell-cell adhesion mediator activity / neural retina development / photoreceptor cell maintenance ...Defective SLC16A1 causes symptomatic deficiency in lactate transport (SDLT) / Proton-coupled monocarboxylate transport / positive regulation of matrix metallopeptidase secretion / acrosomal membrane / dendrite self-avoidance / endothelial tube morphogenesis / response to mercury ion / cell-cell adhesion mediator activity / neural retina development / photoreceptor cell maintenance / neuron projection extension / Basigin interactions / Aspirin ADME / odontogenesis of dentin-containing tooth / D-mannose binding / homophilic cell-cell adhesion / decidualization / positive regulation of vascular endothelial growth factor production / photoreceptor outer segment / Integrin cell surface interactions / response to cAMP / Degradation of the extracellular matrix / neutrophil chemotaxis / photoreceptor inner segment / embryo implantation / positive regulation of endothelial cell migration / axon guidance / protein localization to plasma membrane / sarcolemma / positive regulation of interleukin-6 production / response to peptide hormone / melanosome / virus receptor activity / signaling receptor activity / angiogenesis / basolateral plasma membrane / positive regulation of viral entry into host cell / cell surface receptor signaling pathway / endosome / cadherin binding / Golgi membrane / axon / focal adhesion / endoplasmic reticulum membrane / mitochondrion / extracellular exosome / membrane / plasma membrane類似検索 - 分子機能 Immunoglobulin domain / Immunoglobulin subtype 2 / Immunoglobulin C-2 Type / Immunoglobulin subtype / Immunoglobulin / Ig-like domain profile. / Immunoglobulin-like domain / Immunoglobulin-like domain superfamily / Immunoglobulin-like fold / Immunoglobulins ...Immunoglobulin domain / Immunoglobulin subtype 2 / Immunoglobulin C-2 Type / Immunoglobulin subtype / Immunoglobulin / Ig-like domain profile. / Immunoglobulin-like domain / Immunoglobulin-like domain superfamily / Immunoglobulin-like fold / Immunoglobulins / Immunoglobulin-like / Sandwich / Mainly Beta類似検索 - ドメイン・相同性 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / 解像度: 2.309 Å シンクロトロン / 解像度: 2.309 Å |
|---|
 データ登録者 データ登録者 | Redzic, J.S. / Armstrong, G.S. / Isern, N.G. / Kieft, J.S. / Eisenmesser, E.Z. / Berkeley Structural Genomics Center (BSGC) |
|---|
 引用 引用 |  ジャーナル: J.Mol.Biol. / 年: 2011 ジャーナル: J.Mol.Biol. / 年: 2011
タイトル: The Retinal Specific CD147 Ig0 Domain: From Molecular Structure to Biological Activity.
著者: Redzic, J.S. / Armstrong, G.S. / Isern, N.G. / Jones, D.N. / Kieft, J.S. / Eisenmesser, E.Z. |
|---|
| 履歴 | | 登録 | 2011年2月15日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2011年5月11日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2011年7月13日 | Group: Version format compliance |
|---|
| 改定 1.2 | 2011年8月17日 | Group: Database references |
|---|
| 改定 1.3 | 2024年11月20日 | Group: Data collection / Database references ...Data collection / Database references / Derived calculations / Structure summary
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_entry_details / pdbx_modification_feature / struct_conn / struct_ref_seq_dif
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_entry_details.has_protein_modification / _struct_conn.pdbx_leaving_atom_flag / _struct_ref_seq_dif.details |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  シンクロトロン / 解像度: 2.309 Å
シンクロトロン / 解像度: 2.309 Å  データ登録者
データ登録者 引用
引用 ジャーナル: J.Mol.Biol. / 年: 2011
ジャーナル: J.Mol.Biol. / 年: 2011 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 3qqn.cif.gz
3qqn.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb3qqn.ent.gz
pdb3qqn.ent.gz PDB形式
PDB形式 3qqn.json.gz
3qqn.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/qq/3qqn
https://data.pdbj.org/pub/pdb/validation_reports/qq/3qqn ftp://data.pdbj.org/pub/pdb/validation_reports/qq/3qqn
ftp://data.pdbj.org/pub/pdb/validation_reports/qq/3qqn リンク
リンク 集合体
集合体
 要素
要素 Homo sapiens (ヒト) / 遺伝子: BSG, UNQ6505/PRO21383 / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: BSG, UNQ6505/PRO21383 / 発現宿主: 
 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  ALS
ALS  / ビームライン: 4.2.2 / 波長: 1.02159,1.02195,1.03726
/ ビームライン: 4.2.2 / 波長: 1.02159,1.02195,1.03726 解析
解析 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj










