+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 3jv6 | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Crystal structure of the dimerization domains p52 and RelB | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | TRANSCRIPTION / NF-kB protein / Heterodimer / RelB and p52 / Activator / Nucleus / Phosphoprotein / Transcription regulation / ANK repeat / DNA-binding / Isopeptide bond | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報follicular dendritic cell differentiation / Bcl3/NF-kappaB2 complex / SUMOylation of immune response proteins / Interleukin-1 processing / DEx/H-box helicases activate type I IFN and inflammatory cytokines production / RIP-mediated NFkB activation via ZBP1 / TRAF6 mediated NF-kB activation / T-helper 1 cell differentiation / Dectin-1 mediated noncanonical NF-kB signaling / NIK-->noncanonical NF-kB signaling ...follicular dendritic cell differentiation / Bcl3/NF-kappaB2 complex / SUMOylation of immune response proteins / Interleukin-1 processing / DEx/H-box helicases activate type I IFN and inflammatory cytokines production / RIP-mediated NFkB activation via ZBP1 / TRAF6 mediated NF-kB activation / T-helper 1 cell differentiation / Dectin-1 mediated noncanonical NF-kB signaling / NIK-->noncanonical NF-kB signaling / PKMTs methylate histone lysines / TAK1-dependent IKK and NF-kappa-B activation / CD209 (DC-SIGN) signaling / myeloid dendritic cell differentiation / negative regulation of interferon-beta production / germinal center formation / cellular response to osmotic stress / non-canonical NF-kappaB signal transduction / T-helper 1 type immune response / antigen processing and presentation / canonical NF-kappaB signal transduction / lymph node development / spleen development / response to cytokine / transcription repressor complex / extracellular matrix organization / circadian regulation of gene expression / rhythmic process / DNA-binding transcription activator activity, RNA polymerase II-specific / response to lipopolysaccharide / RNA polymerase II cis-regulatory region sequence-specific DNA binding / DNA-binding transcription factor activity / negative regulation of DNA-templated transcription / synapse / centrosome / protein kinase binding / chromatin / DNA binding / nucleoplasm / identical protein binding / nucleus / cytosol 類似検索 - 分子機能 | ||||||
| 生物種 |  | ||||||
| 手法 |  X線回折 / X線回折 /  分子置換 / 解像度: 2.78 Å 分子置換 / 解像度: 2.78 Å | ||||||
 データ登録者 データ登録者 | Vu, D. / Huang, D.B. / Ghosh, G. | ||||||
 引用 引用 |  ジャーナル: J.Mol.Biol. / 年: 2013 ジャーナル: J.Mol.Biol. / 年: 2013タイトル: A structural basis for selective dimerization by NF-kappa B RelB. 著者: Vu, D. / Huang, D.B. / Vemu, A. / Ghosh, G. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  3jv6.cif.gz 3jv6.cif.gz | 137.7 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb3jv6.ent.gz pdb3jv6.ent.gz | 110.4 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  3jv6.json.gz 3jv6.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  3jv6_validation.pdf.gz 3jv6_validation.pdf.gz | 482.4 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  3jv6_full_validation.pdf.gz 3jv6_full_validation.pdf.gz | 503.9 KB | 表示 | |
| XML形式データ |  3jv6_validation.xml.gz 3jv6_validation.xml.gz | 28 KB | 表示 | |
| CIF形式データ |  3jv6_validation.cif.gz 3jv6_validation.cif.gz | 37.5 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/jv/3jv6 https://data.pdbj.org/pub/pdb/validation_reports/jv/3jv6 ftp://data.pdbj.org/pub/pdb/validation_reports/jv/3jv6 ftp://data.pdbj.org/pub/pdb/validation_reports/jv/3jv6 | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 | 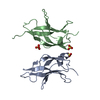
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 2 | 
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 3 | 
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 単位格子 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 非結晶学的対称性 (NCS) | NCSドメイン:
NCSドメイン領域:
NCSアンサンブル:
|
- 要素
要素
| #1: タンパク質 | 分子量: 11405.868 Da / 分子数: 3 / 断片: dimerization domain (UNP residues 278-378) / 由来タイプ: 組換発現 / 由来: (組換発現)   #2: タンパク質 | 分子量: 12430.976 Da / 分子数: 3 / 断片: dimerization domain (UNP residues 225-331) / 由来タイプ: 組換発現 / 由来: (組換発現)   #3: 化合物 | ChemComp-SO4 / #4: 水 | ChemComp-HOH / | |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 5.27 Å3/Da / 溶媒含有率: 76.65 % |
|---|---|
| 結晶化 | 温度: 291 K / 手法: 蒸気拡散法, ハンギングドロップ法 詳細: PEG 8000, ammonium sulfate, VAPOR DIFFUSION, HANGING DROP, temperature 291K |
-データ収集
| 回折 | 平均測定温度: 105 K |
|---|---|
| 放射光源 | 由来:  回転陽極 / タイプ: RIGAKU RU200 / 波長: 1.5418 Å 回転陽極 / タイプ: RIGAKU RU200 / 波長: 1.5418 Å |
| 検出器 | タイプ: MAR scanner 345 mm plate / 検出器: IMAGE PLATE / 日付: 2006年10月15日 / 詳細: mirrors |
| 放射 | モノクロメーター: osmic mirror / プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 1.5418 Å / 相対比: 1 |
| 反射 | 解像度: 2.8→30 Å / Num. all: 33723 / Num. obs: 30666 / % possible obs: 80 % / Observed criterion σ(I): 1 / 冗長度: 4 % / Biso Wilson estimate: 48.8 Å2 / Rsym value: 0.105 / Net I/σ(I): 8.1 |
| 反射 シェル | 解像度: 2.78→2.88 Å / 冗長度: 3 % / Mean I/σ(I) obs: 2.5 / Num. unique all: 2436 / Rsym value: 0.554 / % possible all: 64 |
-位相決定
| 位相決定 | 手法:  分子置換 分子置換 |
|---|
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 / 解像度: 2.78→29.63 Å / Rfactor Rfree error: 0.007 / Occupancy max: 1 / Occupancy min: 0.51 / FOM work R set: 0.702 / Data cutoff high absF: 136706 / Data cutoff low absF: 0 / Isotropic thermal model: GROUP / 交差検証法: THROUGHOUT / σ(F): 2 / 立体化学のターゲット値: Engh & Huber 分子置換 / 解像度: 2.78→29.63 Å / Rfactor Rfree error: 0.007 / Occupancy max: 1 / Occupancy min: 0.51 / FOM work R set: 0.702 / Data cutoff high absF: 136706 / Data cutoff low absF: 0 / Isotropic thermal model: GROUP / 交差検証法: THROUGHOUT / σ(F): 2 / 立体化学のターゲット値: Engh & Huber
| ||||||||||||||||||||||||||||
| 溶媒の処理 | 溶媒モデル: FLAT MODEL / Bsol: 44.256 Å2 / ksol: 0.299 e/Å3 | ||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso max: 140 Å2 / Biso mean: 74.11 Å2 / Biso min: 18.7 Å2
| ||||||||||||||||||||||||||||
| Refine analyze |
| ||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 2.78→29.63 Å
| ||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||
| Refine LS restraints NCS |
| ||||||||||||||||||||||||||||
| LS精密化 シェル | 解像度: 2.78→2.91 Å / Rfactor Rfree error: 0.054 / Total num. of bins used: 8
| ||||||||||||||||||||||||||||
| Xplor file |
|
 ムービー
ムービー コントローラー
コントローラー
















 PDBj
PDBj














