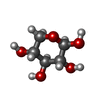
登録構造単位
B: Sugar ABC transporter, periplasmic sugar-binding protein
A: Sugar ABC transporter, periplasmic sugar-binding protein
C: Sugar ABC transporter, periplasmic sugar-binding protein
D: Sugar ABC transporter, periplasmic sugar-binding protein
ヘテロ分子 概要 構成要素の詳細
分子量 (理論値) 分子数 合計 (水以外) 135,128 6 ポリマ- 134,828 4 非ポリマー 300 2 水 6,215 345
1
B: Sugar ABC transporter, periplasmic sugar-binding protein 概要 構成要素の詳細 対称操作
分子量 (理論値) 分子数 合計 (水以外) 33,707 1 ポリマ- 33,707 1 非ポリマー 0 0 水 18 1
タイプ 名称 対称操作 数 identity operation 1_555 x,y,z 1
2
A: Sugar ABC transporter, periplasmic sugar-binding protein 概要 構成要素の詳細 対称操作
分子量 (理論値) 分子数 合計 (水以外) 33,707 1 ポリマ- 33,707 1 非ポリマー 0 0 水 18 1
タイプ 名称 対称操作 数 identity operation 1_555 x,y,z 1
3
C: Sugar ABC transporter, periplasmic sugar-binding protein
ヘテロ分子 概要 構成要素の詳細 対称操作
分子量 (理論値) 分子数 合計 (水以外) 33,857 2 ポリマ- 33,707 1 非ポリマー 150 1 水 18 1
タイプ 名称 対称操作 数 identity operation 1_555 x,y,z 1
4
D: Sugar ABC transporter, periplasmic sugar-binding protein
ヘテロ分子 概要 構成要素の詳細 対称操作
分子量 (理論値) 分子数 合計 (水以外) 33,857 2 ポリマ- 33,707 1 非ポリマー 150 1 水 18 1
タイプ 名称 対称操作 数 identity operation 1_555 x,y,z 1
単位格子 Length a, b, c (Å) 81.100, 75.750, 100.520 Angle α, β, γ (deg.) 90.000, 89.900, 90.000 Int Tables number 4 Space group name H-M P121 1
非結晶学的対称性 (NCS) NCS oper ID Code Matrix ベクター 1 given(1), (1), (1)2 given(0.999999, 0.000372, -0.001637), (0.000372, -1, 0.000139), (-0.001637, -0.00014, -0.999999)40.567001, 0.431856, 50.2158013 given(0.999994, 0.001311, -0.003345), (0.001314, -0.999999, 0.000745), (-0.003344, -0.000749, -0.999994)40.692101, -75.280701, 50.115398
詳細 The biolgical assembly is a monomeric protein consisting of a single polypeptide chain. In this structure there are two forms, one of which has xylose bound, the other does not.
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 Thermotoga maritima (バクテリア)
Thermotoga maritima (バクテリア) X線回折 / 解像度: 2.3 Å
X線回折 / 解像度: 2.3 Å  データ登録者
データ登録者 引用
引用 ジャーナル: To be Published
ジャーナル: To be Published 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 3c6q.cif.gz
3c6q.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb3c6q.ent.gz
pdb3c6q.ent.gz PDB形式
PDB形式 3c6q.json.gz
3c6q.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 3c6q_validation.pdf.gz
3c6q_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 3c6q_full_validation.pdf.gz
3c6q_full_validation.pdf.gz 3c6q_validation.xml.gz
3c6q_validation.xml.gz 3c6q_validation.cif.gz
3c6q_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/c6/3c6q
https://data.pdbj.org/pub/pdb/validation_reports/c6/3c6q ftp://data.pdbj.org/pub/pdb/validation_reports/c6/3c6q
ftp://data.pdbj.org/pub/pdb/validation_reports/c6/3c6q
 リンク
リンク 集合体
集合体




 要素
要素
 Thermotoga maritima (バクテリア)
Thermotoga maritima (バクテリア)
 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 回転陽極 / タイプ: RIGAKU / 波長: 1.5418 Å
回転陽極 / タイプ: RIGAKU / 波長: 1.5418 Å 解析
解析 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj