[English] 日本語
 Yorodumi
Yorodumi- PDB-3bmw: Cyclodextrin glycosyl transferase from Thermoanerobacterium therm... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 3bmw | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Title | Cyclodextrin glycosyl transferase from Thermoanerobacterium thermosulfurigenes EM1 mutant S77P complexed with a maltoheptaose inhibitor | ||||||||||||
 Components Components | Cyclomaltodextrin glucanotransferase | ||||||||||||
 Keywords Keywords | TRANSFERASE / glycosidase / thermostable / family 13 glycosyl hydrolas / ligand / substrate / acarbose / Glycosyltransferase / Metal-binding / Secreted | ||||||||||||
| Function / homology |  Function and homology information Function and homology informationcyclomaltodextrin glucanotransferase / cyclomaltodextrin glucanotransferase activity / starch binding / alpha-amylase activity / carbohydrate metabolic process / extracellular region / metal ion binding Similarity search - Function | ||||||||||||
| Biological species |  Thermoanaerobacterium thermosulfurigenes (bacteria) Thermoanaerobacterium thermosulfurigenes (bacteria) | ||||||||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  FOURIER SYNTHESIS / Resolution: 1.6 Å FOURIER SYNTHESIS / Resolution: 1.6 Å | ||||||||||||
 Authors Authors | Rozeboom, H.J. / van Oosterwijk, N. / Dijkstra, B.W. | ||||||||||||
 Citation Citation |  Journal: Biochem.J. / Year: 2008 Journal: Biochem.J. / Year: 2008Title: Elimination of competing hydrolysis and coupling side reactions of a cyclodextrin glucanotransferase by directed evolution. Authors: Kelly, R.M. / Leemhuis, H. / Rozeboom, H.J. / van Oosterwijk, N. / Dijkstra, B.W. / Dijkhuizen, L. #1:  Journal: J.Biol.Chem. / Year: 1998 Journal: J.Biol.Chem. / Year: 1998Title: Engineering of cyclodextrin product specificity and pH optima of the thermostable cyclodextrin glycosyltransferase from Thermoanaerobacterium thermosulfurigenes EM1 Authors: Wind, R.D. / Uitdehaag, J.C.M. / Buitelaar, R.M. / Dijkstra, B.W. / Dijkhuizen, L. #2:  Journal: J.Mol.Biol. / Year: 1996 Journal: J.Mol.Biol. / Year: 1996Title: Crystal structure at 2.3 A resolution and revised nucleotide sequence of the thermostable cyclodextrin glycosyltransferase from Thermonanaerobacterium thermosulfurigenes EM1 Authors: Knegtel, R.M.A. / Wind, R.D. / Rozeboom, H.J. / Kalk, K.H. / Buitelaar, R.M. / Dijkhuizen, L. / Dijkstra, B.W. | ||||||||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  3bmw.cif.gz 3bmw.cif.gz | 180.4 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb3bmw.ent.gz pdb3bmw.ent.gz | 137.6 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  3bmw.json.gz 3bmw.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/bm/3bmw https://data.pdbj.org/pub/pdb/validation_reports/bm/3bmw ftp://data.pdbj.org/pub/pdb/validation_reports/bm/3bmw ftp://data.pdbj.org/pub/pdb/validation_reports/bm/3bmw | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  3bmvC  1a47S S: Starting model for refinement C: citing same article ( |
|---|---|
| Similar structure data |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| Unit cell |
|
- Components
Components
-Protein , 1 types, 1 molecules A
| #1: Protein | Mass: 75508.109 Da / Num. of mol.: 1 / Mutation: S77P Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Thermoanaerobacterium thermosulfurigenes (bacteria) Thermoanaerobacterium thermosulfurigenes (bacteria)Strain: EM1 / Gene: amyA / Plasmid: PCSCGT-TT / Production host:  References: UniProt: P26827, cyclomaltodextrin glucanotransferase |
|---|
-Sugars , 3 types, 3 molecules
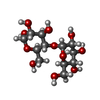
| #2: Polysaccharide | alpha-D-glucopyranose-(1-4)-alpha-D-glucopyranose / alpha-maltose |
|---|---|
| #3: Polysaccharide | alpha-D-quinovopyranose-(1-4)-alpha-D-glucopyranose-(1-4)-alpha-D-glucopyranose Source method: isolated from a genetically manipulated source |
| #4: Polysaccharide | alpha-D-glucopyranose-(1-4)-alpha-D-glucopyranose-(1-4)-alpha-D-glucopyranose / alpha-maltotriose |
-Non-polymers , 6 types, 1168 molecules 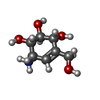










| #5: Chemical | ChemComp-ACI / | ||||||||
|---|---|---|---|---|---|---|---|---|---|
| #6: Chemical | | #7: Chemical | ChemComp-CL / | #8: Chemical | #9: Chemical | ChemComp-GOL / #10: Water | ChemComp-HOH / | |
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.72 Å3/Da / Density % sol: 54.77 % |
|---|---|
| Crystal grow | Temperature: 293 K / Method: vapor diffusion, hanging drop / pH: 7.8 Details: 20% Ammonium sulfate, pH 7.8, VAPOR DIFFUSION, HANGING DROP, temperature 293K |
-Data collection
| Diffraction | Mean temperature: 100 K |
|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  ESRF ESRF  / Beamline: ID14-3 / Wavelength: 0.931 Å / Beamline: ID14-3 / Wavelength: 0.931 Å |
| Detector | Type: ADSC QUANTUM 4 / Detector: CCD / Date: Sep 23, 2007 / Details: Toroidal mirror |
| Radiation | Monochromator: Diamond (111), Ge(220) / Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray |
| Radiation wavelength | Wavelength: 0.931 Å / Relative weight: 1 |
| Reflection | Resolution: 1.6→49.5 Å / Num. all: 102676 / Num. obs: 102676 / % possible obs: 94.2 % / Observed criterion σ(F): 1 / Observed criterion σ(I): 1 / Redundancy: 3.7 % / Biso Wilson estimate: 11.2 Å2 / Rmerge(I) obs: 0.1 / Rsym value: 0.115 / Net I/σ(I): 11.6 |
| Reflection shell | Resolution: 1.6→1.69 Å / Redundancy: 2.5 % / Rmerge(I) obs: 0.19 / Mean I/σ(I) obs: 3.6 / Num. unique all: 11370 / Rsym value: 0.223 / % possible all: 72.7 |
- Processing
Processing
| Software |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  FOURIER SYNTHESIS FOURIER SYNTHESISStarting model: PDB ENTRY 1A47 Resolution: 1.6→49.48 Å / Cor.coef. Fo:Fc: 0.964 / Cor.coef. Fo:Fc free: 0.954 / SU B: 2.142 / SU ML: 0.041 / TLS residual ADP flag: LIKELY RESIDUAL / Isotropic thermal model: isotropic / Cross valid method: THROUGHOUT / ESU R: 0.074 / ESU R Free: 0.072 / Stereochemistry target values: MAXIMUM LIKELIHOOD
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Ion probe radii: 0.8 Å / Shrinkage radii: 0.8 Å / VDW probe radii: 1.4 Å / Solvent model: BABINET MODEL WITH MASK | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso mean: 12.246 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 1.6→49.48 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Resolution: 1.6→1.642 Å / Total num. of bins used: 20
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller













 PDBj
PDBj