| 登録情報 | データベース: PDB / ID: 3adl
|
|---|
| タイトル | Structure of TRBP2 and its molecule implications for miRNA processing |
|---|
 要素 要素 | - RISC-loading complex subunit TARBP2
- RNA (5'-R(P*CP*GP*CP*GP*CP*GP*CP*GP*CP*G)-3')
|
|---|
 キーワード キーワード | GENE REGULATION/RNA / TRBP2 / miRNA processing / GENE REGULATION-RNA complex |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
regulation of siRNA processing / regulation of miRNA processing / negative regulation of cytoplasmic pattern recognition receptor signaling pathway / regulation of viral transcription / regulation of regulatory ncRNA processing / negative regulation of defense response to virus by host / global gene silencing by mRNA cleavage / pre-miRNA binding / Small interfering RNA (siRNA) biogenesis / RISC-loading complex ...regulation of siRNA processing / regulation of miRNA processing / negative regulation of cytoplasmic pattern recognition receptor signaling pathway / regulation of viral transcription / regulation of regulatory ncRNA processing / negative regulation of defense response to virus by host / global gene silencing by mRNA cleavage / pre-miRNA binding / Small interfering RNA (siRNA) biogenesis / RISC-loading complex / RISC complex assembly / miRNA processing / skeletal muscle tissue regeneration / pre-miRNA processing / siRNA processing / siRNA binding / pre-mRNA binding / RISC complex / neural precursor cell proliferation / miRNA binding / MicroRNA (miRNA) biogenesis / positive regulation of muscle cell differentiation / spermatid development / single fertilization / positive regulation of viral genome replication / negative regulation of protein kinase activity / protein sequestering activity / positive regulation of translation / PKR-mediated signaling / multicellular organism growth / double-stranded RNA binding / nuclear body / perinuclear region of cytoplasm / enzyme binding / protein homodimerization activity / nucleoplasm / identical protein binding / nucleus / cytosol / cytoplasm類似検索 - 分子機能 RISC-loading complex subunit TRBP2 / TRBP2 , first double-stranded RNA binding domain / TRBP2 , second double-stranded RNA binding domain / TRBP2 , third double-stranded RNA binding domain / : / Double Stranded RNA Binding Domain - #20 / Double-stranded RNA binding motif / Double-stranded RNA binding motif / Double stranded RNA-binding domain (dsRBD) profile. / Double-stranded RNA-binding domain ...RISC-loading complex subunit TRBP2 / TRBP2 , first double-stranded RNA binding domain / TRBP2 , second double-stranded RNA binding domain / TRBP2 , third double-stranded RNA binding domain / : / Double Stranded RNA Binding Domain - #20 / Double-stranded RNA binding motif / Double-stranded RNA binding motif / Double stranded RNA-binding domain (dsRBD) profile. / Double-stranded RNA-binding domain / Double Stranded RNA Binding Domain / 2-Layer Sandwich / Alpha Beta類似検索 - ドメイン・相同性 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2.2 Å 分子置換 / 解像度: 2.2 Å |
|---|
 データ登録者 データ登録者 | Yuan, Y.A. / Chen, H.Y. |
|---|
 引用 引用 |  ジャーナル: Structure / 年: 2010 ジャーナル: Structure / 年: 2010
タイトル: Structure of arabidopsis HYPONASTIC LEAVES1 and its molecular implications for miRNA processing
著者: Yang, S.W. / Chen, H.Y. / Yang, J. / Machida, S. / Chua, N.H. / Yuan, Y.A. |
|---|
| 履歴 | | 登録 | 2010年1月22日 | 登録サイト: PDBJ / 処理サイト: PDBJ |
|---|
| 改定 1.0 | 2010年5月26日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2011年7月13日 | Group: Advisory / Version format compliance |
|---|
| 改定 1.2 | 2023年11月1日 | Group: Data collection / Database references / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model / struct_ref_seq_dif
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession / _struct_ref_seq_dif.details |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 2.2 Å
分子置換 / 解像度: 2.2 Å  データ登録者
データ登録者 引用
引用 ジャーナル: Structure / 年: 2010
ジャーナル: Structure / 年: 2010 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 3adl.cif.gz
3adl.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb3adl.ent.gz
pdb3adl.ent.gz PDB形式
PDB形式 3adl.json.gz
3adl.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 3adl_validation.pdf.gz
3adl_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 3adl_full_validation.pdf.gz
3adl_full_validation.pdf.gz 3adl_validation.xml.gz
3adl_validation.xml.gz 3adl_validation.cif.gz
3adl_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/ad/3adl
https://data.pdbj.org/pub/pdb/validation_reports/ad/3adl ftp://data.pdbj.org/pub/pdb/validation_reports/ad/3adl
ftp://data.pdbj.org/pub/pdb/validation_reports/ad/3adl リンク
リンク 集合体
集合体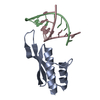
 要素
要素 Homo sapiens (ヒト) / 遺伝子: TARBP2, TRBP / プラスミド: pET28b / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: TARBP2, TRBP / プラスミド: pET28b / 発現宿主: 
 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  NSLS
NSLS  / ビームライン: X12C
/ ビームライン: X12C 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー















 PDBj
PDBj



