| 登録情報 | データベース: PDB / ID: 2mvv
|
|---|
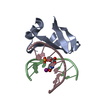
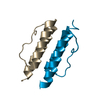
| タイトル | Solution Structure of the 5-phenyl-3-oxo-pentyl Actinorhodin Acyl Carrier Protein from Streptomyces coelicolor |
|---|
 要素 要素 | Actinorhodin polyketide synthase acyl carrier protein |
|---|
 キーワード キーワード | BIOSYNTHETIC PROTEIN / Actinorhodin / ACP / polyketide mimic / ligand recognition |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
lipid A biosynthetic process / acyl binding / acyl carrier activity / antibiotic biosynthetic process / membrane / cytosol類似検索 - 分子機能 ACP-like / Non-ribosomal Peptide Synthetase Peptidyl Carrier Protein; Chain A / Phosphopantetheine attachment site / Phosphopantetheine attachment site. / Phosphopantetheine attachment site / ACP-like superfamily / Carrier protein (CP) domain profile. / Phosphopantetheine binding ACP domain / Orthogonal Bundle / Mainly Alpha類似検索 - ドメイン・相同性 Chem-SXR / Actinorhodin polyketide synthase acyl carrier protein類似検索 - 構成要素 |
|---|
| 生物種 |  Streptomyces coelicolor (バクテリア) Streptomyces coelicolor (バクテリア) |
|---|
| 手法 | 溶液NMR / simulated annealing |
|---|
 データ登録者 データ登録者 | Dong, X. / Bailey, C. / Williams, C. / Crosby, J. / Simpson, T.J. / Willis, C.L. / Crump, M.P. |
|---|
 引用 引用 |  ジャーナル: To be Published ジャーナル: To be Published
タイトル: ACP-ligand recognition: Selection of derivatized aromatic biosynthetic intermediates
著者: Dong, X. / Bailey, C. / Williams, C. / Crosby, J. / Simpson, T.J. / Willis, C.L. / Crump, M.P. |
|---|
| 履歴 | | 登録 | 2014年10月15日 | 登録サイト: BMRB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2015年10月21日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2024年10月9日 | Group: Data collection / Database references ...Data collection / Database references / Derived calculations / Structure summary
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_entry_details / pdbx_modification_feature / struct_conn / struct_ref_seq_dif / struct_site
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _struct_conn.pdbx_leaving_atom_flag / _struct_ref_seq_dif.details / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Streptomyces coelicolor (バクテリア)
Streptomyces coelicolor (バクテリア) データ登録者
データ登録者 引用
引用 ジャーナル: To be Published
ジャーナル: To be Published 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 2mvv.cif.gz
2mvv.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb2mvv.ent.gz
pdb2mvv.ent.gz PDB形式
PDB形式 2mvv.json.gz
2mvv.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 2mvv_validation.pdf.gz
2mvv_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 2mvv_full_validation.pdf.gz
2mvv_full_validation.pdf.gz 2mvv_validation.xml.gz
2mvv_validation.xml.gz 2mvv_validation.cif.gz
2mvv_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/mv/2mvv
https://data.pdbj.org/pub/pdb/validation_reports/mv/2mvv ftp://data.pdbj.org/pub/pdb/validation_reports/mv/2mvv
ftp://data.pdbj.org/pub/pdb/validation_reports/mv/2mvv リンク
リンク 集合体
集合体
 要素
要素 Streptomyces coelicolor (バクテリア)
Streptomyces coelicolor (バクテリア)
 試料調製
試料調製 解析
解析 ムービー
ムービー コントローラー
コントローラー












 PDBj
PDBj

 HSQC
HSQC